| 登録情報 | データベース: PDB / ID: 8vha
|
|---|
| タイトル | Crystal Structure of Human IDH1 R132Q in complex with NADPH and Alpha-Ketoglutarate |
|---|
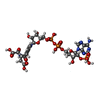
 要素 要素 | Isocitrate dehydrogenase [NADP] cytoplasmic |
|---|
 キーワード キーワード | OXIDOREDUCTASE |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
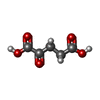
Abnormal conversion of 2-oxoglutarate to 2-hydroxyglutarate / NADPH regeneration / regulation of phospholipid catabolic process / regulation of phospholipid biosynthetic process / NFE2L2 regulating TCA cycle genes / isocitrate metabolic process / NADPH regeneration / isocitrate dehydrogenase (NADP+) / isocitrate dehydrogenase (NADP+) activity / NADP+ metabolic process ...Abnormal conversion of 2-oxoglutarate to 2-hydroxyglutarate / NADPH regeneration / regulation of phospholipid catabolic process / regulation of phospholipid biosynthetic process / NFE2L2 regulating TCA cycle genes / isocitrate metabolic process / NADPH regeneration / isocitrate dehydrogenase (NADP+) / isocitrate dehydrogenase (NADP+) activity / NADP+ metabolic process / 2-oxoglutarate metabolic process / glyoxylate cycle / response to steroid hormone / female gonad development / peroxisomal matrix / tricarboxylic acid cycle / glutathione metabolic process / Peroxisomal protein import / NAD binding / NADP binding / tertiary granule lumen / peroxisome / response to oxidative stress / secretory granule lumen / ficolin-1-rich granule lumen / cadherin binding / Neutrophil degranulation / magnesium ion binding / protein homodimerization activity / mitochondrion / extracellular exosome / extracellular region / identical protein binding / cytoplasm / cytosol類似検索 - 分子機能 Isocitrate dehydrogenase NADP-dependent / Isocitrate/isopropylmalate dehydrogenase, conserved site / Isocitrate and isopropylmalate dehydrogenases signature. / Isopropylmalate dehydrogenase-like domain / Isocitrate/isopropylmalate dehydrogenase / Isocitrate/isopropylmalate dehydrogenase類似検索 - ドメイン・相同性 2-OXOGLUTARIC ACID / Chem-EE1 / Chem-NDP / NITRATE ION / Isocitrate dehydrogenase [NADP] cytoplasmic類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.28 Å 分子置換 / 解像度: 2.28 Å |
|---|
 データ登録者 データ登録者 | Mealka, M. / Sohl, C.D. / Huxford, T. |
|---|
| 資金援助 |  米国, 2件 米国, 2件 | 組織 | 認可番号 | 国 |
|---|
| American Cancer Society | RSG-19-075-01-TBE |  米国 米国 | | National Institutes of Health/National Cancer Institute (NIH/NCI) | R35 GM137773 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: Nat Commun / 年: 2024 ジャーナル: Nat Commun / 年: 2024
タイトル: Active site remodeling in tumor-relevant IDH1 mutants drives distinct kinetic features and potential resistance mechanisms.
著者: Mealka, M. / Sierra, N.A. / Avellaneda Matteo, D. / Albekioni, E. / Khoury, R. / Mai, T. / Conley, B.M. / Coleman, N.J. / Sabo, K.A. / Komives, E.A. / Bobkov, A.A. / Cooksy, A.L. / Silletti, ...著者: Mealka, M. / Sierra, N.A. / Avellaneda Matteo, D. / Albekioni, E. / Khoury, R. / Mai, T. / Conley, B.M. / Coleman, N.J. / Sabo, K.A. / Komives, E.A. / Bobkov, A.A. / Cooksy, A.L. / Silletti, S. / Schiffer, J.M. / Huxford, T. / Sohl, C.D. |
|---|
| 履歴 | | 登録 | 2023年12月31日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2024年4月24日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2024年5月22日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.28 Å
分子置換 / 解像度: 2.28 Å  データ登録者
データ登録者 米国, 2件
米国, 2件  引用
引用 ジャーナル: Nat Commun / 年: 2024
ジャーナル: Nat Commun / 年: 2024 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 8vha.cif.gz
8vha.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb8vha.ent.gz
pdb8vha.ent.gz PDB形式
PDB形式 8vha.json.gz
8vha.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/vh/8vha
https://data.pdbj.org/pub/pdb/validation_reports/vh/8vha ftp://data.pdbj.org/pub/pdb/validation_reports/vh/8vha
ftp://data.pdbj.org/pub/pdb/validation_reports/vh/8vha リンク
リンク 集合体
集合体


 要素
要素 Homo sapiens (ヒト) / 遺伝子: IDH1, PICD / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: IDH1, PICD / 発現宿主: 











 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SSRL
SSRL  / ビームライン: BL12-1 / 波長: 0.97946 Å
/ ビームライン: BL12-1 / 波長: 0.97946 Å 解析
解析 分子置換 / 解像度: 2.28→39.15 Å / SU ML: 0.27 / 交差検証法: FREE R-VALUE / σ(F): 1.34 / 位相誤差: 24.06 / 立体化学のターゲット値: ML
分子置換 / 解像度: 2.28→39.15 Å / SU ML: 0.27 / 交差検証法: FREE R-VALUE / σ(F): 1.34 / 位相誤差: 24.06 / 立体化学のターゲット値: ML ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj










