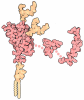
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 7rvg | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| Title | Segment from rabbit/pig prion protein 168-176 QYSNQNSFV | |||||||||
 Components Components | Major prion protein | |||||||||
 Keywords Keywords | PROTEIN FIBRIL / amyloid / prion / fibril / rabbit / pig | |||||||||
| Function / homology |  Function and homology information Function and homology informationaspartic-type endopeptidase inhibitor activity / regulation of calcium ion import across plasma membrane / glycosaminoglycan binding / positive regulation of glutamate receptor signaling pathway / negative regulation of interleukin-17 production / cupric ion binding / regulation of potassium ion transmembrane transport / type 5 metabotropic glutamate receptor binding / negative regulation of dendritic spine maintenance / negative regulation of calcineurin-NFAT signaling cascade ...aspartic-type endopeptidase inhibitor activity / regulation of calcium ion import across plasma membrane / glycosaminoglycan binding / positive regulation of glutamate receptor signaling pathway / negative regulation of interleukin-17 production / cupric ion binding / regulation of potassium ion transmembrane transport / type 5 metabotropic glutamate receptor binding / negative regulation of dendritic spine maintenance / negative regulation of calcineurin-NFAT signaling cascade / negative regulation of interleukin-2 production / negative regulation of activated T cell proliferation / negative regulation of amyloid-beta formation / negative regulation of type II interferon production / cuprous ion binding / positive regulation of protein targeting to membrane / negative regulation of T cell receptor signaling pathway / side of membrane / neuron projection maintenance / inclusion body / positive regulation of calcium-mediated signaling / molecular function activator activity / cellular response to copper ion / positive regulation of protein localization to plasma membrane / molecular condensate scaffold activity / protein homooligomerization / protein destabilization / cellular response to xenobiotic stimulus / cellular response to amyloid-beta / terminal bouton / positive regulation of neuron apoptotic process / amyloid-beta binding / signaling receptor activity / protease binding / response to oxidative stress / nuclear membrane / microtubule binding / learning or memory / intracellular signal transduction / membrane raft / copper ion binding / dendrite / negative regulation of apoptotic process / protein-containing complex binding / cell surface / negative regulation of transcription by RNA polymerase II / endoplasmic reticulum / Golgi apparatus / identical protein binding / plasma membrane / cytosol Similarity search - Function | |||||||||
| Biological species |  | |||||||||
| Method | ELECTRON CRYSTALLOGRAPHY / electron crystallography / AB INITIO PHASING / Resolution: 1 Å | |||||||||
 Authors Authors | Glynn, C. / Rodriguez, J.A. / Hernandez, E. | |||||||||
| Funding support |  United States, 2items United States, 2items
| |||||||||
 Citation Citation |  Journal: To be published Journal: To be publishedTitle: Structural and Biophysical Consequences of Sequence Variation in the B2a2 Loop of Mammalian Prions Authors: Glynn, C. / Hernandez, E. / Gallagher-Jones, M. / Miao, J. / Rodriguez, J.A. | |||||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  7rvg.cif.gz 7rvg.cif.gz | 15.9 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb7rvg.ent.gz pdb7rvg.ent.gz | 7.6 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  7rvg.json.gz 7rvg.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/rv/7rvg https://data.pdbj.org/pub/pdb/validation_reports/rv/7rvg ftp://data.pdbj.org/pub/pdb/validation_reports/rv/7rvg ftp://data.pdbj.org/pub/pdb/validation_reports/rv/7rvg | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  7rvcC  7rvdC  7rveC  7rvfC  7rvhC  7rviC  7rvjC  7rvkC  7rvlC C: citing same article ( |
|---|---|
| Similar structure data | Similarity search - Function & homology  F&H Search F&H Search |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
| #1: Protein/peptide | Mass: 1086.112 Da / Num. of mol.: 1 / Fragment: UNP residues 167-175 / Source method: obtained synthetically / Details: also Sus scrofa / Source: (synth.)  |
|---|---|
| #2: Water | ChemComp-HOH / |
-Experimental details
-Experiment
| Experiment | Method: ELECTRON CRYSTALLOGRAPHY / Number of used crystals: 1 |
|---|---|
| EM experiment | Aggregation state: 3D ARRAY / 3D reconstruction method: electron crystallography |
- Sample preparation
Sample preparation
| Component | Name: Major prion protein / Type: COMPLEX / Entity ID: #1 / Source: NATURAL |
|---|---|
| Source (natural) | Organism:  |
| Specimen | Embedding applied: NO / Shadowing applied: NO / Staining applied: NO / Vitrification applied: NO |
| Crystal grow | Temperature: 298 K / Method: vapor diffusion, hanging drop / pH: 9 Details: 0.05 M CHES, pH 9, 0.2 M lithium sulfate, 1.3 M sodium/potassium tartrate |
-Data collection
| Experimental equipment |  Model: Tecnai F30 / Image courtesy: FEI Company | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Microscopy | Model: FEI TECNAI F30 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Electron gun | Electron source:  FIELD EMISSION GUN / Accelerating voltage: 300 kV / Illumination mode: FLOOD BEAM FIELD EMISSION GUN / Accelerating voltage: 300 kV / Illumination mode: FLOOD BEAM | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Electron lens | Mode: DIFFRACTION | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Specimen holder | Cryogen: NITROGEN | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Image recording | Film or detector model: TVIPS TEMCAM-F416 (4k x 4k) / Num. of grids imaged: 1 / Num. of real images: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| EM diffraction | Camera length: 1 mm | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Diffraction | Mean temperature: 100 K / Serial crystal experiment: N | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Diffraction source | Source: ELECTRON MICROSCOPE / Type: OTHER / Wavelength: 0.0251 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: TVIPS TEMCAM-F416 / Detector: CMOS / Date: Mar 22, 2017 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: electron | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 0.0251 Å / Relative weight: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1→7.18 Å / Num. obs: 2680 / % possible obs: 74.9 % / Redundancy: 7.375 % / Biso Wilson estimate: 4.19 Å2 / CC1/2: 0.994 / Rmerge(I) obs: 0.204 / Rrim(I) all: 0.22 / Χ2: 0.947 / Net I/σ(I): 5.72 / Num. measured all: 19765 / Scaling rejects: 11 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1
|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EM 3D crystal entity | ∠α: 90 ° / ∠β: 111.21 ° / ∠γ: 90 ° / A: 23.57 Å / B: 4.86 Å / C: 27.7 Å / Space group name: P1 / Space group num: 1 | ||||||||||||||||||||||||
| 3D reconstruction | Resolution: 1 Å / Resolution method: DIFFRACTION PATTERN/LAYERLINES / Symmetry type: 3D CRYSTAL | ||||||||||||||||||||||||
| Refinement | Method to determine structure: AB INITIO PHASING / Resolution: 1→7.18 Å / SU ML: 0.09 / Cross valid method: THROUGHOUT / σ(F): 1.36 / Phase error: 24.7 / Stereochemistry target values: ML
| ||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å / Solvent model: FLAT BULK SOLVENT MODEL | ||||||||||||||||||||||||
| Displacement parameters | Biso max: 17.36 Å2 / Biso mean: 5.5722 Å2 / Biso min: 2.44 Å2 | ||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 1→7.18 Å
| ||||||||||||||||||||||||
| LS refinement shell | Refine-ID: ELECTRON CRYSTALLOGRAPHY / Rfactor Rfree error: 0 / Total num. of bins used: 2
|
 Movie
Movie Controller
Controller



 PDBj
PDBj