| 1 | 300 uM [U-13C; U-15N] Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 0.5 mM AEBSF protease inhibitor, 0.04 % v/v sodium azide, 50 uM DSS, 95% H2O/5% D2O | 15N-13C_sample1 | 95% H2O/5% D2O | solution| 2 | 360 uM [U-13C; U-15N] Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 0.5 mM AEBSF protease inhibitor, 0.04 % v/v sodium azide, 50 uM DSS, 95% H2O/5% D2O | 15N-13C_sample2 | 95% H2O/5% D2O | solution| 3 | 300 uM [U-13C; U-15N] Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 1 mM AEBSF protease inhibitor, 0.05 % w/v sodium azide, 50 uM DSS, 95% H2O/5% D2O | 15N-13C_sample3 | 95% H2O/5% D2O | solution| 4 | 400 uM [U-13C; U-15N] Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 0.5 mM AEBSF protease inhibitor, 0.05 % w/v sodium azide, 50 mM DSS, 100% D2O | 15N-13C_sample4_d2o | 100% D2O | solution| 7 | 420 uM [U-13C; U-15N] Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 0.5 mM AEBSF protease inhibitor, 0.04 % w/v sodium azide, 50 mM DSS, 95% H2O/5% D2O | 15N-13C_sample7 | 95% H2O/5% D2O | solution| 8 | 380 uM [U-13C; U-15N] Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 0.5 mM AEBSF protease inhibitor, 0.04 % w/v sodium azide, 50 mM DSS, 95% H2O/5% D2O | 15N-13C_sample8 | 95% H2O/5% D2O | solution| 9 | 400 uM [U-13C; U-15N] Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 0.5 mM AEBSF protease inhibitor, 0.04 % w/v sodium azide, 50 mM DSS, 100% D2O | 15N-13C_sample9_d2o | 100% D2O | solution| 5 | 400 uM [U-2H; U-15N];[13CD1,1H3]ILE;[13CD1,1H3;13CD2,1H3]LEU;[13CG1,1H3;13CG2,1H3]VAL;[13CE1,1H3]MET;[13CG2,1H3]THR Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 0.5 mM AEBSF protease inhibitor, 0.05 % w/v sodium azide, 50 uM DSS, 100% D2O | 2H-15N_ILVMT_sample5_d2O | 100% D2O| Uniformly [2H-15N] sample with [13C-1H] labeling on methyl groups for ILE [d1 only] VAL (g1 and g2), Leu (d1 and d2) and THR (g2). | solution| 6 | 350 uM [U-2H; U-15N];[13CD1,1H3]ILE;[13CD1,1H3;13CD2,1H3]LEU;[13CG1,1H3;13CG2,1H3]VAL;[13CE1,1H3]MET;[13CG2,1H3]THR Tpt1, 20 mM HEPES, 200 mM sodium chloride, 2 mM DTT, 2 mM [U-100% 2H] EDTA, 5 % v/v [U-100% 2H] glycerol, 0.5 mM AEBSF protease inhibitor, 0.05 % w/v sodium azide, 50 uM DSS, 100% D2O | 2H-15N_ILVMT_sample6_d2O | 100% D2O| Uniformly [2H-15N] sample with [13C-1H] labeling on methyl groups for ILE [d1 only] VAL (g1 and g2), Leu (d1 and d2) and THR (g2). | | | | | | | | | | | | | | | | | |  データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Runella slithyformis (バクテリア)
Runella slithyformis (バクテリア) データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: Nucleic Acids Res. / 年: 2021
ジャーナル: Nucleic Acids Res. / 年: 2021 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 7kw8.cif.gz
7kw8.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb7kw8.ent.gz
pdb7kw8.ent.gz PDB形式
PDB形式 7kw8.json.gz
7kw8.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 7kw8_validation.pdf.gz
7kw8_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 7kw8_full_validation.pdf.gz
7kw8_full_validation.pdf.gz 7kw8_validation.xml.gz
7kw8_validation.xml.gz 7kw8_validation.cif.gz
7kw8_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/kw/7kw8
https://data.pdbj.org/pub/pdb/validation_reports/kw/7kw8 ftp://data.pdbj.org/pub/pdb/validation_reports/kw/7kw8
ftp://data.pdbj.org/pub/pdb/validation_reports/kw/7kw8
 リンク
リンク 集合体
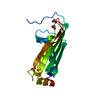
集合体
 要素
要素 Runella slithyformis (バクテリア)
Runella slithyformis (バクテリア)
 試料調製
試料調製 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj HNCA
HNCA