+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6rws | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Fragment AZ-009 binding at the p53pT387/14-3-3 sigma interface | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | PEPTIDE BINDING PROTEIN / protein protein interaction / fragment soaking / stabilization | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of helicase activity / Loss of function of TP53 in cancer due to loss of tetramerization ability / Regulation of TP53 Expression / signal transduction by p53 class mediator / negative regulation of G1 to G0 transition / negative regulation of glucose catabolic process to lactate via pyruvate / Transcriptional activation of cell cycle inhibitor p21 / regulation of intrinsic apoptotic signaling pathway by p53 class mediator / negative regulation of pentose-phosphate shunt / ATP-dependent DNA/DNA annealing activity ...negative regulation of helicase activity / Loss of function of TP53 in cancer due to loss of tetramerization ability / Regulation of TP53 Expression / signal transduction by p53 class mediator / negative regulation of G1 to G0 transition / negative regulation of glucose catabolic process to lactate via pyruvate / Transcriptional activation of cell cycle inhibitor p21 / regulation of intrinsic apoptotic signaling pathway by p53 class mediator / negative regulation of pentose-phosphate shunt / ATP-dependent DNA/DNA annealing activity / Activation of NOXA and translocation to mitochondria / regulation of cell cycle G2/M phase transition / regulation of fibroblast apoptotic process / intrinsic apoptotic signaling pathway in response to hypoxia / oligodendrocyte apoptotic process / negative regulation of miRNA processing / positive regulation of thymocyte apoptotic process / oxidative stress-induced premature senescence / regulation of tissue remodeling / positive regulation of mitochondrial membrane permeability / mRNA transcription / positive regulation of programmed necrotic cell death / bone marrow development / circadian behavior / T cell proliferation involved in immune response / regulation of mitochondrial membrane permeability involved in apoptotic process / germ cell nucleus / RUNX3 regulates CDKN1A transcription / glucose catabolic process to lactate via pyruvate / TP53 Regulates Transcription of Death Receptors and Ligands / TP53 regulates transcription of additional cell cycle genes whose exact role in the p53 pathway remain uncertain / Activation of PUMA and translocation to mitochondria / regulation of DNA damage response, signal transduction by p53 class mediator / histone deacetylase regulator activity / negative regulation of glial cell proliferation / Regulation of TP53 Activity through Association with Co-factors / negative regulation of neuroblast proliferation / mitochondrial DNA repair / T cell lineage commitment / Formation of Senescence-Associated Heterochromatin Foci (SAHF) / ER overload response / thymocyte apoptotic process / B cell lineage commitment / TP53 Regulates Transcription of Caspase Activators and Caspases / negative regulation of mitophagy / regulation of epidermal cell division / protein kinase C inhibitor activity / cardiac septum morphogenesis / negative regulation of DNA replication / entrainment of circadian clock by photoperiod / positive regulation of epidermal cell differentiation / keratinocyte development / keratinization / PI5P Regulates TP53 Acetylation / negative regulation of telomere maintenance via telomerase / Zygotic genome activation (ZGA) / positive regulation of release of cytochrome c from mitochondria / regulation of cell-cell adhesion / Association of TriC/CCT with target proteins during biosynthesis / necroptotic process / TP53 Regulates Transcription of Genes Involved in Cytochrome C Release / SUMOylation of transcription factors / TP53 regulates transcription of several additional cell death genes whose specific roles in p53-dependent apoptosis remain uncertain / TFIID-class transcription factor complex binding / intrinsic apoptotic signaling pathway by p53 class mediator / negative regulation of reactive oxygen species metabolic process / rRNA transcription / Transcriptional Regulation by VENTX / cAMP/PKA signal transduction / Regulation of localization of FOXO transcription factors / replicative senescence / keratinocyte proliferation / general transcription initiation factor binding / cellular response to UV-C / cellular response to actinomycin D / intrinsic apoptotic signaling pathway in response to endoplasmic reticulum stress / phosphoserine residue binding / positive regulation of execution phase of apoptosis / positive regulation of RNA polymerase II transcription preinitiation complex assembly / neuroblast proliferation / intrinsic apoptotic signaling pathway in response to DNA damage by p53 class mediator / response to X-ray / Activation of BAD and translocation to mitochondria / hematopoietic stem cell differentiation / Pyroptosis / viral process / negative regulation of keratinocyte proliferation / embryonic organ development / chromosome organization / establishment of skin barrier / type II interferon-mediated signaling pathway / negative regulation of protein localization to plasma membrane / TP53 Regulates Transcription of Genes Involved in G1 Cell Cycle Arrest / somitogenesis / hematopoietic progenitor cell differentiation / glial cell proliferation / Chk1/Chk2(Cds1) mediated inactivation of Cyclin B:Cdk1 complex / SARS-CoV-2 targets host intracellular signalling and regulatory pathways / negative regulation of fibroblast proliferation / core promoter sequence-specific DNA binding 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 1.53 Å 分子置換 / 解像度: 1.53 Å | ||||||
 データ登録者 データ登録者 | Leysen, S. / Guillory, X. / Wolter, M. / Genet, S. / Somsen, B. / Patel, J. / Castaldi, P. / Ottmann, C. | ||||||
| 資金援助 |  オランダ, 1件 オランダ, 1件
| ||||||
 引用 引用 |  ジャーナル: J.Med.Chem. / 年: 2020 ジャーナル: J.Med.Chem. / 年: 2020タイトル: Fragment-based Differential Targeting of PPI Stabilizer Interfaces. 著者: Guillory, X. / Wolter, M. / Leysen, S. / Neves, J.F. / Kuusk, A. / Genet, S. / Somsen, B. / Morrow, J.K. / Rivers, E. / van Beek, L. / Patel, J. / Goodnow, R. / Schoenherr, H. / Fuller, N. / ...著者: Guillory, X. / Wolter, M. / Leysen, S. / Neves, J.F. / Kuusk, A. / Genet, S. / Somsen, B. / Morrow, J.K. / Rivers, E. / van Beek, L. / Patel, J. / Goodnow, R. / Schoenherr, H. / Fuller, N. / Cao, Q. / Doveston, R.G. / Brunsveld, L. / Arkin, M.R. / Castaldi, P. / Boyd, H. / Landrieu, I. / Chen, H. / Ottmann, C. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6rws.cif.gz 6rws.cif.gz | 75.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6rws.ent.gz pdb6rws.ent.gz | 53.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6rws.json.gz 6rws.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6rws_validation.pdf.gz 6rws_validation.pdf.gz | 1013.4 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6rws_full_validation.pdf.gz 6rws_full_validation.pdf.gz | 1013.7 KB | 表示 | |
| XML形式データ |  6rws_validation.xml.gz 6rws_validation.xml.gz | 14.5 KB | 表示 | |
| CIF形式データ |  6rws_validation.cif.gz 6rws_validation.cif.gz | 22 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/rw/6rws https://data.pdbj.org/pub/pdb/validation_reports/rw/6rws ftp://data.pdbj.org/pub/pdb/validation_reports/rw/6rws ftp://data.pdbj.org/pub/pdb/validation_reports/rw/6rws | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6r5lC  6rhcC  6rjlC  6rjqC  6rjzC  6rk8C  6rkiC  6rkkC  6rkmC  6rl3C  6rl4C  6rl6C  6rm5C  6rm7C  6rp6C  6rwhC  6rwiC  6rwuC  6rx2C  6s39C  6s3cC  6s40C  6s9qC  6sinC  6sioC  6sipC  6siqC  6slvC  6slwC  6slxC  5mocS S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 28210.518 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: SFN, HME1 / 発現宿主: Homo sapiens (ヒト) / 遺伝子: SFN, HME1 / 発現宿主:  |
|---|---|
| #2: タンパク質・ペプチド | 分子量: 1449.520 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成)  Homo sapiens (ヒト) / 参照: UniProt: P04637 Homo sapiens (ヒト) / 参照: UniProt: P04637 |
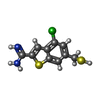
| #3: 化合物 | ChemComp-KLZ / |
| #4: 化合物 | ChemComp-MG / |
| #5: 水 | ChemComp-HOH / |
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.47 Å3/Da / 溶媒含有率: 50.25 % |
|---|---|
| 結晶化 | 温度: 277 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 7.5 詳細: 0.1M Hepes, pH7.5, 27%PEG, 5% Glycerol, 0.2M Calcium Chloride, 2mM DTT. |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  回転陽極 / タイプ: RIGAKU FR-E+ SUPERBRIGHT / 波長: 1.54 Å 回転陽極 / タイプ: RIGAKU FR-E+ SUPERBRIGHT / 波長: 1.54 Å |
| 検出器 | タイプ: RIGAKU SATURN 944+ / 検出器: CCD / 日付: 2016年6月20日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.54 Å / 相対比: 1 |
| 反射 | 解像度: 1.53→66.32 Å / Num. obs: 42938 / % possible obs: 97 % / 冗長度: 6.2 % / Biso Wilson estimate: 15.71 Å2 / CC1/2: 0.997 / Rmerge(I) obs: 0.064 / Rrim(I) all: 0.076 / Net I/σ(I): 17 |
| 反射 シェル | 解像度: 1.53→1.61 Å / 冗長度: 2.7 % / Rmerge(I) obs: 0.391 / Mean I/σ(I) obs: 3.1 / Num. unique obs: 5089 / CC1/2: 0.321 / Rrim(I) all: 0.529 / % possible all: 80.3 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 5MOC 解像度: 1.53→56.11 Å / Cor.coef. Fo:Fc: 0.958 / Cor.coef. Fo:Fc free: 0.933 / Rfactor Rfree error: 0 / SU R Cruickshank DPI: 0.072 / 交差検証法: FREE R-VALUE / σ(F): 0 / SU R Blow DPI: 0.081 / SU Rfree Blow DPI: 0.082 / SU Rfree Cruickshank DPI: 0.075
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 20.41 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze | Luzzati coordinate error obs: 0.18 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.53→56.11 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 1.53→1.57 Å / Rfactor Rfree error: 0 / Total num. of bins used: 20
|
 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj