| 登録情報 | データベース: PDB / ID: 6qh8
|
|---|
| タイトル | Structure of knotted YibK from P. aeruginosa |
|---|
 要素 要素 | tRNA (cytidine(34)-2'-O)-methyltransferase |
|---|
 キーワード キーワード | TRANSFERASE / methyltransferase / topological knot / cyclized protein |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
wobble position cytosine ribose methylation / wobble position uridine ribose methylation / : / tRNA (cytidine(34)-2'-O)-methyltransferase activity / tRNA (5-carboxymethylaminomethyluridine(34)-2'-O)-methyltransferase activity / tRNA (cytidine34-2'-O)-methyltransferase / tRNA methylation / RNA binding / cytoplasm類似検索 - 分子機能 tRNA (cytidine/uridine-2'-O-)-methyltransferase / tRNA/rRNA methyltransferase, SpoU type / SpoU rRNA Methylase family / SPOUT methyltransferase, trefoil knot domain / Alpha/beta knot / tRNA (guanine-N1-)-methyltransferase, N-terminal / Alpha/beta knot methyltransferases / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 DI(HYDROXYETHYL)ETHER / tRNA (cytidine(34)-2'-O)-methyltransferase / tRNA (cytidine(34)-2'-O)-methyltransferase類似検索 - 構成要素 |
|---|
| 生物種 |   Pseudomonas aeruginosa (緑膿菌) Pseudomonas aeruginosa (緑膿菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.2 Å 分子置換 / 解像度: 2.2 Å |
|---|
 データ登録者 データ登録者 | Mikula, K.M. / Tascon, I. / Iwai, H. |
|---|
| 資金援助 |  フィンランド, 2件 フィンランド, 2件 | 組織 | 認可番号 | 国 |
|---|
| Sigrid Juselius Foundation | |  フィンランド フィンランド | | Academy of Finland | 131413, 137995, 277335 |  フィンランド フィンランド |
|
|---|
 引用 引用 |  ジャーナル: Front Chem / 年: 2021 ジャーナル: Front Chem / 年: 2021
タイトル: Tying up the Loose Ends: A Mathematically Knotted Protein.
著者: Hsu, S.D. / Lee, Y.C. / Mikula, K.M. / Backlund, S.M. / Tascon, I. / Goldman, A. / Iwai, H. |
|---|
| 履歴 | | 登録 | 2019年1月16日 | 登録サイト: PDBE / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2020年7月15日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2021年7月28日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year |
|---|
| 改定 1.2 | 2024年1月24日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.2 Å
分子置換 / 解像度: 2.2 Å  データ登録者
データ登録者 フィンランド, 2件
フィンランド, 2件  引用
引用 ジャーナル: Front Chem / 年: 2021
ジャーナル: Front Chem / 年: 2021 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6qh8.cif.gz
6qh8.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6qh8.ent.gz
pdb6qh8.ent.gz PDB形式
PDB形式 6qh8.json.gz
6qh8.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 6qh8_validation.pdf.gz
6qh8_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 6qh8_full_validation.pdf.gz
6qh8_full_validation.pdf.gz 6qh8_validation.xml.gz
6qh8_validation.xml.gz 6qh8_validation.cif.gz
6qh8_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/qh/6qh8
https://data.pdbj.org/pub/pdb/validation_reports/qh/6qh8 ftp://data.pdbj.org/pub/pdb/validation_reports/qh/6qh8
ftp://data.pdbj.org/pub/pdb/validation_reports/qh/6qh8 リンク
リンク 集合体
集合体
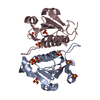

 要素
要素

 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  Diamond
Diamond  / ビームライン: I03 / 波長: 0.9763 Å
/ ビームライン: I03 / 波長: 0.9763 Å 分子置換
分子置換 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj




