+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6nh3 | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | Structure of human endothelial nitric oxide synthase heme domain in complex with (S)-6-(3-fluoro-5-(2-(pyrrolidin-2-yl)ethyl)phenethyl)-4-methylpyridin-2-amine | ||||||
 要素 要素 | Endothelial nitric oxide synthase splice variant eNOS13A | ||||||
 キーワード キーワード | OXIDOREDUCTASE/OXIDOREDUCTASE inhibitor / nitric oxide synthase inhibitor complex heme enzyme / OXIDOREDUCTASE / OXIDOREDUCTASE-OXIDOREDUCTASE inhibitor complex | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報negative regulation of muscle hyperplasia / regulation of the force of heart contraction by chemical signal / NOSIP mediated eNOS trafficking / tetrahydrobiopterin metabolic process / NOSTRIN mediated eNOS trafficking / smooth muscle hyperplasia / regulation of nervous system process / superoxide-generating NAD(P)H oxidase activity / : / ovulation from ovarian follicle ...negative regulation of muscle hyperplasia / regulation of the force of heart contraction by chemical signal / NOSIP mediated eNOS trafficking / tetrahydrobiopterin metabolic process / NOSTRIN mediated eNOS trafficking / smooth muscle hyperplasia / regulation of nervous system process / superoxide-generating NAD(P)H oxidase activity / : / ovulation from ovarian follicle / pulmonary valve morphogenesis / response to fluid shear stress / positive regulation of guanylate cyclase activity / negative regulation of biomineral tissue development / Nitric oxide stimulates guanylate cyclase / regulation of systemic arterial blood pressure by endothelin / ROS and RNS production in phagocytes / tetrahydrobiopterin binding / arginine binding / aortic valve morphogenesis / endocardial cushion morphogenesis / ventricular septum morphogenesis / positive regulation of Notch signaling pathway / cadmium ion binding / negative regulation of potassium ion transport / negative regulation of calcium ion transport / nitric oxide mediated signal transduction / negative regulation of platelet activation / actin monomer binding / blood vessel remodeling / nitric-oxide synthase (NADPH) / positive regulation of blood vessel endothelial cell migration / nitric-oxide synthase activity / endothelial cell migration / L-arginine catabolic process / negative regulation of extrinsic apoptotic signaling pathway via death domain receptors / regulation of sodium ion transport / eNOS activation / nitric oxide metabolic process / Tetrahydrobiopterin (BH4) synthesis, recycling, salvage and regulation / negative regulation of blood pressure / homeostasis of number of cells within a tissue / response to hormone / nitric oxide biosynthetic process / removal of superoxide radicals / cell redox homeostasis / lipopolysaccharide-mediated signaling pathway / blood vessel diameter maintenance / VEGFR2 mediated vascular permeability / mitochondrion organization / establishment of localization in cell / negative regulation of smooth muscle cell proliferation / lung development / potassium ion transport / caveola / regulation of blood pressure / positive regulation of angiogenesis / calcium ion transport / vasodilation / endocytic vesicle membrane / FMN binding / flavin adenine dinucleotide binding / NADP binding / response to heat / High laminar flow shear stress activates signaling by PIEZO1 and PECAM1:CDH5:KDR in endothelial cells / scaffold protein binding / angiogenesis / response to lipopolysaccharide / in utero embryonic development / cytoskeleton / Extra-nuclear estrogen signaling / calmodulin binding / Golgi membrane / negative regulation of cell population proliferation / heme binding / positive regulation of gene expression / Golgi apparatus / metal ion binding / nucleus / plasma membrane / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  フーリエ合成 / 解像度: 2.01 Å フーリエ合成 / 解像度: 2.01 Å | ||||||
 データ登録者 データ登録者 | Chreifi, G. / Li, H. / Poulos, T.L. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: J. Med. Chem. / 年: 2019 ジャーナル: J. Med. Chem. / 年: 2019タイトル: Optimization of Blood-Brain Barrier Permeability with Potent and Selective Human Neuronal Nitric Oxide Synthase Inhibitors Having a 2-Aminopyridine Scaffold. 著者: Do, H.T. / Li, H. / Chreifi, G. / Poulos, T.L. / Silverman, R.B. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6nh3.cif.gz 6nh3.cif.gz | 707 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6nh3.ent.gz pdb6nh3.ent.gz | 585.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6nh3.json.gz 6nh3.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6nh3_validation.pdf.gz 6nh3_validation.pdf.gz | 3.5 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6nh3_full_validation.pdf.gz 6nh3_full_validation.pdf.gz | 3.5 MB | 表示 | |
| XML形式データ |  6nh3_validation.xml.gz 6nh3_validation.xml.gz | 70.2 KB | 表示 | |
| CIF形式データ |  6nh3_validation.cif.gz 6nh3_validation.cif.gz | 94.5 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/nh/6nh3 https://data.pdbj.org/pub/pdb/validation_reports/nh/6nh3 ftp://data.pdbj.org/pub/pdb/validation_reports/nh/6nh3 ftp://data.pdbj.org/pub/pdb/validation_reports/nh/6nh3 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6ng1C  6ng2C  6ng4C  6ng5C  6ng6C  6ng7C  6ng8C  6ngaC  6ngbC  6ngcC  6ngdC  6ngeC  6ngfC  6nghC  6ngiC  6ngjC  6ngkC  6nglC  6ngmC  6ngnC  6ngpC  6ngqC  6ngrC  6ngsC  6ngtC  6nguC  6ngvC  6ngwC  6ngxC  6ngyC  6ngzC  6nh0C  6nh1C  6nh2C  6nh4C  6nh5C  6nh6C  6nh7C  6nh8C  6nhbC  6nhcC  6nhdC  6nheC  6nhfC  4dipS S: 精密化の開始モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| 2 | 
| ||||||||
| 単位格子 |
|
- 要素
要素
-タンパク質 , 1種, 4分子 ABCD
| #1: タンパク質 | 分子量: 49345.770 Da / 分子数: 4 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 細胞株: endothelial / プラスミド: pCWori / 発現宿主: Homo sapiens (ヒト) / 細胞株: endothelial / プラスミド: pCWori / 発現宿主:  |
|---|
-非ポリマー , 8種, 624分子 
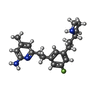













| #2: 化合物 | ChemComp-HEM / #3: 化合物 | ChemComp-KL4 / #4: 化合物 | ChemComp-BTB / #5: 化合物 | ChemComp-ZN / #6: 化合物 | #7: 化合物 | ChemComp-CL / #8: 化合物 | ChemComp-GD / #9: 水 | ChemComp-HOH / | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.69 Å3/Da / 溶媒含有率: 54.3 % / 解説: rods |
|---|---|
| 結晶化 | 温度: 277 K / 手法: 蒸気拡散法, シッティングドロップ法 / pH: 7.5 詳細: 12-15% PEG3350, 0.1M BIS-TRIS 0.2-0.3M MG ACETATE, 0.1M GdCl3 10% glycerol, 5 mM TCEP |
-データ収集
| 回折 | 平均測定温度: 100 K / Serial crystal experiment: N |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  ALS ALS  / ビームライン: 5.0.2 / 波長: 1 Å / ビームライン: 5.0.2 / 波長: 1 Å |
| 検出器 | タイプ: DECTRIS PILATUS 300K / 検出器: PIXEL / 日付: 2017年5月28日 / 詳細: mirrors |
| 放射 | モノクロメーター: graphite / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1 Å / 相対比: 1 |
| 反射 | 解像度: 2.01→90 Å / Num. obs: 129352 / % possible obs: 99.9 % / Observed criterion σ(I): -3 / 冗長度: 5.6 % / CC1/2: 0.994 / Rmerge(I) obs: 0.175 / Rpim(I) all: 0.122 / Rsym value: 0.175 / Net I/σ(I): 6.2 |
| 反射 シェル | 解像度: 2.01→2.06 Å / 冗長度: 5.7 % / Rmerge(I) obs: 3.021 / Mean I/σ(I) obs: 0.8 / Num. unique obs: 6454 / CC1/2: 0.333 / Rpim(I) all: 2.052 / Rsym value: 3.021 / % possible all: 99.9 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  フーリエ合成 フーリエ合成開始モデル: 4DIP 解像度: 2.01→88.868 Å / SU ML: 0.3 / 交差検証法: FREE R-VALUE / σ(F): 0 / 位相誤差: 31
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 減衰半径: 0.9 Å / VDWプローブ半径: 1.11 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.01→88.868 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLS | 手法: refined / Origin x: 83.9069 Å / Origin y: -2.0249 Å / Origin z: -191.0088 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 TLSグループ | Selection details: all |
 ムービー
ムービー コントローラー
コントローラー























 PDBj
PDBj















