| 登録情報 | データベース: PDB / ID: 6mgn
|
|---|
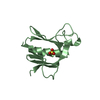
| タイトル | mouse Id1 (51-104) - human hE47 (348-399) complex |
|---|
 要素 要素 | - DNA-binding protein inhibitor ID-1
- Transcription factor E2-alpha
|
|---|
 キーワード キーワード | DNA BINDING PROTEIN / DNA-binding protein inhibitor ID-1 / transcription factor E2-alpha isoform E47 [Homo sapiens] |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
vitamin D response element binding / Oncogene Induced Senescence / bHLH transcription factor binding / lung vasculature development / collagen metabolic process / immunoglobulin V(D)J recombination / endothelial cell morphogenesis / endothelial cell apoptotic process / TGFBR3 expression / mitogen-activated protein kinase kinase kinase binding ...vitamin D response element binding / Oncogene Induced Senescence / bHLH transcription factor binding / lung vasculature development / collagen metabolic process / immunoglobulin V(D)J recombination / endothelial cell morphogenesis / endothelial cell apoptotic process / TGFBR3 expression / mitogen-activated protein kinase kinase kinase binding / negative regulation of cold-induced thermogenesis / Myogenesis / B cell lineage commitment / E-box binding / lung morphogenesis / regulation of G1/S transition of mitotic cell cycle / regulation of MAPK cascade / negative regulation of osteoblast differentiation / regulation of angiogenesis / BMP signaling pathway / negative regulation of endothelial cell apoptotic process / positive regulation of DNA-binding transcription factor activity / transcription regulator inhibitor activity / cis-regulatory region sequence-specific DNA binding / positive regulation of cell cycle / positive regulation of B cell proliferation / positive regulation of neuron differentiation / B cell differentiation / euchromatin / protein destabilization / circadian rhythm / DNA-binding transcription repressor activity, RNA polymerase II-specific / RNA polymerase II transcription regulator complex / nervous system development / RUNX1 regulates transcription of genes involved in differentiation of HSCs / heart development / DNA-binding transcription activator activity, RNA polymerase II-specific / transcription regulator complex / DNA-binding transcription factor binding / RNA polymerase II-specific DNA-binding transcription factor binding / DNA-binding transcription factor activity, RNA polymerase II-specific / protein dimerization activity / RNA polymerase II cis-regulatory region sequence-specific DNA binding / DNA-binding transcription factor activity / protein heterodimerization activity / negative regulation of gene expression / response to antibiotic / negative regulation of DNA-templated transcription / apoptotic process / positive regulation of gene expression / regulation of transcription by RNA polymerase II / regulation of DNA-templated transcription / chromatin / positive regulation of DNA-templated transcription / negative regulation of transcription by RNA polymerase II / protein homodimerization activity / positive regulation of transcription by RNA polymerase II / protein-containing complex / DNA binding / nucleoplasm / nucleus / cytoplasm類似検索 - 分子機能 DNA-binding protein inhibitor / : / Helix-loop-helix DNA-binding domain / MYOD Basic-Helix-Loop-Helix Domain, subunit B / Helix-loop-helix DNA-binding domain / helix loop helix domain / Myc-type, basic helix-loop-helix (bHLH) domain / Myc-type, basic helix-loop-helix (bHLH) domain profile. / Helix-loop-helix DNA-binding domain superfamily / Few Secondary Structures / Irregular類似検索 - ドメイン・相同性 Transcription factor E2-alpha / DNA-binding protein inhibitor ID-1類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト)
  Mus musculus (ハツカネズミ) Mus musculus (ハツカネズミ) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.901 Å 分子置換 / 解像度: 1.901 Å |
|---|
 データ登録者 データ登録者 | Benezra, R. / Pavletich, N.P. / Gall, A.-L. / Goldgur, Y. |
|---|
| 資金援助 |  米国, 1件 米国, 1件 | 組織 | 認可番号 | 国 |
|---|
| National Institutes of Health/National Cancer Institute (NIH/NCI) | PO1 CA094060 |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: Cell Rep / 年: 2019 ジャーナル: Cell Rep / 年: 2019
タイトル: A Small-Molecule Pan-Id Antagonist Inhibits Pathologic Ocular Neovascularization.
著者: Wojnarowicz, P.M. / Lima E Silva, R. / Ohnaka, M. / Lee, S.B. / Chin, Y. / Kulukian, A. / Chang, S.H. / Desai, B. / Garcia Escolano, M. / Shah, R. / Garcia-Cao, M. / Xu, S. / Kadam, R. / ...著者: Wojnarowicz, P.M. / Lima E Silva, R. / Ohnaka, M. / Lee, S.B. / Chin, Y. / Kulukian, A. / Chang, S.H. / Desai, B. / Garcia Escolano, M. / Shah, R. / Garcia-Cao, M. / Xu, S. / Kadam, R. / Goldgur, Y. / Miller, M.A. / Ouerfelli, O. / Yang, G. / Arakawa, T. / Albanese, S.K. / Garland, W.A. / Stoller, G. / Chaudhary, J. / Norton, L. / Soni, R.K. / Philip, J. / Hendrickson, R.C. / Iavarone, A. / Dannenberg, A.J. / Chodera, J.D. / Pavletich, N. / Lasorella, A. / Campochiaro, P.A. / Benezra, R. |
|---|
| 履歴 | | 登録 | 2018年9月14日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2019年9月18日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2019年10月16日 | Group: Data collection / Database references / カテゴリ: citation / citation_author
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_DOI / _citation.pdbx_database_id_PubMed / _citation.title / _citation.year |
|---|
| 改定 1.2 | 2019年12月4日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.3 | 2023年10月11日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.901 Å
分子置換 / 解像度: 1.901 Å  データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: Cell Rep / 年: 2019
ジャーナル: Cell Rep / 年: 2019 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 6mgn.cif.gz
6mgn.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb6mgn.ent.gz
pdb6mgn.ent.gz PDB形式
PDB形式 6mgn.json.gz
6mgn.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 6mgn_validation.pdf.gz
6mgn_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 6mgn_full_validation.pdf.gz
6mgn_full_validation.pdf.gz 6mgn_validation.xml.gz
6mgn_validation.xml.gz 6mgn_validation.cif.gz
6mgn_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/mg/6mgn
https://data.pdbj.org/pub/pdb/validation_reports/mg/6mgn ftp://data.pdbj.org/pub/pdb/validation_reports/mg/6mgn
ftp://data.pdbj.org/pub/pdb/validation_reports/mg/6mgn リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: TCF3, BHLHB21, E2A, ITF1 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: TCF3, BHLHB21, E2A, ITF1 / 発現宿主: 


 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  NSLS
NSLS  / ビームライン: X9A / 波長: 0.92 Å
/ ビームライン: X9A / 波長: 0.92 Å 解析
解析 分子置換
分子置換
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj





