+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 6gz7 | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Polyamide - DNA complex NMR structure | ||||||||||||||||||||
 要素 要素 | DNA (5'-D(* キーワード キーワードUNKNOWN FUNCTION / Polyamide DNA complex | 機能・相同性 | Chem-FGW / DNA / DNA (> 10) |  機能・相同性情報 機能・相同性情報生物種 | synthetic construct (人工物) | 手法 | 溶液NMR / molecular dynamics |  データ登録者 データ登録者Aman, K. |  引用 引用 ジャーナル: Chemistry / 年: 2019 ジャーナル: Chemistry / 年: 2019タイトル: Structural and Kinetic Profiling of Allosteric Modulation of Duplex DNA Induced by DNA-Binding Polyamide Analogues. 著者: Aman, K. / Padroni, G. / Parkinson, J.A. / Welte, T. / Burley, G.A. 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6gz7.cif.gz 6gz7.cif.gz | 209.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6gz7.ent.gz pdb6gz7.ent.gz | 168.8 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6gz7.json.gz 6gz7.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/gz/6gz7 https://data.pdbj.org/pub/pdb/validation_reports/gz/6gz7 ftp://data.pdbj.org/pub/pdb/validation_reports/gz/6gz7 ftp://data.pdbj.org/pub/pdb/validation_reports/gz/6gz7 | HTTPS FTP |
|---|
-関連構造データ
| 類似構造データ | |
|---|---|
| その他のデータベース |
|
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 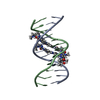
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: DNA鎖 | 分子量: 3940.603 Da / 分子数: 2 / 由来タイプ: 合成 / 由来: (合成) synthetic construct (人工物) #2: 化合物 | ChemComp-FGW / | |
|---|
-実験情報
-実験
| 実験 | 手法: 溶液NMR | ||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 詳細 |
| ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 試料 |
| ||||||||||||||||||||
| 試料状態 | Ionic strength units: Not defined / Label: PA-ODN1 complex conditions / pH: 7.4 / 圧: 1 atm / 温度: 298 K |
-NMR測定
| NMRスペクトロメーター | タイプ: Bruker AVANCE II / 製造業者: Bruker / モデル: AVANCE II / 磁場強度: 600 MHz |
|---|
- 解析
解析
| NMR software |
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: molecular dynamics / ソフトェア番号: 2 詳細: the structures are based on a total of 310 NOE distance restraints | |||||||||||||||
| 代表構造 | 選択基準: minimized average structure | |||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: all calculated structures submitted 計算したコンフォーマーの数: 11 / 登録したコンフォーマーの数: 11 |
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj








































 HSQC
HSQC