+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 6e3z | ||||||
|---|---|---|---|---|---|---|---|
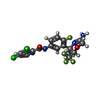
| Title | Structure of Bace-1 in complex with Ligand 8 | ||||||
 Components Components | Beta-secretase 1 | ||||||
 Keywords Keywords | HYDROLASE/INHIBITOR / bace protease / hydrolase / HYDROLASE-INHIBITOR complex | ||||||
| Function / homology |  Function and homology information Function and homology informationmemapsin 2 / Golgi-associated vesicle lumen / beta-aspartyl-peptidase activity / signaling receptor ligand precursor processing / amyloid-beta formation / amyloid precursor protein catabolic process / membrane protein ectodomain proteolysis / amyloid-beta metabolic process / detection of mechanical stimulus involved in sensory perception of pain / response to insulin-like growth factor stimulus ...memapsin 2 / Golgi-associated vesicle lumen / beta-aspartyl-peptidase activity / signaling receptor ligand precursor processing / amyloid-beta formation / amyloid precursor protein catabolic process / membrane protein ectodomain proteolysis / amyloid-beta metabolic process / detection of mechanical stimulus involved in sensory perception of pain / response to insulin-like growth factor stimulus / prepulse inhibition / cellular response to manganese ion / multivesicular body / swimming behavior / cellular response to copper ion / presynaptic modulation of chemical synaptic transmission / hippocampal mossy fiber to CA3 synapse / protein serine/threonine kinase binding / trans-Golgi network / protein processing / recycling endosome / response to lead ion / cellular response to amyloid-beta / synaptic vesicle / late endosome / peptidase activity / positive regulation of neuron apoptotic process / amyloid-beta binding / endopeptidase activity / amyloid fibril formation / aspartic-type endopeptidase activity / early endosome / lysosome / endosome / endosome membrane / membrane raft / endoplasmic reticulum lumen / Amyloid fiber formation / axon / neuronal cell body / dendrite / enzyme binding / cell surface / Golgi apparatus / proteolysis / membrane / plasma membrane Similarity search - Function | ||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 1.94 Å MOLECULAR REPLACEMENT / Resolution: 1.94 Å | ||||||
 Authors Authors | Shaffer, P.L. | ||||||
 Citation Citation |  Journal: Acs Symp.Ser. / Year: 2020 Journal: Acs Symp.Ser. / Year: 2020Title: Discovery and Chemical Development of JNJ-50138803, a Clinical Candidate BACE1 Inhibitor Authors: Gijsen, H.J.M. / Lin, J. / Houpis, Y. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  6e3z.cif.gz 6e3z.cif.gz | 484.9 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb6e3z.ent.gz pdb6e3z.ent.gz | 397.7 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  6e3z.json.gz 6e3z.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/e3/6e3z https://data.pdbj.org/pub/pdb/validation_reports/e3/6e3z ftp://data.pdbj.org/pub/pdb/validation_reports/e3/6e3z ftp://data.pdbj.org/pub/pdb/validation_reports/e3/6e3z | HTTPS FTP |
|---|
-Related structure data
| Similar structure data |
|---|
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| |||||||||
| 2 | 
| |||||||||
| 3 | 
| |||||||||
| Unit cell |
| |||||||||
| Components on special symmetry positions |
|
- Components
Components
| #1: Protein | Mass: 48111.129 Da / Num. of mol.: 3 Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Gene: BACE1, BACE, KIAA1149 / Production host: Homo sapiens (human) / Gene: BACE1, BACE, KIAA1149 / Production host:  #2: Chemical | ChemComp-HRV / #3: Water | ChemComp-HOH / | Has protein modification | Y | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.52 Å3/Da / Density % sol: 51.13 % |
|---|---|
| Crystal grow | Temperature: 293 K / Method: vapor diffusion / pH: 6.25 / Details: 17% PEG-4000, 0.1 M MES |
-Data collection
| Diffraction | Mean temperature: 100 K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X06SA / Wavelength: 0.99986 Å / Beamline: X06SA / Wavelength: 0.99986 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: DECTRIS PILATUS3 6M / Detector: PIXEL / Date: Oct 19, 2011 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 0.99986 Å / Relative weight: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.94→49.451 Å / Num. obs: 104486 / % possible obs: 98.8 % / Redundancy: 4.13 % / Biso Wilson estimate: 33.42 Å2 / Rmerge F obs: 0.096 / Rmerge(I) obs: 0.044 / Rrim(I) all: 0.051 / Χ2: 1.067 / Net I/σ(I): 18.16 / Num. measured all: 431560 / Scaling rejects: 204 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1
|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT / Resolution: 1.94→49.451 Å / SU ML: 0.25 / Cross valid method: THROUGHOUT / σ(F): 1.35 / Phase error: 26.2 MOLECULAR REPLACEMENT / Resolution: 1.94→49.451 Å / SU ML: 0.25 / Cross valid method: THROUGHOUT / σ(F): 1.35 / Phase error: 26.2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Shrinkage radii: 0.9 Å / VDW probe radii: 1.11 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 115.43 Å2 / Biso mean: 47.1521 Å2 / Biso min: 22.61 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 1.94→49.451 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Rfactor Rfree error: 0 / Total num. of bins used: 6
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller























 PDBj
PDBj