+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 60000 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | sperm whale myoglobin 1-nitrosopropane | |||||||||
 要素 要素 | Myoglobin | |||||||||
 キーワード キーワード | OXYGEN STORAGE / Myoglobin / sperm whale / 1-nitrosopropane | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報酸化還元酵素; 他の含窒素化合物が電子供与する / nitrite reductase activity / sarcoplasm / 酸化還元酵素; 過酸化物を電子受容体にする; ペルオキシダーゼ / removal of superoxide radicals / oxygen carrier activity / peroxidase activity / oxygen binding / heme binding / extracellular exosome / metal ion binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 |  X線回折 / 解像度: 2 Å X線回折 / 解像度: 2 Å | |||||||||
 データ登録者 データ登録者 | Herrera, V.E. | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 2023 ジャーナル: Biochemistry / 年: 2023タイトル: Insights into Nitrosoalkane Binding to Myoglobin Provided by Crystallography of Wild-Type and Distal Pocket Mutant Derivatives. 著者: Herrera, V.E. / Charles, T.P. / Scott, T.G. / Prather, K.Y. / Nguyen, N.T. / Sohl, C.D. / Thomas, L.M. / Richter-Addo, G.B. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  6e04.cif.gz 6e04.cif.gz | 52.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb6e04.ent.gz pdb6e04.ent.gz | 35.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  6e04.json.gz 6e04.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  6e04_validation.pdf.gz 6e04_validation.pdf.gz | 821.2 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  6e04_full_validation.pdf.gz 6e04_full_validation.pdf.gz | 822.5 KB | 表示 | |
| XML形式データ |  6e04_validation.xml.gz 6e04_validation.xml.gz | 10.2 KB | 表示 | |
| CIF形式データ |  6e04_validation.cif.gz 6e04_validation.cif.gz | 14.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/e0/6e04 https://data.pdbj.org/pub/pdb/validation_reports/e0/6e04 ftp://data.pdbj.org/pub/pdb/validation_reports/e0/6e04 ftp://data.pdbj.org/pub/pdb/validation_reports/e0/6e04 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||||||
| 2 | 
| ||||||||||||
| 単位格子 |
| ||||||||||||
| Components on special symmetry positions |
|
- 要素
要素
-タンパク質 , 1種, 1分子 A
| #1: タンパク質 | 分子量: 17365.164 Da / 分子数: 1 / 由来タイプ: 組換発現 由来: (組換発現)  遺伝子: MB / 発現宿主:  |
|---|
-非ポリマー , 5種, 154分子 
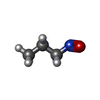







| #2: 化合物 | ChemComp-HEM / | ||||
|---|---|---|---|---|---|
| #3: 化合物 | ChemComp-XEM / | ||||
| #4: 化合物 | ChemComp-SO4 / #5: 化合物 | ChemComp-NA / | #6: 水 | ChemComp-HOH / | |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 3.08 Å3/Da / 溶媒含有率: 60.12 % |
|---|---|
| 結晶化 | 温度: 298 K / 手法: 蒸気拡散法, ハンギングドロップ法 詳細: 2.56-3.20 M AS, 100 mM Tris-HCl, 1 mm EDTA, pH 7.4 or 9.0. PH範囲: 7.4-9.0 |
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  回転陽極 / タイプ: RIGAKU MICROMAX-007 HF / 波長: 1.54178 Å 回転陽極 / タイプ: RIGAKU MICROMAX-007 HF / 波長: 1.54178 Å |
| 検出器 | タイプ: DECTRIS PILATUS 200K / 検出器: PIXEL / 日付: 2018年3月5日 |
| 放射 | モノクロメーター: mirrors / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.54178 Å / 相対比: 1 |
| 反射 | 解像度: 2→45.34 Å / Num. obs: 14515 / % possible obs: 99.69 % / 冗長度: 14.2 % / Net I/σ(I): 16.78 |
| 反射 シェル | 解像度: 2→2.03 Å |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 解像度: 2→45.34 Å / Cor.coef. Fo:Fc: 0.951 / Cor.coef. Fo:Fc free: 0.932 / SU B: 3.038 / SU ML: 0.087 / 交差検証法: THROUGHOUT / ESU R: 0.149 / ESU R Free: 0.135 / 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.2 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 17.284 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: 1 / 解像度: 2→45.34 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー





























 PDBj
PDBj






