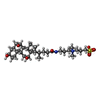
| 登録情報 | データベース: PDB / ID: 5xga
|
|---|
| タイトル | Crystal structure of the EnvZ periplasmic domain with CHAPS |
|---|
 要素 要素 | Osmolarity sensor protein EnvZ |
|---|
 キーワード キーワード | TRANSFERASE / histidine kinase / EnvZ |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
response to osmotic stress / histidine kinase / phosphorelay sensor kinase activity / phosphoprotein phosphatase activity / phosphorelay signal transduction system / outer membrane-bounded periplasmic space / protein autophosphorylation / signal transduction / protein homodimerization activity / ATP binding ...response to osmotic stress / histidine kinase / phosphorelay sensor kinase activity / phosphoprotein phosphatase activity / phosphorelay signal transduction system / outer membrane-bounded periplasmic space / protein autophosphorylation / signal transduction / protein homodimerization activity / ATP binding / identical protein binding / plasma membrane / cytosol類似検索 - 分子機能 : / HAMP domain / HAMP (Histidine kinases, Adenylyl cyclases, Methyl binding proteins, Phosphatases) domain / HAMP domain profile. / HAMP domain / His Kinase A (phospho-acceptor) domain / His Kinase A (phosphoacceptor) domain / Signal transduction histidine kinase, dimerisation/phosphoacceptor domain / Signal transduction histidine kinase-related protein, C-terminal / Signal transduction histidine kinase, dimerisation/phosphoacceptor domain superfamily ...: / HAMP domain / HAMP (Histidine kinases, Adenylyl cyclases, Methyl binding proteins, Phosphatases) domain / HAMP domain profile. / HAMP domain / His Kinase A (phospho-acceptor) domain / His Kinase A (phosphoacceptor) domain / Signal transduction histidine kinase, dimerisation/phosphoacceptor domain / Signal transduction histidine kinase-related protein, C-terminal / Signal transduction histidine kinase, dimerisation/phosphoacceptor domain superfamily / Histidine kinase domain / Histidine kinase domain profile. / Histidine kinase-, DNA gyrase B-, and HSP90-like ATPase / Histidine kinase-like ATPases / Histidine kinase/HSP90-like ATPase superfamily類似検索 - ドメイン・相同性 |
|---|
| 生物種 |   Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  単波長異常分散 / 解像度: 1.951 Å 単波長異常分散 / 解像度: 1.951 Å |
|---|
 データ登録者 データ登録者 | Hwang, E. / Cheong, H.K. / Jeon, Y.H. / Cheong, C. |
|---|
 引用 引用 |  ジャーナル: FEBS Lett. / 年: 2017 ジャーナル: FEBS Lett. / 年: 2017
タイトル: Crystal structure of the EnvZ periplasmic domain with CHAPS.
著者: Hwang, E. / Cheong, H.K. / Kim, S.Y. / Kwon, O. / Blain, K.Y. / Choe, S. / Yeo, K.J. / Jung, Y.W. / Jeon, Y.H. / Cheong, C. |
|---|
| 履歴 | | 登録 | 2017年4月13日 | 登録サイト: PDBJ / 処理サイト: PDBJ |
|---|
| 置き換え | 2017年7月19日 | ID: 5DCJ |
|---|
| 改定 1.0 | 2017年7月19日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年8月30日 | Group: Data collection / カテゴリ: diffrn_detector / Item: _diffrn_detector.detector |
|---|
| 改定 1.2 | 2024年3月27日 | Group: Data collection / Database references / カテゴリ: chem_comp_atom / chem_comp_bond / database_2
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  単波長異常分散 / 解像度: 1.951 Å
単波長異常分散 / 解像度: 1.951 Å  データ登録者
データ登録者 引用
引用 ジャーナル: FEBS Lett. / 年: 2017
ジャーナル: FEBS Lett. / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5xga.cif.gz
5xga.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5xga.ent.gz
pdb5xga.ent.gz PDB形式
PDB形式 5xga.json.gz
5xga.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 5xga_validation.pdf.gz
5xga_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 5xga_full_validation.pdf.gz
5xga_full_validation.pdf.gz 5xga_validation.xml.gz
5xga_validation.xml.gz 5xga_validation.cif.gz
5xga_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/xg/5xga
https://data.pdbj.org/pub/pdb/validation_reports/xg/5xga ftp://data.pdbj.org/pub/pdb/validation_reports/xg/5xga
ftp://data.pdbj.org/pub/pdb/validation_reports/xg/5xga リンク
リンク 集合体
集合体
 要素
要素

 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト: PAL/PLS
シンクロトロン / サイト: PAL/PLS  / ビームライン: 4A / 波長: 1 Å
/ ビームライン: 4A / 波長: 1 Å 解析
解析 単波長異常分散 / 解像度: 1.951→27.854 Å / SU ML: 0.21 / 交差検証法: FREE R-VALUE / σ(F): 1.56 / 位相誤差: 25.18
単波長異常分散 / 解像度: 1.951→27.854 Å / SU ML: 0.21 / 交差検証法: FREE R-VALUE / σ(F): 1.56 / 位相誤差: 25.18  ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj