| 登録情報 | データベース: PDB / ID: 5wiu
|
|---|
| タイトル | Structure of the human D4 Dopamine receptor in complex with Nemonapride |
|---|
 要素 要素 | D(4) dopamine receptor, soluble cytochrome b562 chimera |
|---|
 キーワード キーワード | SIGNALING PROTEIN/ANTAGONIST / GPCR / dopamine receptor / antagonist / sodium / SIGNALING PROTEIN-ANTAGONIST complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
positive regulation of dopamine uptake involved in synaptic transmission / dopamine neurotransmitter receptor activity, coupled via Gi/Go / response to histamine / epinephrine binding / dopamine neurotransmitter receptor activity / adenylate cyclase-inhibiting dopamine receptor signaling pathway / Dopamine receptors / dopamine binding / phospholipase C-activating dopamine receptor signaling pathway / G protein-coupled serotonin receptor activity ...positive regulation of dopamine uptake involved in synaptic transmission / dopamine neurotransmitter receptor activity, coupled via Gi/Go / response to histamine / epinephrine binding / dopamine neurotransmitter receptor activity / adenylate cyclase-inhibiting dopamine receptor signaling pathway / Dopamine receptors / dopamine binding / phospholipase C-activating dopamine receptor signaling pathway / G protein-coupled serotonin receptor activity / regulation of dopamine metabolic process / neurotransmitter receptor activity / fear response / behavioral response to ethanol / norepinephrine binding / arachidonate secretion / regulation of postsynaptic neurotransmitter receptor internalization / inhibitory postsynaptic potential / negative regulation of protein secretion / potassium channel regulator activity / social behavior / G protein-coupled receptor signaling pathway, coupled to cyclic nucleotide second messenger / behavioral fear response / behavioral response to cocaine / response to amphetamine / adult locomotory behavior / electron transport chain / regulation of circadian rhythm / SH3 domain binding / adenylate cyclase-modulating G protein-coupled receptor signaling pathway / intracellular calcium ion homeostasis / rhythmic process / G alpha (i) signalling events / chemical synaptic transmission / periplasmic space / electron transfer activity / positive regulation of MAPK cascade / postsynapse / iron ion binding / heme binding / centrosome / dendrite / glutamatergic synapse / membrane / metal ion binding / identical protein binding / plasma membrane類似検索 - 分子機能 Dopamine D4 receptor / Dopamine receptor family / Cytochrome b562 / Cytochrome b562 / Cytochrome c/b562 / Serpentine type 7TM GPCR chemoreceptor Srsx / G-protein coupled receptors family 1 signature. / 7 transmembrane receptor (rhodopsin family) / G protein-coupled receptor, rhodopsin-like / GPCR, rhodopsin-like, 7TM / G-protein coupled receptors family 1 profile.類似検索 - ドメイン・相同性 Nemonapride / OLEIC ACID / DI(HYDROXYETHYL)ETHER / PHOSPHATE ION / Soluble cytochrome b562 / D(4) dopamine receptor類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト)
  Escherichia coli (大腸菌) Escherichia coli (大腸菌) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.962 Å 分子置換 / 解像度: 1.962 Å |
|---|
 データ登録者 データ登録者 | Wacker, D. / Wang, S. / Levit, A. / Che, T. / Betz, R.M. / McCorvy, J.D. / Venkatakrishnan, A.J. / Huang, X.-P. / Dror, R.O. / Shoichet, B.K. / Roth, B.L. |
|---|
| 資金援助 |  米国, 4件 米国, 4件 | 組織 | 認可番号 | 国 |
|---|
| National Institutes of Health/National Institute of Mental Health (NIH/NIMH) | R01MH112205 |  米国 米国 | | National Institutes of Health/National Institute of Mental Health (NIH/NIMH) | HHSN-271-2013-00017-C |  米国 米国 | | National Institutes of Health/National Institute of Mental Health (NIH/NIMH) | U19MH082441 |  米国 米国 | | University of North Carolina | UNC Michael Hooker Chair for Protein Therapeutics and Translational Proteomics |  米国 米国 |
|
|---|
 引用 引用 |  ジャーナル: Science / 年: 2017 ジャーナル: Science / 年: 2017
タイトル: D4 dopamine receptor high-resolution structures enable the discovery of selective agonists.
著者: Wang, S. / Wacker, D. / Levit, A. / Che, T. / Betz, R.M. / McCorvy, J.D. / Venkatakrishnan, A.J. / Huang, X.P. / Dror, R.O. / Shoichet, B.K. / Roth, B.L. |
|---|
| 履歴 | | 登録 | 2017年7月20日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2017年10月18日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年11月1日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.journal_volume / _citation.page_first ..._citation.journal_volume / _citation.page_first / _citation.page_last / _citation.pdbx_database_id_PubMed / _citation.title / _citation_author.name |
|---|
| 改定 1.2 | 2018年1月17日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.3 | 2019年11月27日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.4 | 2023年10月4日 | Group: Data collection / Database references / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
| 改定 1.5 | 2024年10月23日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.962 Å
分子置換 / 解像度: 1.962 Å  データ登録者
データ登録者 米国, 4件
米国, 4件  引用
引用 ジャーナル: Science / 年: 2017
ジャーナル: Science / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5wiu.cif.gz
5wiu.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5wiu.ent.gz
pdb5wiu.ent.gz PDB形式
PDB形式 5wiu.json.gz
5wiu.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/wi/5wiu
https://data.pdbj.org/pub/pdb/validation_reports/wi/5wiu ftp://data.pdbj.org/pub/pdb/validation_reports/wi/5wiu
ftp://data.pdbj.org/pub/pdb/validation_reports/wi/5wiu リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト), (組換発現)
Homo sapiens (ヒト), (組換発現) 
 Insecta (節足動物) / 参照: UniProt: P21917, UniProt: P0ABE7
Insecta (節足動物) / 参照: UniProt: P21917, UniProt: P0ABE7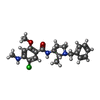









 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 23-ID-B / 波長: 1.033 Å
/ ビームライン: 23-ID-B / 波長: 1.033 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj

















