| 登録情報 | データベース: PDB / ID: 5v4y
|
|---|
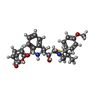
| タイトル | X-ray crystal structure of wild type HIV-1 protease in complex with GRL-09510 |
|---|
 要素 要素 | Protease |
|---|
 キーワード キーワード | HYDROLASE/HYDROLASE INHIBITOR / GRL-09510 / HIV-1 PROTEASE / PROTEASE-INHIBITOR / Pyran / Furan / NONPEPTIDIC / HYDROLASE-HYDROLASE INHIBITOR COMPLEX / CROWN-THF |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
aspartic-type endopeptidase activity / proteolysis類似検索 - 分子機能 Retropepsin-like catalytic domain / Retropepsins / Retroviral aspartyl protease / Aspartyl protease, retroviral-type family profile. / Peptidase A2A, retrovirus, catalytic / Cathepsin D, subunit A; domain 1 / Acid Proteases / Aspartic peptidase, active site / Eukaryotic and viral aspartyl proteases active site. / Aspartic peptidase domain superfamily ...Retropepsin-like catalytic domain / Retropepsins / Retroviral aspartyl protease / Aspartyl protease, retroviral-type family profile. / Peptidase A2A, retrovirus, catalytic / Cathepsin D, subunit A; domain 1 / Acid Proteases / Aspartic peptidase, active site / Eukaryotic and viral aspartyl proteases active site. / Aspartic peptidase domain superfamily / Beta Barrel / Mainly Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.9 Å 分子置換 / 解像度: 1.9 Å |
|---|
 データ登録者 データ登録者 | Yedidi, R.S. / Delino, N.S. / Das, D. / Kaufman, J.D. / Wingfield, P.T. / Ghosh, A.K. / Mitsuya, H. |
|---|
 引用 引用 |  ジャーナル: Sci Rep / 年: 2017 ジャーナル: Sci Rep / 年: 2017
タイトル: GRL-09510, a Unique P2-Crown-Tetrahydrofuranylurethane -Containing HIV-1 Protease Inhibitor, Maintains Its Favorable Antiviral Activity against Highly-Drug-Resistant HIV-1 Variants in vitro.
著者: Amano, M. / Miguel Salcedo-Gomez, P. / Yedidi, R.S. / Delino, N.S. / Nakata, H. / Venkateswara Rao, K. / Ghosh, A.K. / Mitsuya, H. |
|---|
| 履歴 | | 登録 | 2017年3月11日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2017年9月13日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2017年10月4日 | Group: Database references / カテゴリ: citation
Item: _citation.country / _citation.journal_abbrev ..._citation.country / _citation.journal_abbrev / _citation.journal_id_CSD / _citation.journal_id_ISSN / _citation.journal_volume / _citation.pdbx_database_id_DOI / _citation.title / _citation.year |
|---|
| 改定 1.2 | 2017年10月11日 | Group: Database references / カテゴリ: citation / citation_author
Item: _citation.page_first / _citation.page_last ..._citation.page_first / _citation.page_last / _citation.pdbx_database_id_PubMed / _citation.title / _citation_author.name |
|---|
| 改定 1.3 | 2023年10月4日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_special_symmetry
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報
 Human immunodeficiency virus 1 (ヒト免疫不全ウイルス)
Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.9 Å
分子置換 / 解像度: 1.9 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Sci Rep / 年: 2017
ジャーナル: Sci Rep / 年: 2017 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5v4y.cif.gz
5v4y.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5v4y.ent.gz
pdb5v4y.ent.gz PDB形式
PDB形式 5v4y.json.gz
5v4y.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 5v4y_validation.pdf.gz
5v4y_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 5v4y_full_validation.pdf.gz
5v4y_full_validation.pdf.gz 5v4y_validation.xml.gz
5v4y_validation.xml.gz 5v4y_validation.cif.gz
5v4y_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/v4/5v4y
https://data.pdbj.org/pub/pdb/validation_reports/v4/5v4y ftp://data.pdbj.org/pub/pdb/validation_reports/v4/5v4y
ftp://data.pdbj.org/pub/pdb/validation_reports/v4/5v4y
 リンク
リンク 集合体
集合体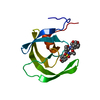

 要素
要素
 Human immunodeficiency virus 1 (ヒト免疫不全ウイルス)
Human immunodeficiency virus 1 (ヒト免疫不全ウイルス)
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 22-ID / 波長: 1 Å
/ ビームライン: 22-ID / 波長: 1 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー



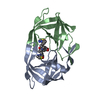




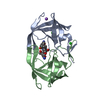













 PDBj
PDBj