| 登録情報 | データベース: PDB / ID: 5jxv
|
|---|
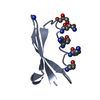
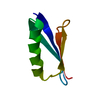
| タイトル | Solid-state MAS NMR structure of immunoglobulin beta 1 binding domain of protein G (GB1) |
|---|
 要素 要素 | Immunoglobulin G-binding protein G |
|---|
 キーワード キーワード | IMMUNE SYSTEM / Globular / alpha beta |
|---|
| 機能・相同性 | Ubiquitin-like (UB roll) - #10 / Ubiquitin-like (UB roll) / Roll / Alpha Beta / :  機能・相同性情報 機能・相同性情報 |
|---|
| 生物種 |  Streptococcus dysgalactiae subsp. equisimilis (バクテリア) Streptococcus dysgalactiae subsp. equisimilis (バクテリア) |
|---|
| 手法 | 個体NMR / torsion angle dynamics |
|---|
 データ登録者 データ登録者 | Andreas, L.B. / Jaudzems, K. / Stanek, J. / Lalli, D. / Bertarello, A. / Le Marchand, T. / Cala-De Paepe, D. / Kotelovica, S. / Akopjana, I. / Knott, B. ...Andreas, L.B. / Jaudzems, K. / Stanek, J. / Lalli, D. / Bertarello, A. / Le Marchand, T. / Cala-De Paepe, D. / Kotelovica, S. / Akopjana, I. / Knott, B. / Wegner, S. / Engelke, F. / Lesage, A. / Emsley, L. / Tars, K. / Herrmann, T. / Pintacuda, G. |
|---|
| 資金援助 |  フランス, フランス,  ドイツ, 6件 ドイツ, 6件 | 組織 | 認可番号 | 国 |
|---|
| Centre national de la recherche scientifique | IR-RMN FR3050 |  フランス フランス | | European Union's FP7 | 2012-ITN no 317127 |  フランス フランス | | European Research Council | 648974 |  フランス フランス | | European Union's FP7 | 624918 |  フランス フランス | | European Union's Horison 2020 | 661175 |  フランス フランス | | European Molecular Biology Organization | GA-2013-609409 |  ドイツ ドイツ |
|
|---|
 引用 引用 |  ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2016 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2016
タイトル: Structure of fully protonated proteins by proton-detected magic-angle spinning NMR.
著者: Andreas, L.B. / Jaudzems, K. / Stanek, J. / Lalli, D. / Bertarello, A. / Le Marchand, T. / Cala-De Paepe, D. / Kotelovica, S. / Akopjana, I. / Knott, B. / Wegner, S. / Engelke, F. / Lesage, A. ...著者: Andreas, L.B. / Jaudzems, K. / Stanek, J. / Lalli, D. / Bertarello, A. / Le Marchand, T. / Cala-De Paepe, D. / Kotelovica, S. / Akopjana, I. / Knott, B. / Wegner, S. / Engelke, F. / Lesage, A. / Emsley, L. / Tars, K. / Herrmann, T. / Pintacuda, G. |
|---|
| 履歴 | | 登録 | 2016年5月13日 | 登録サイト: RCSB / 処理サイト: PDBE |
|---|
| 改定 1.0 | 2016年8月10日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2016年8月17日 | Group: Database references |
|---|
| 改定 1.2 | 2016年8月31日 | Group: Database references |
|---|
| 改定 1.3 | 2018年2月7日 | Group: Experimental preparation / カテゴリ: pdbx_nmr_exptl_sample_conditions
Item: _pdbx_nmr_exptl_sample_conditions.temperature / _pdbx_nmr_exptl_sample_conditions.temperature_units |
|---|
| 改定 1.4 | 2018年2月28日 | Group: Author supporting evidence / カテゴリ: pdbx_audit_support / Item: _pdbx_audit_support.funding_organization |
|---|
| 改定 1.5 | 2019年8月21日 | Group: Data collection / カテゴリ: pdbx_nmr_software / pdbx_nmr_spectrometer
Item: _pdbx_nmr_software.name / _pdbx_nmr_spectrometer.model |
|---|
| 改定 1.6 | 2024年6月19日 | Group: Data collection / Database references / カテゴリ: chem_comp_atom / chem_comp_bond / database_2
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Streptococcus dysgalactiae subsp. equisimilis (バクテリア)
Streptococcus dysgalactiae subsp. equisimilis (バクテリア) データ登録者
データ登録者 フランス,
フランス,  ドイツ, 6件
ドイツ, 6件  引用
引用 ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2016
ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 2016 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 5jxv.cif.gz
5jxv.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb5jxv.ent.gz
pdb5jxv.ent.gz PDB形式
PDB形式 5jxv.json.gz
5jxv.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/jx/5jxv
https://data.pdbj.org/pub/pdb/validation_reports/jx/5jxv ftp://data.pdbj.org/pub/pdb/validation_reports/jx/5jxv
ftp://data.pdbj.org/pub/pdb/validation_reports/jx/5jxv リンク
リンク 集合体
集合体
 要素
要素 Streptococcus dysgalactiae subsp. equisimilis (バクテリア)
Streptococcus dysgalactiae subsp. equisimilis (バクテリア)
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj

 NMRPipe
NMRPipe