[English] 日本語
 Yorodumi
Yorodumi- PDB-4wx4: Crystal structure of adenovirus 8 protease in complex with a nitr... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 4wx4 | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of adenovirus 8 protease in complex with a nitrile inhibitor | ||||||
 Components Components |
| ||||||
 Keywords Keywords | HYDROLASE / cysteine protease / inhibitor / cofactor | ||||||
| Function / homology |  Function and homology information Function and homology informationadenain / virion component / cysteine-type endopeptidase activity / host cell nucleus / proteolysis / DNA binding Similarity search - Function | ||||||
| Biological species |  Human adenovirus D serotype 8 Human adenovirus D serotype 8synthetic construct (others) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / Resolution: 1.03 Å SYNCHROTRON / Resolution: 1.03 Å | ||||||
 Authors Authors | Grosche, P. / Sirockin, F. / Mac Sweeney, A. / Ramage, P. / Erbel, P. / Melkko, S. / Bernardi, A. / Hughes, N. / Ellis, D. / Combrink, K. ...Grosche, P. / Sirockin, F. / Mac Sweeney, A. / Ramage, P. / Erbel, P. / Melkko, S. / Bernardi, A. / Hughes, N. / Ellis, D. / Combrink, K. / Jarousse, N. / Altmann, E. | ||||||
 Citation Citation |  Journal: Bioorg.Med.Chem.Lett. / Year: 2015 Journal: Bioorg.Med.Chem.Lett. / Year: 2015Title: Structure-based design and optimization of potent inhibitors of the adenoviral protease. Authors: Grosche, P. / Sirockin, F. / Mac Sweeney, A. / Ramage, P. / Erbel, P. / Melkko, S. / Bernardi, A. / Hughes, N. / Ellis, D. / Combrink, K.D. / Jarousse, N. / Altmann, E. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  4wx4.cif.gz 4wx4.cif.gz | 114.7 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb4wx4.ent.gz pdb4wx4.ent.gz | 86.1 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  4wx4.json.gz 4wx4.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/wx/4wx4 https://data.pdbj.org/pub/pdb/validation_reports/wx/4wx4 ftp://data.pdbj.org/pub/pdb/validation_reports/wx/4wx4 ftp://data.pdbj.org/pub/pdb/validation_reports/wx/4wx4 | HTTPS FTP |
|---|
-Related structure data
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| Unit cell |
|
- Components
Components
-Protein / Protein/peptide , 2 types, 2 molecules AC
| #1: Protein | Mass: 23124.508 Da / Num. of mol.: 1 / Source method: isolated from a natural source / Source: (natural)  Human adenovirus D serotype 8 / References: UniProt: B9A5C1 Human adenovirus D serotype 8 / References: UniProt: B9A5C1 |
|---|---|
| #2: Protein/peptide | Mass: 1313.639 Da / Num. of mol.: 1 / Source method: obtained synthetically / Source: (synth.) synthetic construct (others) |
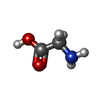
-Non-polymers , 4 types, 253 molecules 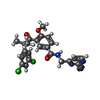





| #3: Chemical | ChemComp-3VF / |
|---|---|
| #4: Chemical | ChemComp-EPE / |
| #5: Chemical | ChemComp-GLY / |
| #6: Water | ChemComp-HOH / |
-Details
| Has protein modification | Y |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.26 Å3/Da / Density % sol: 45.62 % |
|---|---|
| Crystal grow | Temperature: 298 K / Method: vapor diffusion, hanging drop Details: Crystallization Reservoir Solution = 0.2M proline, 0.1M HEPES pH 7.5, 10% PEG3350 Crystallization Protein Solution = 5 mg/ml adenain in 20 mM Tris, 100 mM NaCl, pH 7.6. 5 mM inhibitor added. |
-Data collection
| Diffraction | Mean temperature: 100 K | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  SLS SLS  / Beamline: X10SA / Wavelength: 1 Å / Beamline: X10SA / Wavelength: 1 Å | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: DECTRIS PILATUS 6M / Detector: PIXEL / Date: Mar 25, 2013 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 1 Å / Relative weight: 1 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.03→58.9 Å / Num. obs: 102036 / % possible obs: 85.7 % / Observed criterion σ(I): -3 / Redundancy: 3.1 % / Biso Wilson estimate: 11.29 Å2 / Rmerge F obs: 0.029 / Rmerge(I) obs: 0.025 / Rrim(I) all: 0.029 / Χ2: 1.015 / Net I/σ(I): 26.93 / Num. measured all: 273190 | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell | Diffraction-ID: 1 / Rejects: _
|
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Resolution: 1.03→34.79 Å / Cor.coef. Fo:Fc: 0.98 / Cor.coef. Fo:Fc free: 0.975 / WRfactor Rfree: 0.3082 / WRfactor Rwork: 0.2413 / FOM work R set: 0.705 / SU B: 0.482 / SU ML: 0.012 / SU Rfree: 0.4 / Cross valid method: THROUGHOUT / σ(F): 0 / ESU R: 0.023 / ESU R Free: 0.024 / Stereochemistry target values: MAXIMUM LIKELIHOOD Details: HYDROGENS HAVE BEEN USED IF PRESENT IN THE INPUT U VALUES : REFINED INDIVIDUALLY
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Ion probe radii: 0.8 Å / Shrinkage radii: 0.8 Å / VDW probe radii: 1.2 Å / Solvent model: MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 96.37 Å2 / Biso mean: 12.065 Å2 / Biso min: 4.34 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: final / Resolution: 1.03→34.79 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Resolution: 1.03→1.057 Å / Total num. of bins used: 20
|
 Movie
Movie Controller
Controller











 PDBj
PDBj




