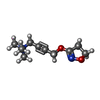
| 登録情報 | データベース: PDB / ID: 4mqs
|
|---|
| タイトル | Structure of active human M2 muscarinic acetylcholine receptor bound to the agonist iperoxo |
|---|
 要素 要素 | - Muscarinic acetylcholine receptor M2
- Nanobody 9-8
|
|---|
 キーワード キーワード | SIGNALING PROTEIN / G protein-coupled receptor / Muscarinic acetylcholine receptor |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
phospholipase C-activating G protein-coupled acetylcholine receptor signaling pathway / Muscarinic acetylcholine receptors / G protein-coupled acetylcholine receptor activity / cholinergic synapse / regulation of smooth muscle contraction / adenylate cyclase-inhibiting G protein-coupled acetylcholine receptor signaling pathway / arrestin family protein binding / regulation of heart contraction / G protein-coupled receptor signaling pathway, coupled to cyclic nucleotide second messenger / presynaptic modulation of chemical synaptic transmission ...phospholipase C-activating G protein-coupled acetylcholine receptor signaling pathway / Muscarinic acetylcholine receptors / G protein-coupled acetylcholine receptor activity / cholinergic synapse / regulation of smooth muscle contraction / adenylate cyclase-inhibiting G protein-coupled acetylcholine receptor signaling pathway / arrestin family protein binding / regulation of heart contraction / G protein-coupled receptor signaling pathway, coupled to cyclic nucleotide second messenger / presynaptic modulation of chemical synaptic transmission / clathrin-coated endocytic vesicle membrane / adenylate cyclase-modulating G protein-coupled receptor signaling pathway / response to virus / adenylate cyclase-inhibiting G protein-coupled receptor signaling pathway / G protein-coupled acetylcholine receptor signaling pathway / nervous system development / Cargo recognition for clathrin-mediated endocytosis / Clathrin-mediated endocytosis / presynapse / G alpha (i) signalling events / chemical synaptic transmission / postsynaptic membrane / cilium / ciliary basal body / G protein-coupled receptor signaling pathway / synapse / dendrite / nucleolus / Golgi apparatus / membrane / plasma membrane類似検索 - 分子機能 Muscarinic acetylcholine receptor M2 / Muscarinic acetylcholine receptor family / Rhopdopsin 7-helix transmembrane proteins / Rhodopsin 7-helix transmembrane proteins / Serpentine type 7TM GPCR chemoreceptor Srsx / G-protein coupled receptors family 1 signature. / 7 transmembrane receptor (rhodopsin family) / G protein-coupled receptor, rhodopsin-like / GPCR, rhodopsin-like, 7TM / G-protein coupled receptors family 1 profile. ...Muscarinic acetylcholine receptor M2 / Muscarinic acetylcholine receptor family / Rhopdopsin 7-helix transmembrane proteins / Rhodopsin 7-helix transmembrane proteins / Serpentine type 7TM GPCR chemoreceptor Srsx / G-protein coupled receptors family 1 signature. / 7 transmembrane receptor (rhodopsin family) / G protein-coupled receptor, rhodopsin-like / GPCR, rhodopsin-like, 7TM / G-protein coupled receptors family 1 profile. / Immunoglobulins / Up-down Bundle / Immunoglobulin-like / Sandwich / Mainly Beta / Mainly Alpha類似検索 - ドメイン・相同性 Chem-IXO / Muscarinic acetylcholine receptor M2類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト)
  Lama glama (ラマ) Lama glama (ラマ) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 3.5 Å 分子置換 / 解像度: 3.5 Å |
|---|
 データ登録者 データ登録者 | Kruse, A.C. / Ring, A.M. / Manglik, A. / Hu, J. / Hu, K. / Eitel, K. / Huebner, H. / Pardon, E. / Valant, C. / Sexton, P.M. ...Kruse, A.C. / Ring, A.M. / Manglik, A. / Hu, J. / Hu, K. / Eitel, K. / Huebner, H. / Pardon, E. / Valant, C. / Sexton, P.M. / Christopoulos, A. / Felder, C.C. / Gmeiner, P. / Steyaert, J. / Weis, W.I. / Garcia, K.C. / Wess, J. / Kobilka, B.K. |
|---|
 引用 引用 |  ジャーナル: Nature / 年: 2013 ジャーナル: Nature / 年: 2013
タイトル: Activation and allosteric modulation of a muscarinic acetylcholine receptor.
著者: Kruse, A.C. / Ring, A.M. / Manglik, A. / Hu, J. / Hu, K. / Eitel, K. / Hubner, H. / Pardon, E. / Valant, C. / Sexton, P.M. / Christopoulos, A. / Felder, C.C. / Gmeiner, P. / Steyaert, J. / ...著者: Kruse, A.C. / Ring, A.M. / Manglik, A. / Hu, J. / Hu, K. / Eitel, K. / Hubner, H. / Pardon, E. / Valant, C. / Sexton, P.M. / Christopoulos, A. / Felder, C.C. / Gmeiner, P. / Steyaert, J. / Weis, W.I. / Garcia, K.C. / Wess, J. / Kobilka, B.K. |
|---|
| 履歴 | | 登録 | 2013年9月16日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2013年11月27日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2013年12月4日 | Group: Database references |
|---|
| 改定 1.2 | 2013年12月18日 | Group: Database references |
|---|
| 改定 1.3 | 2017年7月5日 | Group: Source and taxonomy / カテゴリ: entity_src_gen |
|---|
| 改定 1.4 | 2023年9月20日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 1.5 | 2024年10月9日 | Group: Structure summary
カテゴリ: pdbx_entry_details / pdbx_modification_feature |
|---|
|
|---|
| Remark 650 | HELIX DETERMINATION METHOD: AUTHOR DETERMINED |
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト)
 X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 3.5 Å
分子置換 / 解像度: 3.5 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Nature / 年: 2013
ジャーナル: Nature / 年: 2013 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 4mqs.cif.gz
4mqs.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb4mqs.ent.gz
pdb4mqs.ent.gz PDB形式
PDB形式 4mqs.json.gz
4mqs.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/mq/4mqs
https://data.pdbj.org/pub/pdb/validation_reports/mq/4mqs ftp://data.pdbj.org/pub/pdb/validation_reports/mq/4mqs
ftp://data.pdbj.org/pub/pdb/validation_reports/mq/4mqs リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: CHRM2 / プラスミド: PVL1392
Homo sapiens (ヒト) / 遺伝子: CHRM2 / プラスミド: PVL1392


 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 23-ID-D / 波長: 1.033 Å
/ ビームライン: 23-ID-D / 波長: 1.033 Å 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー














 PDBj
PDBj