| 登録情報 | データベース: PDB / ID: 4j3y
|
|---|
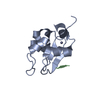
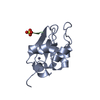
| タイトル | Crystal structure of XIAP-BIR2 domain |
|---|
 要素 要素 | E3 ubiquitin-protein ligase XIAP |
|---|
 キーワード キーワード | APOPTOSIS / IAP / XIAP / CASPASE / APOPTOSIS INHIBITOR |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
regulation of apoptosis involved in tissue homeostasis / positive regulation of protein linear polyubiquitination / copper ion homeostasis / regulation of BMP signaling pathway / regulation of nucleotide-binding domain, leucine rich repeat containing receptor signaling pathway / nucleotide-binding oligomerization domain containing 1 signaling pathway / nucleotide-binding oligomerization domain containing 2 signaling pathway / SMAC, XIAP-regulated apoptotic response / cysteine-type endopeptidase inhibitor activity involved in apoptotic process / Activation of caspases through apoptosome-mediated cleavage ...regulation of apoptosis involved in tissue homeostasis / positive regulation of protein linear polyubiquitination / copper ion homeostasis / regulation of BMP signaling pathway / regulation of nucleotide-binding domain, leucine rich repeat containing receptor signaling pathway / nucleotide-binding oligomerization domain containing 1 signaling pathway / nucleotide-binding oligomerization domain containing 2 signaling pathway / SMAC, XIAP-regulated apoptotic response / cysteine-type endopeptidase inhibitor activity involved in apoptotic process / Activation of caspases through apoptosome-mediated cleavage / Regulation of the apoptosome activity / SMAC (DIABLO) binds to IAPs / SMAC(DIABLO)-mediated dissociation of IAP:caspase complexes / TNFR1-induced proapoptotic signaling / RIPK1-mediated regulated necrosis / regulation of innate immune response / protein K63-linked ubiquitination / positive regulation of type I interferon production / negative regulation of tumor necrosis factor-mediated signaling pathway / cysteine-type endopeptidase inhibitor activity / protein serine/threonine kinase binding / Regulation of PTEN localization / positive regulation of protein ubiquitination / TNFR1-induced NF-kappa-B signaling pathway / positive regulation of JNK cascade / Deactivation of the beta-catenin transactivating complex / Regulation of TNFR1 signaling / RING-type E3 ubiquitin transferase / Regulation of necroptotic cell death / Regulation of PTEN stability and activity / Wnt signaling pathway / ubiquitin-protein transferase activity / ubiquitin protein ligase activity / positive regulation of canonical Wnt signaling pathway / regulation of inflammatory response / neuron apoptotic process / regulation of apoptotic process / response to lipopolysaccharide / positive regulation of canonical NF-kappaB signal transduction / regulation of cell cycle / defense response to bacterium / DNA damage response / negative regulation of apoptotic process / zinc ion binding / nucleoplasm / identical protein binding / nucleus / cytoplasm / cytosol類似検索 - 分子機能 XIAP/BIRC8, UBA domain / : / BIRC2/3-like, UBA domain / Inhibitor Of Apoptosis Protein (2mihbC-IAP-1); Chain A / Inhibitor Of Apoptosis Protein (2mihbC-IAP-1); Chain A / : / BIR repeat. / BIR repeat / Inhibitor of Apoptosis domain / BIR repeat profile. ...XIAP/BIRC8, UBA domain / : / BIRC2/3-like, UBA domain / Inhibitor Of Apoptosis Protein (2mihbC-IAP-1); Chain A / Inhibitor Of Apoptosis Protein (2mihbC-IAP-1); Chain A / : / BIR repeat. / BIR repeat / Inhibitor of Apoptosis domain / BIR repeat profile. / Baculoviral inhibition of apoptosis protein repeat / Zinc finger, C3HC4 type (RING finger) / Death-like domain superfamily / Ring finger / Zinc finger RING-type profile. / Zinc finger, RING-type / Orthogonal Bundle / Mainly Alpha類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 1.45 Å 分子置換 / 解像度: 1.45 Å |
|---|
 データ登録者 データ登録者 | Lukacs, C.M. / Janson, C.A. |
|---|
 引用 引用 |  ジャーナル: Acta Crystallogr.,Sect.D / 年: 2013 ジャーナル: Acta Crystallogr.,Sect.D / 年: 2013
タイトル: The structure of XIAP BIR2: understanding the selectivity of the BIR domains.
著者: Lukacs, C. / Belunis, C. / Crowther, R. / Danho, W. / Gao, L. / Goggin, B. / Janson, C.A. / Li, S. / Remiszewski, S. / Schutt, A. / Thakur, M.K. / Singh, S.K. / Swaminathan, S. / Pandey, R. / ...著者: Lukacs, C. / Belunis, C. / Crowther, R. / Danho, W. / Gao, L. / Goggin, B. / Janson, C.A. / Li, S. / Remiszewski, S. / Schutt, A. / Thakur, M.K. / Singh, S.K. / Swaminathan, S. / Pandey, R. / Tyagi, R. / Gosu, R. / Kamath, A.V. / Kuglstatter, A. |
|---|
| 履歴 | | 登録 | 2013年2月6日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2013年9月25日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2013年10月16日 | Group: Database references |
|---|
| 改定 1.2 | 2019年7月17日 | Group: Data collection / Refinement description / カテゴリ: software
Item: _software.classification / _software.name / _software.version |
|---|
| 改定 1.3 | 2023年9月20日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_asym_id / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_asym_id / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 1.45 Å
分子置換 / 解像度: 1.45 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Acta Crystallogr.,Sect.D / 年: 2013
ジャーナル: Acta Crystallogr.,Sect.D / 年: 2013 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 4j3y.cif.gz
4j3y.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb4j3y.ent.gz
pdb4j3y.ent.gz PDB形式
PDB形式 4j3y.json.gz
4j3y.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 4j3y_validation.pdf.gz
4j3y_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 4j3y_full_validation.pdf.gz
4j3y_full_validation.pdf.gz 4j3y_validation.xml.gz
4j3y_validation.xml.gz 4j3y_validation.cif.gz
4j3y_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/j3/4j3y
https://data.pdbj.org/pub/pdb/validation_reports/j3/4j3y ftp://data.pdbj.org/pub/pdb/validation_reports/j3/4j3y
ftp://data.pdbj.org/pub/pdb/validation_reports/j3/4j3y リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: API3, BIRC4, IAP3, U32974, XIAP / プラスミド: PET28A / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: API3, BIRC4, IAP3, U32974, XIAP / プラスミド: PET28A / 発現宿主: 
 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SLS
SLS  / ビームライン: X10SA
/ ビームライン: X10SA 解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj










