| 登録情報 | データベース: PDB / ID: 3mo0
|
|---|
| タイトル | Human G9a-like (GLP, also known as EHMT1) in complex with inhibitor E11 |
|---|
 要素 要素 | Histone-lysine N-methyltransferase, H3 lysine-9 specific 5 |
|---|
 キーワード キーワード | TRANSFERASE / Epigenetics / Histone lysine methylation / enzymatic inhibition / lysine mimics |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
[histone H3]-lysine9 N-methyltransferase / peptidyl-lysine monomethylation / peptidyl-lysine dimethylation / histone H3K9 methyltransferase activity / histone H3K9me2 methyltransferase activity / histone H3K27 methyltransferase activity / facultative heterochromatin formation / C2H2 zinc finger domain binding / protein-lysine N-methyltransferase activity / DNA methylation-dependent constitutive heterochromatin formation ...[histone H3]-lysine9 N-methyltransferase / peptidyl-lysine monomethylation / peptidyl-lysine dimethylation / histone H3K9 methyltransferase activity / histone H3K9me2 methyltransferase activity / histone H3K27 methyltransferase activity / facultative heterochromatin formation / C2H2 zinc finger domain binding / protein-lysine N-methyltransferase activity / DNA methylation-dependent constitutive heterochromatin formation / Transcriptional Regulation by E2F6 / Transcriptional Regulation by VENTX / regulation of embryonic development / response to fungicide / epigenetic regulation of gene expression / 転移酵素; 一炭素原子の基を移すもの; メチル基を移すもの / Regulation of endogenous retroelements by the Human Silencing Hub (HUSH) complex / transcription corepressor binding / methyltransferase activity / Regulation of TP53 Activity through Methylation / PKMTs methylate histone lysines / p53 binding / positive regulation of cold-induced thermogenesis / chromatin organization / Senescence-Associated Secretory Phenotype (SASP) / nuclear body / negative regulation of DNA-templated transcription / chromatin / negative regulation of transcription by RNA polymerase II / zinc ion binding / nucleoplasm / nucleus類似検索 - 分子機能 Histone-lysine N-methyltransferase EHMT1 / Histone-lysine N-methyltransferase EHMT1/EHMT2 / : / Histone-lysine N-methyltransferase EHMT1/EHMT2, Cys-rich region / Pre-SET motif / Pre-SET domain / Pre-SET domain profile. / N-terminal to some SET domains / Beta-clip-like / SET domain ...Histone-lysine N-methyltransferase EHMT1 / Histone-lysine N-methyltransferase EHMT1/EHMT2 / : / Histone-lysine N-methyltransferase EHMT1/EHMT2, Cys-rich region / Pre-SET motif / Pre-SET domain / Pre-SET domain profile. / N-terminal to some SET domains / Beta-clip-like / SET domain / Ankyrin repeats (many copies) / SET (Su(var)3-9, Enhancer-of-zeste, Trithorax) domain / SET domain / SET domain profile. / SET domain superfamily / SET domain / Beta Complex / Ankyrin repeats (3 copies) / Ankyrin repeat profile. / Ankyrin repeat region circular profile. / ankyrin repeats / Ankyrin repeat / Ankyrin repeat-containing domain superfamily / Mainly Beta類似検索 - ドメイン・相同性 Chem-E11 / S-ADENOSYL-L-HOMOCYSTEINE / Histone-lysine N-methyltransferase EHMT1類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.78 Å 分子置換 / 解像度: 2.78 Å |
|---|
 データ登録者 データ登録者 | Chang, Y. / Horton, J.R. / Cheng, X. |
|---|
 引用 引用 |  ジャーナル: J.Mol.Biol. / 年: 2010 ジャーナル: J.Mol.Biol. / 年: 2010
タイトル: Adding a lysine mimic in the design of potent inhibitors of histone lysine methyltransferases.
著者: Chang, Y. / Ganesh, T. / Horton, J.R. / Spannhoff, A. / Liu, J. / Sun, A. / Zhang, X. / Bedford, M.T. / Shinkai, Y. / Snyder, J.P. / Cheng, X. |
|---|
| 履歴 | | 登録 | 2010年4月22日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2010年6月30日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2023年9月6日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Refinement description
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_initial_refinement_model / pdbx_struct_conn_angle / struct_conn / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_asym_id / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_asym_id / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_asym_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_asym_id / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_asym_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
| 改定 1.3 | 2024年11月20日 | Group: Data collection / Structure summary
カテゴリ: chem_comp / pdbx_entry_details / pdbx_modification_feature
Item: _chem_comp.mon_nstd_flag / _chem_comp.type |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.78 Å
分子置換 / 解像度: 2.78 Å  データ登録者
データ登録者 引用
引用 ジャーナル: J.Mol.Biol. / 年: 2010
ジャーナル: J.Mol.Biol. / 年: 2010 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 3mo0.cif.gz
3mo0.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb3mo0.ent.gz
pdb3mo0.ent.gz PDB形式
PDB形式 3mo0.json.gz
3mo0.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 3mo0_validation.pdf.gz
3mo0_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 3mo0_full_validation.pdf.gz
3mo0_full_validation.pdf.gz 3mo0_validation.xml.gz
3mo0_validation.xml.gz 3mo0_validation.cif.gz
3mo0_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/mo/3mo0
https://data.pdbj.org/pub/pdb/validation_reports/mo/3mo0 ftp://data.pdbj.org/pub/pdb/validation_reports/mo/3mo0
ftp://data.pdbj.org/pub/pdb/validation_reports/mo/3mo0 リンク
リンク 集合体
集合体


 要素
要素 Homo sapiens (ヒト) / 遺伝子: EHMT1, EUHMTASE1, KIAA1876, KMT1D / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: EHMT1, EUHMTASE1, KIAA1876, KMT1D / 発現宿主: 

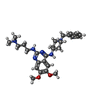







 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  APS
APS  / ビームライン: 22-ID / 波長: 0.99999
/ ビームライン: 22-ID / 波長: 0.99999  解析
解析 分子置換
分子置換 ムービー
ムービー コントローラー
コントローラー















 PDBj
PDBj













