[English] 日本語
 Yorodumi
Yorodumi- PDB-3k2a: Crystal structure of the homeobox domain of human homeobox protei... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 3k2a | ||||||
|---|---|---|---|---|---|---|---|
| Title | Crystal structure of the homeobox domain of human homeobox protein Meis2 | ||||||
 Components Components | Homeobox protein Meis2 | ||||||
 Keywords Keywords | DNA BINDING PROTEIN / homeobox domain / human homeobox protein MEIS2 / DNA-binding / transcription / Homeobox / Nucleus / Phosphoprotein | ||||||
| Function / homology |  Function and homology information Function and homology informationpositive regulation of cardiac muscle myoblast proliferation / negative regulation of myeloid cell differentiation / eye development / response to growth factor / embryonic pattern specification / pancreas development / transcription factor binding / response to mechanical stimulus / positive regulation of mitotic cell cycle / animal organ morphogenesis ...positive regulation of cardiac muscle myoblast proliferation / negative regulation of myeloid cell differentiation / eye development / response to growth factor / embryonic pattern specification / pancreas development / transcription factor binding / response to mechanical stimulus / positive regulation of mitotic cell cycle / animal organ morphogenesis / brain development / visual learning / sequence-specific double-stranded DNA binding / DNA-binding transcription activator activity, RNA polymerase II-specific / sequence-specific DNA binding / DNA-binding transcription factor activity, RNA polymerase II-specific / RNA polymerase II cis-regulatory region sequence-specific DNA binding / positive regulation of cell population proliferation / chromatin / perinuclear region of cytoplasm / negative regulation of transcription by RNA polymerase II / positive regulation of transcription by RNA polymerase II / DNA binding / nucleus Similarity search - Function | ||||||
| Biological species |  Homo sapiens (human) Homo sapiens (human) | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  SAD / Resolution: 1.95 Å SAD / Resolution: 1.95 Å | ||||||
 Authors Authors | Lam, R. / Soloveychik, M. / Battaile, K.P. / Romanov, V. / Lam, K. / Beletskaya, I. / Gordon, E. / Pai, E.F. / Chirgadze, N.Y. | ||||||
 Citation Citation |  Journal: To be Published Journal: To be PublishedTitle: Crystal structure of the homeobox domain of human homeobox protein Meis2 Authors: Lam, R. / Soloveychik, M. / Battaile, K.P. / Romanov, V. / Lam, K. / Beletskaya, I. / Gordon, E. / Pai, E.F. / Chirgadze, N.Y. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  3k2a.cif.gz 3k2a.cif.gz | 38.9 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb3k2a.ent.gz pdb3k2a.ent.gz | 26.2 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  3k2a.json.gz 3k2a.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/k2/3k2a https://data.pdbj.org/pub/pdb/validation_reports/k2/3k2a ftp://data.pdbj.org/pub/pdb/validation_reports/k2/3k2a ftp://data.pdbj.org/pub/pdb/validation_reports/k2/3k2a | HTTPS FTP |
|---|
-Related structure data
| Similar structure data |
|---|
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 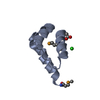
| ||||||||||||
| 2 | 
| ||||||||||||
| 3 | x 8
| ||||||||||||
| Unit cell |
| ||||||||||||
| Components on special symmetry positions |
|
- Components
Components
| #1: Protein | Mass: 7879.710 Da / Num. of mol.: 2 / Fragment: Residues 281-345 (homeobox domain) Source method: isolated from a genetically manipulated source Source: (gene. exp.)  Homo sapiens (human) / Gene: MEIS2, MRG1 / Plasmid: pET28-LIC / Production host: Homo sapiens (human) / Gene: MEIS2, MRG1 / Plasmid: pET28-LIC / Production host:  #2: Chemical | #3: Chemical | #4: Water | ChemComp-HOH / | Has protein modification | Y | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.57 Å3/Da / Density % sol: 52.17 % |
|---|---|
| Crystal grow | Temperature: 298 K / Method: vapor diffusion, sitting drop / pH: 7.5 Details: 28% PEG4000, 8% isopropanol, 0.1M sodium acetate, 10mM L-proline, pH 7.5, VAPOR DIFFUSION, SITTING DROP, temperature 298.0K |
-Data collection
| Diffraction | Mean temperature: 100 K | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  APS APS  / Beamline: 17-BM / Wavelength: 0.9791 Å / Beamline: 17-BM / Wavelength: 0.9791 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Detector | Type: ADSC QUANTUM 210 / Detector: CCD / Date: Aug 5, 2009 / Details: Si(111) double-crystal monochromator | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Radiation wavelength | Wavelength: 0.9791 Å / Relative weight: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection | Resolution: 1.95→50 Å / Num. obs: 12319 / % possible obs: 99.6 % / Redundancy: 28.5 % / Rmerge(I) obs: 0.063 / Χ2: 1.667 / Net I/σ(I): 17.6 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Reflection shell |
|
-Phasing
| Phasing | Method:  SAD SAD | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Phasing MAD set |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Phasing MAD set shell |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Phasing dm | Method: Solvent flattening and Histogram matching / Reflection: 12190 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Phasing dm shell |
|
- Processing
Processing
| Software |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  SAD / Resolution: 1.95→25.13 Å / Cor.coef. Fo:Fc: 0.946 / Cor.coef. Fo:Fc free: 0.937 / WRfactor Rfree: 0.238 / WRfactor Rwork: 0.22 / Occupancy max: 1 / Occupancy min: 0.5 / SU B: 7.039 / SU ML: 0.092 / Cross valid method: THROUGHOUT / σ(F): 0 / ESU R: 0.153 / ESU R Free: 0.138 / Stereochemistry target values: MAXIMUM LIKELIHOOD SAD / Resolution: 1.95→25.13 Å / Cor.coef. Fo:Fc: 0.946 / Cor.coef. Fo:Fc free: 0.937 / WRfactor Rfree: 0.238 / WRfactor Rwork: 0.22 / Occupancy max: 1 / Occupancy min: 0.5 / SU B: 7.039 / SU ML: 0.092 / Cross valid method: THROUGHOUT / σ(F): 0 / ESU R: 0.153 / ESU R Free: 0.138 / Stereochemistry target values: MAXIMUM LIKELIHOODDetails: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS. U VALUES: RESIDUAL ONLY
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Ion probe radii: 0.8 Å / Shrinkage radii: 0.8 Å / VDW probe radii: 1.4 Å / Solvent model: BABINET MODEL WITH MASK | |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso max: 61.75 Å2 / Biso mean: 29.967 Å2 / Biso min: 20.69 Å2
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 1.95→25.13 Å
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 20
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS params. | Method: refined / Refine-ID: X-RAY DIFFRACTION
| |||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement TLS group |
|
 Movie
Movie Controller
Controller












 PDBj
PDBj





