+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 3gca | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | The structural basis for recognition of the preQ0 metabolite by an unusually small riboswitch aptamer domain | ||||||
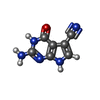
 要素 要素 | PreQ1 riboswitch | ||||||
 キーワード キーワード | RNA / PreQ1 / PreQ0 / riboswitch / ribosomal binding site / amptamer / metabolite | ||||||
| 機能・相同性 | Chem-PQ0 / RNA / RNA (> 10) 機能・相同性情報 機能・相同性情報 | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  多波長異常分散 / 解像度: 2.75 Å 多波長異常分散 / 解像度: 2.75 Å | ||||||
 データ登録者 データ登録者 | Spitale, R.C. / Wedekind, J.E. | ||||||
 引用 引用 |  ジャーナル: J.Biol.Chem. / 年: 2009 ジャーナル: J.Biol.Chem. / 年: 2009タイトル: The Structural Basis for Recognition of the PreQ0 Metabolite by an Unusually Small Riboswitch Aptamer Domain. 著者: Spitale, R.C. / Torelli, A.T. / Krucinska, J. / Bandarian, V. / Wedekind, J.E. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  3gca.cif.gz 3gca.cif.gz | 27.7 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb3gca.ent.gz pdb3gca.ent.gz | 19.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  3gca.json.gz 3gca.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  3gca_validation.pdf.gz 3gca_validation.pdf.gz | 415 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  3gca_full_validation.pdf.gz 3gca_full_validation.pdf.gz | 418.1 KB | 表示 | |
| XML形式データ |  3gca_validation.xml.gz 3gca_validation.xml.gz | 4.1 KB | 表示 | |
| CIF形式データ |  3gca_validation.cif.gz 3gca_validation.cif.gz | 4.7 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/gc/3gca https://data.pdbj.org/pub/pdb/validation_reports/gc/3gca ftp://data.pdbj.org/pub/pdb/validation_reports/gc/3gca ftp://data.pdbj.org/pub/pdb/validation_reports/gc/3gca | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
|
- 要素
要素
| #1: RNA鎖 | 分子量: 10599.417 Da / 分子数: 1 / 由来タイプ: 合成 詳細: The RNA strand was chemically synthesized based on the sequence of Class I, Type I PreQ1 riboswitch aptamer domain from T. tengcongensis |
|---|---|
| #2: 化合物 | ChemComp-PQ0 / |
| #3: 化合物 |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 4.93 Å3/Da / 溶媒含有率: 75.05 % | ||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | 温度: 293 K / 手法: 蒸気拡散法, ハンギングドロップ法 / pH: 6 詳細: 1.8 M Li2SO4, 0.10 M Na-cacodylate pH 6.0, 0.01 M Mg(SO4)2-, 5% (v/v) 1,3-propanediol and 2 mM spermine., VAPOR DIFFUSION, HANGING DROP, temperature 293K | ||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 |
|
-データ収集
| 回折 | 平均測定温度: 100 K | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  SSRL SSRL  / ビームライン: BL7-1 / 波長: 1.1395, 1.1407, 0.97622, 1.1395 / ビームライン: BL7-1 / 波長: 1.1395, 1.1407, 0.97622, 1.1395 | ||||||||||||
| 検出器 | タイプ: Quantum 315 CCD detector / 検出器: CCD / 日付: 2009年1月29日 詳細: Vertical focusing mirror; single crystal (Si111) bent monochromator (horizontal focusing). | ||||||||||||
| 放射 | プロトコル: MAD / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray | ||||||||||||
| 放射波長 |
| ||||||||||||
| 反射 | 解像度: 2.75→50 Å / Num. obs: 5990 / % possible obs: 97.6 % / Observed criterion σ(F): 0 / Observed criterion σ(I): -3 / 冗長度: 16.6 % / Biso Wilson estimate: 75 Å2 / Rsym value: 0.056 / Net I/σ(I): 36.47 | ||||||||||||
| 反射 シェル | 解像度: 2.75→2.85 Å / 冗長度: 15.8 % / Mean I/σ(I) obs: 6.5 / Num. unique all: 579 / Rsym value: 0.36 / % possible all: 98.5 |
- 解析
解析
| ソフトウェア |
| |||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  多波長異常分散 / 解像度: 2.75→28.33 Å / Rfactor Rfree error: 0.013 / Data cutoff high absF: 303382.6 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: CNS 1.2 / 詳細: BULK SOLVENT MODEL USED 多波長異常分散 / 解像度: 2.75→28.33 Å / Rfactor Rfree error: 0.013 / Data cutoff high absF: 303382.6 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: CNS 1.2 / 詳細: BULK SOLVENT MODEL USED
| |||||||||||||||||||||
| 溶媒の処理 | 溶媒モデル: FLAT MODEL / Bsol: 51.0924 Å2 / ksol: 0.2 e/Å3 | |||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 76 Å2
| |||||||||||||||||||||
| Refine analyze |
| |||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2.75→28.33 Å
| |||||||||||||||||||||
| 拘束条件 |
| |||||||||||||||||||||
| LS精密化 シェル | 解像度: 2.75→2.92 Å / Rfactor Rfree error: 0.06 / Total num. of bins used: 6
| |||||||||||||||||||||
| Xplor file |
|
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj