| 登録情報 | データベース: PDB / ID: 2mov
|
|---|
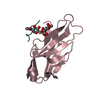
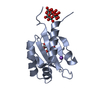
| タイトル | Receptor for Advanced Glycation End Products (RAGE) Specifically Recognizes Methylglyoxal Derived AGEs. |
|---|
 要素 要素 | Advanced glycosylation end product-specific receptor |
|---|
 キーワード キーワード | PROTEIN BINDING / PROTEIN/LIGAND |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
regulation of CD4-positive, alpha-beta T cell activation / negative regulation of blood circulation / advanced glycation end-product receptor activity / positive regulation of endothelin production / regulation of T cell mediated cytotoxicity / glucose mediated signaling pathway / negative regulation of long-term synaptic depression / positive regulation of monocyte extravasation / positive regulation of aspartic-type endopeptidase activity involved in amyloid precursor protein catabolic process / positive regulation of dendritic cell differentiation ...regulation of CD4-positive, alpha-beta T cell activation / negative regulation of blood circulation / advanced glycation end-product receptor activity / positive regulation of endothelin production / regulation of T cell mediated cytotoxicity / glucose mediated signaling pathway / negative regulation of long-term synaptic depression / positive regulation of monocyte extravasation / positive regulation of aspartic-type endopeptidase activity involved in amyloid precursor protein catabolic process / positive regulation of dendritic cell differentiation / regulation of p38MAPK cascade / regulation of non-canonical NF-kappaB signal transduction / scavenger receptor activity / induction of positive chemotaxis / transcytosis / protein localization to membrane / positive regulation of monocyte chemotactic protein-1 production / positive regulation of heterotypic cell-cell adhesion / S100 protein binding / regulation of long-term synaptic potentiation / regulation of spontaneous synaptic transmission / laminin receptor activity / positive regulation of p38MAPK cascade / negative regulation of interleukin-10 production / positive regulation of activated T cell proliferation / response to amyloid-beta / TRAF6 mediated NF-kB activation / Advanced glycosylation endproduct receptor signaling / transport across blood-brain barrier / negative regulation of long-term synaptic potentiation / positive regulation of chemokine production / positive regulation of interleukin-12 production / positive regulation of interleukin-1 beta production / astrocyte activation / positive regulation of JNK cascade / microglial cell activation / TAK1-dependent IKK and NF-kappa-B activation / regulation of synaptic plasticity / fibrillar center / response to wounding / positive regulation of non-canonical NF-kappaB signal transduction / cellular response to amyloid-beta / transmembrane signaling receptor activity / positive regulation of interleukin-6 production / neuron projection development / positive regulation of tumor necrosis factor production / cell junction / signaling receptor activity / positive regulation of NF-kappaB transcription factor activity / amyloid-beta binding / regulation of inflammatory response / postsynapse / molecular adaptor activity / learning or memory / positive regulation of ERK1 and ERK2 cascade / cell surface receptor signaling pathway / response to hypoxia / inflammatory response / positive regulation of protein phosphorylation / apical plasma membrane / protein-containing complex binding / cell surface / extracellular region / identical protein binding / plasma membrane類似検索 - 分子機能 CD80-like, immunoglobulin C2-set / CD80-like C2-set immunoglobulin domain / Immunoglobulin / Immunoglobulin domain / Immunoglobulin domain / Immunoglobulin subtype 2 / Immunoglobulin C-2 Type / Immunoglobulin/major histocompatibility complex, conserved site / Immunoglobulins and major histocompatibility complex proteins signature. / Immunoglobulin subtype ...CD80-like, immunoglobulin C2-set / CD80-like C2-set immunoglobulin domain / Immunoglobulin / Immunoglobulin domain / Immunoglobulin domain / Immunoglobulin subtype 2 / Immunoglobulin C-2 Type / Immunoglobulin/major histocompatibility complex, conserved site / Immunoglobulins and major histocompatibility complex proteins signature. / Immunoglobulin subtype / Immunoglobulin / Ig-like domain profile. / Immunoglobulin-like domain / Immunoglobulin-like domain superfamily / Immunoglobulins / Immunoglobulin-like fold / Immunoglobulin-like / Sandwich / Mainly Beta類似検索 - ドメイン・相同性 Chem-IOR / Advanced glycosylation end product-specific receptor類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 | 溶液NMR / simulated annealing |
|---|
| Model details | fewest violations, model12 |
|---|
 データ登録者 データ登録者 | Shekhtman, A. / Xue, J. / Ray, R. / Singer, D. / Bohme, D. / Burz, D.S. / Rai, V. / Hoffman, R. |
|---|
 引用 引用 |  ジャーナル: Biochemistry / 年: 2014 ジャーナル: Biochemistry / 年: 2014
タイトル: The Receptor for Advanced Glycation End Products (RAGE) Specifically Recognizes Methylglyoxal-Derived AGEs.
著者: Xue, J. / Ray, R. / Singer, D. / Bohme, D. / Burz, D.S. / Rai, V. / Hoffmann, R. / Shekhtman, A. |
|---|
| 履歴 | | 登録 | 2014年5月5日 | 登録サイト: BMRB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2014年6月25日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2023年6月14日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Other
カテゴリ: database_2 / pdbx_database_status ...database_2 / pdbx_database_status / pdbx_nmr_spectrometer / struct_ref_seq_dif / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_database_status.status_code_nmr_data / _pdbx_nmr_spectrometer.model / _struct_ref_seq_dif.details / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) データ登録者
データ登録者 引用
引用 ジャーナル: Biochemistry / 年: 2014
ジャーナル: Biochemistry / 年: 2014 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2mov.cif.gz
2mov.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2mov.ent.gz
pdb2mov.ent.gz PDB形式
PDB形式 2mov.json.gz
2mov.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2mov_validation.pdf.gz
2mov_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2mov_full_validation.pdf.gz
2mov_full_validation.pdf.gz 2mov_validation.xml.gz
2mov_validation.xml.gz 2mov_validation.cif.gz
2mov_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/mo/2mov
https://data.pdbj.org/pub/pdb/validation_reports/mo/2mov ftp://data.pdbj.org/pub/pdb/validation_reports/mo/2mov
ftp://data.pdbj.org/pub/pdb/validation_reports/mo/2mov リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: AGER, RAGE / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: AGER, RAGE / 発現宿主: 
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj













 HSQC
HSQC