| 登録情報 | データベース: PDB / ID: 2jt6
|
|---|
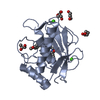
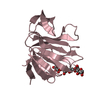
| タイトル | Solution structure of matrix metalloproteinase 3 (MMP-3) in the presence of 3-4'-cyanobyphenyl-4-yloxy)-n-hdydroxypropionamide (MMP-3 inhibitor VII) |
|---|
 要素 要素 | Stromelysin-1 |
|---|
 キーワード キーワード | HYDROLASE / metalloproteinase / MMP / Calcium / Collagen degradation / Extracellular matrix / Glycoprotein / Metal-binding / Metalloprotease / Polymorphism / Protease / Zinc / Zymogen |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
stromelysin 1 / cellular response to UV-A / regulation of neuroinflammatory response / Assembly of collagen fibrils and other multimeric structures / Activation of Matrix Metalloproteinases / response to amyloid-beta / Collagen degradation / collagen catabolic process / negative regulation of reactive oxygen species metabolic process / extracellular matrix disassembly ...stromelysin 1 / cellular response to UV-A / regulation of neuroinflammatory response / Assembly of collagen fibrils and other multimeric structures / Activation of Matrix Metalloproteinases / response to amyloid-beta / Collagen degradation / collagen catabolic process / negative regulation of reactive oxygen species metabolic process / extracellular matrix disassembly / Degradation of the extracellular matrix / extracellular matrix organization / EGFR Transactivation by Gastrin / extracellular matrix / negative regulation of phosphatidylinositol 3-kinase/protein kinase B signal transduction / cellular response to nitric oxide / regulation of cell migration / cellular response to reactive oxygen species / cellular response to amino acid stimulus / positive regulation of protein-containing complex assembly / protein catabolic process / metalloendopeptidase activity / metallopeptidase activity / peptidase activity / cellular response to lipopolysaccharide / Interleukin-4 and Interleukin-13 signaling / endopeptidase activity / Extra-nuclear estrogen signaling / innate immune response / serine-type endopeptidase activity / mitochondrion / proteolysis / extracellular space / extracellular region / zinc ion binding / nucleus / cytosol類似検索 - 分子機能 Hemopexin, conserved site / Hemopexin domain signature. / Hemopexin-like domain / Peptidoglycan binding-like / Peptidase M10A, cysteine switch, zinc binding site / Matrixins cysteine switch. / Hemopexin-like repeats / Hemopexin-like domain superfamily / Hemopexin / Putative peptidoglycan binding domain ...Hemopexin, conserved site / Hemopexin domain signature. / Hemopexin-like domain / Peptidoglycan binding-like / Peptidase M10A, cysteine switch, zinc binding site / Matrixins cysteine switch. / Hemopexin-like repeats / Hemopexin-like domain superfamily / Hemopexin / Putative peptidoglycan binding domain / Hemopexin repeat profile. / Hemopexin-like repeats. / Peptidase M10A / Peptidase M10A, catalytic domain / Peptidase M10, metallopeptidase / Matrixin / PGBD-like superfamily / Peptidase, metallopeptidase / Zinc-dependent metalloprotease / Collagenase (Catalytic Domain) / Collagenase (Catalytic Domain) / Metallopeptidase, catalytic domain superfamily / Neutral zinc metallopeptidases, zinc-binding region signature. / 3-Layer(aba) Sandwich / Alpha Beta類似検索 - ドメイン・相同性 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 | 溶液NMR / molecular dynamics |
|---|
 データ登録者 データ登録者 | Alcaraz, L.A. / Banci, L. / Bertini, I. / Cantini, F. / Donaire, A. / Gonnelli, L. |
|---|
 引用 引用 |  ジャーナル: J.Biol.Inorg.Chem. / 年: 2007 ジャーナル: J.Biol.Inorg.Chem. / 年: 2007
タイトル: Matrix metalloproteinase-inhibitor interaction: the solution structure of the catalytic domain of human matrix metalloproteinase-3 with different inhibitors
著者: Alcaraz, L.A. / Banci, L. / Bertini, I. / Cantini, F. / Donaire, A. / Gonnelli, L. |
|---|
| 履歴 | | 登録 | 2007年7月23日 | 登録サイト: BMRB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2008年2月19日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2011年7月13日 | Group: Version format compliance |
|---|
| 改定 2.0 | 2020年2月19日 | Group: Atomic model / Data collection ...Atomic model / Data collection / Database references / Derived calculations / Experimental preparation / Other
カテゴリ: atom_site / database_2 ...atom_site / database_2 / pdbx_database_status / pdbx_nmr_sample_details / pdbx_nmr_software / pdbx_nmr_spectrometer / pdbx_struct_assembly / pdbx_struct_oper_list
Item: _atom_site.auth_atom_id / _atom_site.label_atom_id ..._atom_site.auth_atom_id / _atom_site.label_atom_id / _pdbx_database_status.status_code_cs / _pdbx_nmr_sample_details.contents / _pdbx_nmr_software.name / _pdbx_nmr_spectrometer.model |
|---|
| 改定 2.1 | 2024年5月1日 | Group: Data collection / Database references / Derived calculations
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_struct_conn_angle / struct_conn / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr2_auth_comp_id / _pdbx_struct_conn_angle.ptnr2_auth_seq_id / _pdbx_struct_conn_angle.ptnr2_label_asym_id / _pdbx_struct_conn_angle.ptnr2_label_atom_id / _pdbx_struct_conn_angle.ptnr2_label_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) データ登録者
データ登録者 引用
引用 ジャーナル: J.Biol.Inorg.Chem. / 年: 2007
ジャーナル: J.Biol.Inorg.Chem. / 年: 2007 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2jt6.cif.gz
2jt6.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2jt6.ent.gz
pdb2jt6.ent.gz PDB形式
PDB形式 2jt6.json.gz
2jt6.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード 2jt6_validation.pdf.gz
2jt6_validation.pdf.gz wwPDB検証レポート
wwPDB検証レポート 2jt6_full_validation.pdf.gz
2jt6_full_validation.pdf.gz 2jt6_validation.xml.gz
2jt6_validation.xml.gz 2jt6_validation.cif.gz
2jt6_validation.cif.gz https://data.pdbj.org/pub/pdb/validation_reports/jt/2jt6
https://data.pdbj.org/pub/pdb/validation_reports/jt/2jt6 ftp://data.pdbj.org/pub/pdb/validation_reports/jt/2jt6
ftp://data.pdbj.org/pub/pdb/validation_reports/jt/2jt6 リンク
リンク 集合体
集合体
 要素
要素 Homo sapiens (ヒト) / 遺伝子: MMP3, STMY1 / 生物種 (発現宿主): Escherichia coli / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: MMP3, STMY1 / 生物種 (発現宿主): Escherichia coli / 発現宿主: 
 試料調製
試料調製 解析
解析 ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj













 HSQC
HSQC