[English] 日本語
 Yorodumi
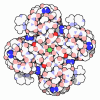
Yorodumi- PDB-2hmt: Diamond-shaped octameric ring structure of an RCK domain with NAD... -
+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 2hmt | ||||||
|---|---|---|---|---|---|---|---|
| Title | Diamond-shaped octameric ring structure of an RCK domain with NADH bound | ||||||
 Components Components | YuaA protein | ||||||
 Keywords Keywords | TRANSPORT PROTEIN / RCK / KTN / KTR / KTRA / KTRAB / membrane protein / ion transporter / symporter | ||||||
| Function / homology |  Function and homology information Function and homology informationpotassium channel activity / potassium ion transmembrane transport / identical protein binding / plasma membrane Similarity search - Function | ||||||
| Biological species |  | ||||||
| Method |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.2 Å MOLECULAR REPLACEMENT / Resolution: 2.2 Å | ||||||
 Authors Authors | Albright, R.A. / Morais-Cabral, J.H. | ||||||
 Citation Citation |  Journal: Cell(Cambridge,Mass.) / Year: 2006 Journal: Cell(Cambridge,Mass.) / Year: 2006Title: The RCK Domain of the KtrAB K(+) Transporter: Multiple Conformations of an Octameric Ring. Authors: Albright, R.A. / Ibar, J.L. / Kim, C.U. / Gruner, S.M. / Morais-Cabral, J.H. #1:  Journal: Cell(Cambridge,Mass.) / Year: 2002 Journal: Cell(Cambridge,Mass.) / Year: 2002Title: A Mechanism of Regulating Transmembrane Potassium Flux through a Ligand-Mediated Conformational Switch Authors: Roosild, T.P. / Miller, S. / Booth, I.R. / Choe, S. #2:  Journal: Nature / Year: 2002 Journal: Nature / Year: 2002Title: Crystal structure and mechanism of a calcium-gated potassium channel Authors: Jiang, Y. / Lee, A. / Chen, J. / Cadene, M. / Chait, B.T. / MacKinnon, R. | ||||||
| History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  2hmt.cif.gz 2hmt.cif.gz | 73.5 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb2hmt.ent.gz pdb2hmt.ent.gz | 54.4 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  2hmt.json.gz 2hmt.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/hm/2hmt https://data.pdbj.org/pub/pdb/validation_reports/hm/2hmt ftp://data.pdbj.org/pub/pdb/validation_reports/hm/2hmt ftp://data.pdbj.org/pub/pdb/validation_reports/hm/2hmt | HTTPS FTP |
|---|
-Related structure data
| Related structure data |  2hmsC  2hmuC  2hmvC  2hmwC  1lsuS S: Starting model for refinement C: citing same article ( |
|---|---|
| Similar structure data |
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||
| Unit cell |
| ||||||||
| Details | The biological assembly is an octameric ring generated from the asymmetric unit dimer using these symmetry operators: X, Y, Z and 2-X, Y, 1-Z and 2-X, 1-Y, Z and X, 1-Y, 1-Z |
- Components
Components
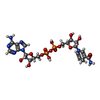
| #1: Protein | Mass: 16076.447 Da / Num. of mol.: 2 / Fragment: RCK core domain (KTN), residues 1-144 / Mutation: C22V Source method: isolated from a genetically manipulated source Source: (gene. exp.)   #2: Chemical | #3: Water | ChemComp-HOH / | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 3.21 Å3/Da / Density % sol: 61.68 % |
|---|---|
| Crystal grow | Temperature: 293 K / Method: vapor diffusion, sitting drop / pH: 8.8 Details: 500mM MgCl2, 50mM Tris pH 8.8, 8.5% (w/v) PEG 2000, VAPOR DIFFUSION, SITTING DROP, temperature 293K |
-Data collection
| Diffraction | Mean temperature: 100 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  CHESS CHESS  / Beamline: A1 / Wavelength: 0.9764 Å / Beamline: A1 / Wavelength: 0.9764 Å |
| Detector | Type: ADSC QUANTUM 210 / Detector: CCD / Date: Nov 16, 2005 |
| Radiation | Monochromator: Si 111 / Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 0.9764 Å / Relative weight: 1 |
| Reflection | Resolution: 2.2→50 Å / Num. all: 22051 / Num. obs: 21282 / % possible obs: 96.5 % / Observed criterion σ(F): 0 / Observed criterion σ(I): 0 / Redundancy: 7.2 % / Rmerge(I) obs: 0.107 / Χ2: 1.016 / Net I/σ(I): 8.9 |
| Reflection shell | Resolution: 2.2→2.28 Å / Redundancy: 6.3 % / Rmerge(I) obs: 0.59 / Num. unique all: 2140 / Χ2: 1.096 / % possible all: 99.4 |
- Processing
Processing
| Software |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT MOLECULAR REPLACEMENTStarting model: single domain of PDB entry 1LSU Resolution: 2.2→50 Å / FOM work R set: 0.855 / Cross valid method: THROUGHOUT / σ(F): 0 / Stereochemistry target values: Engh & Huber
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Solvent computation | Bsol: 44.465 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Displacement parameters | Biso mean: 46.987 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.2→50 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS refinement shell | Refine-ID: X-RAY DIFFRACTION / Total num. of bins used: 38
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Xplor file |
|
 Movie
Movie Controller
Controller










 PDBj
PDBj