+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 2ez5 | ||||||
|---|---|---|---|---|---|---|---|
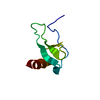
| タイトル | Solution Structure of the dNedd4 WW3* Domain- Comm LPSY Peptide Complex | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | SIGNALLING PROTEIN / LIGASE / Nedd4 / WW domain / Commissureless / PY motif / binding affinity | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of cardiac myofibril assembly / dendrite guidance / Roundabout binding / subsynaptic reticulum / Downregulation of SMAD2/3:SMAD4 transcriptional activity / ISG15 antiviral mechanism / Downregulation of ERBB4 signaling / Regulation of PTEN localization / imaginal disc-derived wing vein morphogenesis / Regulation of PTEN stability and activity ...positive regulation of cardiac myofibril assembly / dendrite guidance / Roundabout binding / subsynaptic reticulum / Downregulation of SMAD2/3:SMAD4 transcriptional activity / ISG15 antiviral mechanism / Downregulation of ERBB4 signaling / Regulation of PTEN localization / imaginal disc-derived wing vein morphogenesis / Regulation of PTEN stability and activity / Antigen processing: Ubiquitination & Proteasome degradation / neuron recognition / Golgi to lysosome transport / regulation of dendrite development / positive regulation of cardioblast proliferation / HECT-type E3 ubiquitin transferase / sodium channel inhibitor activity / Notch binding / axon midline choice point recognition / positive regulation of synapse assembly / regulation of dendrite morphogenesis / WW domain binding / dendrite morphogenesis / neuromuscular junction development / myosin binding / intracellular vesicle / positive regulation of endocytosis / positive regulation of receptor internalization / endocytic vesicle / negative regulation of Notch signaling pathway / synapse assembly / Notch signaling pathway / protein sequestering activity / axon guidance / negative regulation of smoothened signaling pathway / receptor internalization / endocytosis / ubiquitin-protein transferase activity / positive regulation of protein catabolic process / ubiquitin protein ligase activity / late endosome membrane / late endosome / nervous system development / ubiquitin-dependent protein catabolic process / vesicle / protein ubiquitination / protein domain specific binding / lysosomal membrane / Golgi apparatus / plasma membrane / cytosol / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  | ||||||
| 手法 | 溶液NMR / torsion angle dynamics | ||||||
 データ登録者 データ登録者 | Kanelis, V. / Bruce, M.C. / Skrynnikov, N.R. / Rotin, D. / Forman-Kay, J.D. | ||||||
 引用 引用 |  ジャーナル: Structure / 年: 2006 ジャーナル: Structure / 年: 2006タイトル: Structural Determinants for High-Affinity Binding in a Nedd4 WW3(*) Domain-Comm PY Motif Complex 著者: Kanelis, V. / Bruce, M.C. / Skrynnikov, N.R. / Rotin, D. / Forman-Kay, J.D. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  2ez5.cif.gz 2ez5.cif.gz | 510.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb2ez5.ent.gz pdb2ez5.ent.gz | 423.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  2ez5.json.gz 2ez5.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  2ez5_validation.pdf.gz 2ez5_validation.pdf.gz | 353.2 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  2ez5_full_validation.pdf.gz 2ez5_full_validation.pdf.gz | 730 KB | 表示 | |
| XML形式データ |  2ez5_validation.xml.gz 2ez5_validation.xml.gz | 34.3 KB | 表示 | |
| CIF形式データ |  2ez5_validation.cif.gz 2ez5_validation.cif.gz | 55.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ez/2ez5 https://data.pdbj.org/pub/pdb/validation_reports/ez/2ez5 ftp://data.pdbj.org/pub/pdb/validation_reports/ez/2ez5 ftp://data.pdbj.org/pub/pdb/validation_reports/ez/2ez5 | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質・ペプチド | 分子量: 5155.705 Da / 分子数: 1 / 断片: WW3* domain / 由来タイプ: 組換発現 由来: (組換発現)  発現宿主:  参照: UniProt: Q9VVI3, 合成酵素; C-N結合を形成; 酸-D-アミノ酸リガーゼ(ペプチド合成) |
|---|---|
| #2: タンパク質・ペプチド | 分子量: 1203.279 Da / 分子数: 1 / 断片: residues 227-237 / 由来タイプ: 合成 詳細: A peptide comprising residues 227-237 of Commissureless from Drosophila melanogaster was made using standard Fmoc peptide synthesis 参照: UniProt: Q24139 |
-実験情報
-実験
| 実験 | 手法: 溶液NMR | ||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
| ||||||||||||||||||||||||||||||||
| NMR実験の詳細 | Text: MIXING TIMES WERE: 175 MS FOR THE 3D F1,F3-13C,15N EDITED NOESY; 140 FOR THE DOUBLE FILTERED NOESY; 250 FOR THE HALF-FILTERED NOESY |
- 試料調製
試料調製
| 詳細 | 内容: 1.1 MM DNEDD4 WW3* DOMAIN, U- 13C,U-15N, 1.1 MM COMM LPSY PEPTIDE, UNLABELLED, 10 MM NA PHOS, PH 7.0, 20 MM NACL,90% H2O/10% D2O; 1.1 MM DNEDD4 WW3* DOMAIN, U- 13C,U -15N, 1.1 MM COMM LPSY ...内容: 1.1 MM DNEDD4 WW3* DOMAIN, U- 13C,U-15N, 1.1 MM COMM LPSY PEPTIDE, UNLABELLED, 10 MM NA PHOS, PH 7.0, 20 MM NACL,90% H2O/10% D2O; 1.1 MM DNEDD4 WW3* DOMAIN, U- 13C,U -15N, 1.1 MM COMM LPSY PEPTIDE, UNLABELLED, 10 MM NA PHOS, PH 7.0, 20 MM NACL,100% D2O; 1.4 MM DNEDD4 WW3* DOMAIN, U- 13C,U -15N, 1.0 MM COMM LPSY PEPTIDE, UNLABELLED, 10 MM NA PHOS, PH 7.0, 20 MM NACL, 90% H2O/10% D2O |
|---|---|
| 試料状態 | イオン強度: 10 mM NA PHOS, 20 mM NACL mM NA PHOS, 20 mM NACL; 10 mM NA PHOS, 20 mM NACL pH: 7 / 圧: 1 atm / 温度: 288 K |
-NMR測定
| NMRスペクトロメーター | タイプ: Varian INOVA / 製造業者: Varian / モデル: INOVA / 磁場強度: 500 MHz |
|---|
- 解析
解析
| NMR software |
| ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: torsion angle dynamics / ソフトェア番号: 1 | ||||||||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: structures with the lowest energy 計算したコンフォーマーの数: 200 / 登録したコンフォーマーの数: 30 |
 ムービー
ムービー コントローラー
コントローラー









 PDBj
PDBj



 NMRPipe
NMRPipe