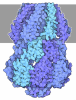
| 登録情報 | データベース: PDB / ID: 2aaq
|
|---|
| タイトル | Crystal Structure Analysis of the human Glutahione Reductase, complexed with GoPI |
|---|
 要素 要素 | glutathione reductase |
|---|
 キーワード キーワード | OXIDOREDUCTASE / Disulfide reductase / homodimer / antioxidative system / glutathione reduction / gold-coordination / protein gold complex |
|---|
| 機能・相同性 |  機能・相同性情報 機能・相同性情報
glutathione-disulfide reductase / Metabolism of ingested H2SeO4 and H2SeO3 into H2Se / glutathione-disulfide reductase (NADPH) activity / Interconversion of nucleotide di- and triphosphates / NFE2L2 regulating anti-oxidant/detoxification enzymes / Detoxification of Reactive Oxygen Species / glutathione metabolic process / cell redox homeostasis / TP53 Regulates Metabolic Genes / flavin adenine dinucleotide binding ...glutathione-disulfide reductase / Metabolism of ingested H2SeO4 and H2SeO3 into H2Se / glutathione-disulfide reductase (NADPH) activity / Interconversion of nucleotide di- and triphosphates / NFE2L2 regulating anti-oxidant/detoxification enzymes / Detoxification of Reactive Oxygen Species / glutathione metabolic process / cell redox homeostasis / TP53 Regulates Metabolic Genes / flavin adenine dinucleotide binding / NADP binding / cellular response to oxidative stress / electron transfer activity / mitochondrial matrix / external side of plasma membrane / mitochondrion / extracellular exosome / cytosol類似検索 - 分子機能 Glutathione reductase, eukaryote/bacterial / Pyridine nucleotide-disulphide oxidoreductase / : / Pyridine nucleotide-disulphide oxidoreductase, class I / Pyridine nucleotide-disulphide oxidoreductase, class I, active site / Pyridine nucleotide-disulphide oxidoreductases class-I active site. / FAD/NAD-linked reductase, C-terminal dimerisation domain / Pyridine nucleotide-disulphide oxidoreductase, dimerisation domain / Pyridine nucleotide-disulphide oxidoreductase, dimerisation domain / FAD/NAD-linked reductase, dimerisation domain superfamily ...Glutathione reductase, eukaryote/bacterial / Pyridine nucleotide-disulphide oxidoreductase / : / Pyridine nucleotide-disulphide oxidoreductase, class I / Pyridine nucleotide-disulphide oxidoreductase, class I, active site / Pyridine nucleotide-disulphide oxidoreductases class-I active site. / FAD/NAD-linked reductase, C-terminal dimerisation domain / Pyridine nucleotide-disulphide oxidoreductase, dimerisation domain / Pyridine nucleotide-disulphide oxidoreductase, dimerisation domain / FAD/NAD-linked reductase, dimerisation domain superfamily / FAD/NAD(P)-binding domain / Pyridine nucleotide-disulphide oxidoreductase / Enolase-like; domain 1 / FAD/NAD(P)-binding domain / FAD/NAD(P)-binding domain / 3-Layer(bba) Sandwich / FAD/NAD(P)-binding domain superfamily / 2-Layer Sandwich / Alpha Beta類似検索 - ドメイン・相同性 : / Chem-AUP / FLAVIN-ADENINE DINUCLEOTIDE / : / PHOSPHATE ION / Glutathione reductase, mitochondrial類似検索 - 構成要素 |
|---|
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) |
|---|
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2.6 Å 分子置換 / 解像度: 2.6 Å |
|---|
 データ登録者 データ登録者 | Urig, S. / Fritz-Wolf, K. / Reau, R. / Herold-Mende, C. / Toth, K. / Davioud-Charvet, E. / Becker, K. |
|---|
 引用 引用 |  ジャーナル: Angew.Chem.Int.Ed.Engl. / 年: 2006 ジャーナル: Angew.Chem.Int.Ed.Engl. / 年: 2006
タイトル: Undressing of Phosphine Gold(I) Complexes as Irreversible Inhibitors of Human Disulfide Reductases.
著者: Urig, S. / Fritz-Wolf, K. / Reau, R. / Herold-Mende, C. / Toth, K. / Davioud-Charvet, E. / Becker, K. |
|---|
| 履歴 | | 登録 | 2005年7月14日 | 登録サイト: RCSB / 処理サイト: RCSB |
|---|
| 改定 1.0 | 2006年4月4日 | Provider: repository / タイプ: Initial release |
|---|
| 改定 1.1 | 2008年4月30日 | Group: Version format compliance |
|---|
| 改定 1.2 | 2011年7月13日 | Group: Derived calculations / Version format compliance |
|---|
| 改定 1.3 | 2017年10月11日 | Group: Refinement description / カテゴリ: software / Item: _software.classification / _software.name |
|---|
| 改定 1.4 | 2024年10月30日 | Group: Data collection / Database references ...Data collection / Database references / Derived calculations / Structure summary
カテゴリ: chem_comp_atom / chem_comp_bond ...chem_comp_atom / chem_comp_bond / database_2 / pdbx_entry_details / pdbx_modification_feature / pdbx_struct_conn_angle / struct_conn / struct_site
Item: _database_2.pdbx_DOI / _database_2.pdbx_database_accession ..._database_2.pdbx_DOI / _database_2.pdbx_database_accession / _pdbx_struct_conn_angle.ptnr1_auth_comp_id / _pdbx_struct_conn_angle.ptnr1_auth_seq_id / _pdbx_struct_conn_angle.ptnr1_label_asym_id / _pdbx_struct_conn_angle.ptnr1_label_atom_id / _pdbx_struct_conn_angle.ptnr1_label_comp_id / _pdbx_struct_conn_angle.ptnr1_label_seq_id / _pdbx_struct_conn_angle.ptnr3_auth_comp_id / _pdbx_struct_conn_angle.ptnr3_auth_seq_id / _pdbx_struct_conn_angle.ptnr3_label_asym_id / _pdbx_struct_conn_angle.ptnr3_label_atom_id / _pdbx_struct_conn_angle.ptnr3_label_comp_id / _pdbx_struct_conn_angle.ptnr3_label_seq_id / _pdbx_struct_conn_angle.value / _struct_conn.pdbx_dist_value / _struct_conn.ptnr1_auth_comp_id / _struct_conn.ptnr1_auth_seq_id / _struct_conn.ptnr1_label_asym_id / _struct_conn.ptnr1_label_atom_id / _struct_conn.ptnr1_label_comp_id / _struct_conn.ptnr1_label_seq_id / _struct_conn.ptnr2_auth_comp_id / _struct_conn.ptnr2_auth_seq_id / _struct_conn.ptnr2_label_asym_id / _struct_conn.ptnr2_label_atom_id / _struct_conn.ptnr2_label_comp_id / _struct_conn.ptnr2_label_seq_id / _struct_site.pdbx_auth_asym_id / _struct_site.pdbx_auth_comp_id / _struct_site.pdbx_auth_seq_id |
|---|
|
|---|
 データを開く
データを開く 基本情報
基本情報 要素
要素 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト)
Homo sapiens (ヒト) X線回折 /
X線回折 /  シンクロトロン /
シンクロトロン /  分子置換 / 解像度: 2.6 Å
分子置換 / 解像度: 2.6 Å  データ登録者
データ登録者 引用
引用 ジャーナル: Angew.Chem.Int.Ed.Engl. / 年: 2006
ジャーナル: Angew.Chem.Int.Ed.Engl. / 年: 2006 構造の表示
構造の表示 Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク ダウンロード
ダウンロード 2aaq.cif.gz
2aaq.cif.gz PDBx/mmCIF形式
PDBx/mmCIF形式 pdb2aaq.ent.gz
pdb2aaq.ent.gz PDB形式
PDB形式 2aaq.json.gz
2aaq.json.gz PDBx/mmJSON形式
PDBx/mmJSON形式 その他のダウンロード
その他のダウンロード https://data.pdbj.org/pub/pdb/validation_reports/aa/2aaq
https://data.pdbj.org/pub/pdb/validation_reports/aa/2aaq ftp://data.pdbj.org/pub/pdb/validation_reports/aa/2aaq
ftp://data.pdbj.org/pub/pdb/validation_reports/aa/2aaq リンク
リンク 集合体
集合体

 要素
要素 Homo sapiens (ヒト) / 遺伝子: hGR / プラスミド: pUB302-2 / 発現宿主:
Homo sapiens (ヒト) / 遺伝子: hGR / プラスミド: pUB302-2 / 発現宿主: 




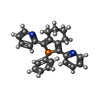










 X線回折 / 使用した結晶の数: 1
X線回折 / 使用した結晶の数: 1  試料調製
試料調製 シンクロトロン / サイト:
シンクロトロン / サイト:  SLS
SLS  / ビームライン: X06SA / 波長: 0.902691 Å
/ ビームライン: X06SA / 波長: 0.902691 Å 解析
解析 分子置換 / 解像度: 2.6→14.98 Å / Rfactor Rfree error: 0.009 / Data cutoff high absF: 3176837.56 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: Engh & Huber
分子置換 / 解像度: 2.6→14.98 Å / Rfactor Rfree error: 0.009 / Data cutoff high absF: 3176837.56 / Data cutoff low absF: 0 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0 / 立体化学のターゲット値: Engh & Huber ムービー
ムービー コントローラー
コントローラー













 PDBj
PDBj