+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1rrd | ||||||
|---|---|---|---|---|---|---|---|
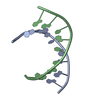
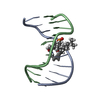
| タイトル | DNA/RNA HYBRID DUPLEX CONTAINING A PURINE-RICH RNA STRAND, NMR, 10 STRUCTURES | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | DNA-RNA HYBRID / DNA/RNA HYBRID / PURINE/PYRIMIDINE-RICH STRANDS / ANTISENSE | ||||||
| 機能・相同性 | DNA / RNA 機能・相同性情報 機能・相同性情報 | ||||||
| 手法 | 溶液NMR / simulated annealing | ||||||
 データ登録者 データ登録者 | Gyi, J.I. / Lane, A.N. / Conn, G.L. / Brown, T. | ||||||
 引用 引用 |  ジャーナル: Biochemistry / 年: 1998 ジャーナル: Biochemistry / 年: 1998タイトル: Solution structures of DNA.RNA hybrids with purine-rich and pyrimidine-rich strands: comparison with the homologous DNA and RNA duplexes. 著者: Gyi, J.I. / Lane, A.N. / Conn, G.L. / Brown, T. #1:  ジャーナル: Biochemistry / 年: 1996 ジャーナル: Biochemistry / 年: 1996タイトル: Comparison of the Thermodynamic Stabilities and Solution Conformations of DNA.RNA Hybrids Containing Purine-Rich and Pyrimidine-Rich Strands with DNA and RNA Duplexes 著者: Gyi, J.I. / Conn, G.L. / Lane, A.N. / Brown, T. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1rrd.cif.gz 1rrd.cif.gz | 130 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1rrd.ent.gz pdb1rrd.ent.gz | 106 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1rrd.json.gz 1rrd.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1rrd_validation.pdf.gz 1rrd_validation.pdf.gz | 330.6 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1rrd_full_validation.pdf.gz 1rrd_full_validation.pdf.gz | 409.7 KB | 表示 | |
| XML形式データ |  1rrd_validation.xml.gz 1rrd_validation.xml.gz | 4.2 KB | 表示 | |
| CIF形式データ |  1rrd_validation.cif.gz 1rrd_validation.cif.gz | 6.8 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/rr/1rrd https://data.pdbj.org/pub/pdb/validation_reports/rr/1rrd ftp://data.pdbj.org/pub/pdb/validation_reports/rr/1rrd ftp://data.pdbj.org/pub/pdb/validation_reports/rr/1rrd | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: RNA鎖 | 分子量: 3287.076 Da / 分子数: 1 / 由来タイプ: 合成 |
|---|---|
| #2: DNA鎖 | 分子量: 2961.940 Da / 分子数: 1 / 由来タイプ: 合成 |
-実験情報
-実験
| 実験 | 手法: 溶液NMR | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 試料状態 | pH: 7 / 温度: 303 K |
|---|---|
| 結晶化 | *PLUS 手法: other / 詳細: NMR |
-NMR測定
| NMRスペクトロメーター |
|
|---|
- 解析
解析
| ソフトウェア | 名称:  AMBER / 分類: 精密化 AMBER / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR software |
| ||||||||||||||||||||||||
| 精密化 | 手法: simulated annealing / ソフトェア番号: 1 詳細: DISTANCE CONSTRAINTS FOR GLYCOSIDIC TORSION ANGLES, PENTOSE PSEUDOROTATIONAL PHASE ANGLES/AMPLITUDES AND FRACTION OF SOUTH STATE SUGARS CALCULATED FROM NOE BUILD-UP CURVES AND COUPLING ...詳細: DISTANCE CONSTRAINTS FOR GLYCOSIDIC TORSION ANGLES, PENTOSE PSEUDOROTATIONAL PHASE ANGLES/AMPLITUDES AND FRACTION OF SOUTH STATE SUGARS CALCULATED FROM NOE BUILD-UP CURVES AND COUPLING CONSTANTS BY A LEAST-SQUARES/GRID SEARCH METHOD IMPLEMENTED IN NUCFIT AND PFIT (A.N. LANE, NIMR, UK). TEN DIFFERENT SETS OF UNIQUE RESTRAINTS GENERATED 10 STRUCTURES, THE AVERAGE OF WHICH SATISFIED THE EXPERIMENTALLY DERIVED FRACTION OF SOUTH STATE SUGARS BETTER STRUCTURES GENERATED FROM A SINGLE SET OF RESTRAINTS. INTERNU CLEOTIDE DISTANCE CONSTRAINTS CALCULATED FROM NOE-BUILD-UP CURVES. STRUCTURES CALCULATED BY SIMULATED ANNEALING/RMD PROTOCOL WITHIN DISCOVER 95.0 USING AN AMBER FORCE FIELD AND A DISTANCE DIELECTRIC CONSTANT. | ||||||||||||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: LOWEST POTENTIAL ENERGY, MINIMAL VIOLATIONS AND ACCEPTABLE STEREOCHEMISTRY 計算したコンフォーマーの数: 100 / 登録したコンフォーマーの数: 10 |
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj