+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1rax | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | RA-DOMAIN OF RAL GUANOSINE-NUCLEOTIDE DISSOCIATION STIMULATOR | ||||||
 要素 要素 | PROTEIN (RA-DOMAIN OF RAL GUANOSINE DISSOCIATION STIMULATOR) | ||||||
 キーワード キーワード | RAS-BINDING DOMAIN / RALGEF / RALGDS / RAS / RA | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報GTPase regulator activity / brush border / p38MAPK events / guanyl-nucleotide exchange factor activity / RAF/MAP kinase cascade / Ras protein signal transduction / nucleus / plasma membrane / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 | 溶液NMR / DISTANCE GEOMETRY, SIMULATED ANNEALING | ||||||
 データ登録者 データ登録者 | Mueller, T.D. / Handel, L. / Schmieder, P. / Oschkinat, H. | ||||||
 引用 引用 |  ジャーナル: To be Published ジャーナル: To be Publishedタイトル: High-Resolution Structure of the Ra-Domain of Human Ralgds and a Dynamics Study of its Binding Loop to Ras 著者: Mueller, T.D. / Handel, L. / Schmieder, P. / Oschkinat, H. #1:  ジャーナル: Nat.Struct.Biol. / 年: 1997 ジャーナル: Nat.Struct.Biol. / 年: 1997タイトル: Three-dimensional structure of the Ras-interacting domain of RalGDS. 著者: Huang, L. / Weng, X. / Hofer, F. / Martin, G.S. / Kim, S.H. #2:  ジャーナル: Nat.Struct.Biol. / 年: 1997 ジャーナル: Nat.Struct.Biol. / 年: 1997タイトル: Structure of the Ras-binding domain of RalGEF and implications for Ras binding and signalling. 著者: Geyer, M. / Herrmann, C. / Wohlgemuth, S. / Wittinghofer, A. / Kalbitzer, H.R. #3: ジャーナル: J.Biol.Chem. / 年: 1996 タイトル: Differential interaction of the ras family GTP-binding proteins H-Ras, Rap1A, and R-Ras with the putative effector molecules Raf kinase and Ral-guanine nucleotide exchange factor. 著者: Herrmann, C. / Horn, G. / Spaargaren, M. / Wittinghofer, A. #4: ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 1994 タイトル: Identification of the guanine nucleotide dissociation stimulator for Ral as a putative effector molecule of R-ras, H-ras, K-ras, and Rap. 著者: Spaargaren, M. / Bischoff, J.R. #5: ジャーナル: Proc.Natl.Acad.Sci.USA / 年: 1994 タイトル: Activated Ras interacts with the Ral guanine nucleotide dissociation stimulator. 著者: Hofer, F. / Fields, S. / Schneider, C. / Martin, G.S. #6: ジャーナル: Embo J. / 年: 1993 タイトル: Characterization of a guanine nucleotide dissociation stimulator for a ras-related GTPase. 著者: Albright, C.F. / Giddings, B.W. / Liu, J. / Vito, M. / Weinberg, R.A. | ||||||
| 履歴 |
|
- 構造の表示
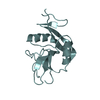
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1rax.cif.gz 1rax.cif.gz | 299.3 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1rax.ent.gz pdb1rax.ent.gz | 246.7 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1rax.json.gz 1rax.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ra/1rax https://data.pdbj.org/pub/pdb/validation_reports/ra/1rax ftp://data.pdbj.org/pub/pdb/validation_reports/ra/1rax ftp://data.pdbj.org/pub/pdb/validation_reports/ra/1rax | HTTPS FTP |
|---|
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: タンパク質 | 分子量: 12888.555 Da / 分子数: 1 / 断片: RAS-BINDING DOMAIN / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: RALGDS / プラスミド: PGEX-2T / 遺伝子 (発現宿主): HUMAN RALGDS GENE (RALGDS) / 発現宿主: Homo sapiens (ヒト) / 遺伝子: RALGDS / プラスミド: PGEX-2T / 遺伝子 (発現宿主): HUMAN RALGDS GENE (RALGDS) / 発現宿主:  |
|---|
-実験情報
-実験
| 実験 | 手法: 溶液NMR | ||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| NMR実験 |
|
- 試料調製
試料調製
| 試料状態 | pH: 6.5 / 温度: 300 K |
|---|
-NMR測定
| NMRスペクトロメーター |
|
|---|
- 解析
解析
| NMR software |
| ||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: DISTANCE GEOMETRY, SIMULATED ANNEALING / ソフトェア番号: 1 | ||||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: STRUCTURES WITH THE LOWEST TOTAL ENERGY AND NOE ENERGY WERE SELECTED 計算したコンフォーマーの数: 20 / 登録したコンフォーマーの数: 10 |
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj



 X-PLOR
X-PLOR