+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1p4z | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Effect of Sequence on the Conformational Geometry of DNA Holliday Junctions | ||||||||||||||||||
 要素 要素 | 5'-D(* キーワード キーワードDNA / B-DNA / Double Helix | 機能・相同性 | DNA |  機能・相同性情報 機能・相同性情報手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換 / 解像度: 2 Å 分子置換 / 解像度: 2 Å  データ登録者 データ登録者Hays, F.A. / Vargason, J.M. / Ho, P.S. |  引用 引用 ジャーナル: Biochemistry / 年: 2003 ジャーナル: Biochemistry / 年: 2003タイトル: Effect of Sequence on the Conformation of DNA Holliday Junctions 著者: Hays, F.A. / Vargason, J.M. / Ho, P.S. 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1p4z.cif.gz 1p4z.cif.gz | 16.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1p4z.ent.gz pdb1p4z.ent.gz | 10.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1p4z.json.gz 1p4z.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1p4z_validation.pdf.gz 1p4z_validation.pdf.gz | 378.7 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1p4z_full_validation.pdf.gz 1p4z_full_validation.pdf.gz | 379.2 KB | 表示 | |
| XML形式データ |  1p4z_validation.xml.gz 1p4z_validation.xml.gz | 3.3 KB | 表示 | |
| CIF形式データ |  1p4z_validation.cif.gz 1p4z_validation.cif.gz | 4.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/p4/1p4z https://data.pdbj.org/pub/pdb/validation_reports/p4/1p4z ftp://data.pdbj.org/pub/pdb/validation_reports/p4/1p4z ftp://data.pdbj.org/pub/pdb/validation_reports/p4/1p4z | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 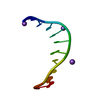
| ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 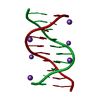
| ||||||||||||||||||
| 単位格子 |
| ||||||||||||||||||
| Components on special symmetry positions |
| ||||||||||||||||||
| 詳細 | THIS ENTRY CONTAINS THE CRYSTALLOGRAPHIC ASYMMETRIC UNIT WHICH CONSISTS OF ONE CHAIN. GENERATION OF THE DOUBLE HELIX CAN BE PERFORMED WITH THE FOLLOWING: matrix= (0.50000 0.86603 0.00000 ) (0.86603 -0.50000 0.00000 ) (0.00000 0.00000 -1.00000 ) translation= (16.68855 -28.90537 14.61163) |
- 要素
要素
| #1: DNA鎖 | 分子量: 3045.004 Da / 分子数: 1 / 由来タイプ: 合成 詳細: DNA was synthesized on an Applied Biosystems DNA synthesizer using phosphoramidite chemistry, with the trityl-protecting group left intact at the 5-terminal nucleotide, FOR SUBSEQUENT HPLC ...詳細: DNA was synthesized on an Applied Biosystems DNA synthesizer using phosphoramidite chemistry, with the trityl-protecting group left intact at the 5-terminal nucleotide, FOR SUBSEQUENT HPLC PURIFICATION, THEN DEPROTECTED BY TREATMENT WITH 3% ACETIC ACID FOR FIFTEEN MINUTES, NEUTRALIZED WITH AMMONIUM HYDROXIDE, AND DESALTED ON A SIGMA G-25 SEPHADEX COLUMN. | ||
|---|---|---|---|
| #2: 化合物 | | #3: 水 | ChemComp-HOH / | |
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 1.87 Å3/Da / 溶媒含有率: 33.78 % | ||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | 温度: 293 K / pH: 7.5 詳細: 0.6mM DNA, 5mM TRIS(HCl), 25mM Ca-Acetate, 7% MPD, pH 7.5, VAPOR DIFFUSION, SITTING DROP, temperature 293K, pH 7.50 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 結晶化 | *PLUS 温度: 20 ℃ / pH: 7.5 / 手法: 蒸気拡散法 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 103 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  APS APS  / ビームライン: 14-BM-C / 波長: 1 / ビームライン: 14-BM-C / 波長: 1 |
| 検出器 | タイプ: ADSC QUANTUM 4 / 検出器: CCD / 日付: 2002年7月18日 / 詳細: BENT CONICAL SI-MIRROR (RH COATING) |
| 放射 | モノクロメーター: BENT GE(111) MONOCHROMATOR / プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1 Å / 相対比: 1 |
| 反射 | 解像度: 2→17.47 Å / Num. obs: 2143 / % possible obs: 95.1 % / Observed criterion σ(I): 0 / Biso Wilson estimate: 3.6 Å2 / Rmerge(I) obs: 0.039 |
| 反射 シェル | 解像度: 2→2.13 Å / Rmerge(I) obs: 0.124 / Mean I/σ(I) obs: 2.38 / % possible all: 74.6 |
| 反射 | *PLUS 最高解像度: 2 Å / 最低解像度: 50 Å / Num. obs: 2143 / % possible obs: 94.6 % / Rmerge(I) obs: 0.048 / Num. measured all: 32690 |
| 反射 シェル | *PLUS % possible obs: 53.2 % / Rmerge(I) obs: 0.124 / Mean I/σ(I) obs: 3.3 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: UNPUBLISHED RESULTS OF STRUCTURE WITH ISOMORPHOUS UNIT CELL DIMENSIONS 解像度: 2→17.47 Å / Rfactor Rfree error: 0.019 / Isotropic thermal model: RESTRAINED / 交差検証法: THROUGHOUT / σ(F): 0
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 7.8 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine analyze |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 2→17.47 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 2→2.13 Å / Rfactor Rfree error: 0.055 / Total num. of bins used: 6
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | *PLUS 最高解像度: 2 Å / 最低解像度: 20 Å / % reflection Rfree: 10 % / Rfactor Rfree: 0.268 / Rfactor Rwork: 0.236 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 | *PLUS
|
 ムービー
ムービー コントローラー
コントローラー








 PDBj
PDBj




