+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1oao | ||||||
|---|---|---|---|---|---|---|---|
| タイトル | NiZn[Fe4S4] and NiNi[Fe4S4] clusters in closed and open alpha subunits of acetyl-CoA synthase/carbon monoxide dehydrogenase | ||||||
 要素 要素 | (CARBON MONOXIDE DEHYDROGENASE/ACETYL-COA SYNTHASE SUBUNIT ...) x 2 | ||||||
 キーワード キーワード | OXIDOREDUCTASE/TRANSFERASE / OXIDOREDUCTASE-TRANSFERASE COMPLEX / ELECTRON TRANSFER / OXIDOREDUCTASE / ACETYL-COA FORMATION / WOOD/LJUNGDAHL PATHWAY / NICKEL | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報CO-methylating acetyl-CoA synthase / CO-methylating acetyl-CoA synthase activity / anaerobic carbon monoxide dehydrogenase / hydroxylamine reductase activity / anaerobic carbon-monoxide dehydrogenase activity / carbon fixation / acetyl-CoA metabolic process / nickel cation binding / generation of precursor metabolites and energy / peroxidase activity ...CO-methylating acetyl-CoA synthase / CO-methylating acetyl-CoA synthase activity / anaerobic carbon monoxide dehydrogenase / hydroxylamine reductase activity / anaerobic carbon-monoxide dehydrogenase activity / carbon fixation / acetyl-CoA metabolic process / nickel cation binding / generation of precursor metabolites and energy / peroxidase activity / response to hydrogen peroxide / 4 iron, 4 sulfur cluster binding / metal ion binding 類似検索 - 分子機能 | ||||||
| 生物種 |  MOORELLA THERMOACETICA (バクテリア) MOORELLA THERMOACETICA (バクテリア) | ||||||
| 手法 |  X線回折 / X線回折 /  シンクロトロン / シンクロトロン /  分子置換, 分子置換,  多波長異常分散 / 解像度: 1.9 Å 多波長異常分散 / 解像度: 1.9 Å | ||||||
 データ登録者 データ登録者 | Darnault, C. / Volbeda, A. / Kim, E.J. / Legrand, P. / Vernede, X. / Lindahl, P.A. / Fontecilla-Camps, J.C. | ||||||
 引用 引用 |  ジャーナル: Nat.Struct.Biol. / 年: 2003 ジャーナル: Nat.Struct.Biol. / 年: 2003タイトル: Ni-Zn-[Fe4-S4] and Ni-Ni-[Fe4-S4] Clusters in Closed and Open Alpha Subunits of Acetyl-Coa Synthase/Carbon Monoxide Dehydrogenase 著者: Darnault, C. / Volbeda, A. / Kim, E.J. / Legrand, P. / Vernede, X. / Lindahl, P.A. / Fontecilla-Camps, J.C. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1oao.cif.gz 1oao.cif.gz | 573.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1oao.ent.gz pdb1oao.ent.gz | 467.3 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1oao.json.gz 1oao.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1oao_validation.pdf.gz 1oao_validation.pdf.gz | 571.1 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1oao_full_validation.pdf.gz 1oao_full_validation.pdf.gz | 631.7 KB | 表示 | |
| XML形式データ |  1oao_validation.xml.gz 1oao_validation.xml.gz | 111.9 KB | 表示 | |
| CIF形式データ |  1oao_validation.cif.gz 1oao_validation.cif.gz | 161 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/oa/1oao https://data.pdbj.org/pub/pdb/validation_reports/oa/1oao ftp://data.pdbj.org/pub/pdb/validation_reports/oa/1oao ftp://data.pdbj.org/pub/pdb/validation_reports/oa/1oao | HTTPS FTP |
-関連構造データ
| 関連構造データ |  1jjy S: 精密化の開始モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||
| 単位格子 |
| ||||||||
| 非結晶学的対称性 (NCS) | NCS oper: (Code: given Matrix: (0.161329, -0.978881, -0.125561), ベクター: |
- 要素
要素
-CARBON MONOXIDE DEHYDROGENASE/ACETYL-COA SYNTHASE SUBUNIT ... , 2種, 4分子 ABCD
| #1: タンパク質 | 分子量: 73006.930 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  MOORELLA THERMOACETICA (バクテリア) MOORELLA THERMOACETICA (バクテリア)参照: UniProt: P27989, carbon-monoxide dehydrogenase (acceptor), anaerobic carbon monoxide dehydrogenase #2: タンパク質 | 分子量: 81816.930 Da / 分子数: 2 / 由来タイプ: 天然 / 由来: (天然)  MOORELLA THERMOACETICA (バクテリア) / 参照: UniProt: P27988, CO-methylating acetyl-CoA synthase MOORELLA THERMOACETICA (バクテリア) / 参照: UniProt: P27988, CO-methylating acetyl-CoA synthase |
|---|
-非ポリマー , 12種, 1328分子 
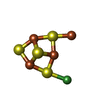




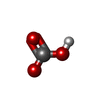
















| #3: 化合物 | ChemComp-SF4 / #4: 化合物 | #5: 化合物 | #6: 化合物 | ChemComp-SO4 / #7: 化合物 | ChemComp-GOL / #8: 化合物 | #9: 化合物 | ChemComp-BCT / | #10: 化合物 | ChemComp-ZN / | #11: 化合物 | #12: 化合物 | ChemComp-SX / | #13: 化合物 | ChemComp-ACT / | #14: 水 | ChemComp-HOH / | |
|---|
-詳細
| 構成要素の詳細 | CATALYZES THE INTERCONVERSION OF CO AND CO2 AND THE SYNTHESIS OF ACETYL-COENZYME A FROM THE ...CATALYZES THE INTERCONVE |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.69 Å3/Da / 溶媒含有率: 54.24 % | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | pH: 7.2 / 詳細: pH 7.20 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 結晶化 | *PLUS 温度: 20 ℃ / pH: 8 / 手法: 蒸気拡散法, ハンギングドロップ法 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 100 K |
|---|---|
| 放射光源 | 由来:  シンクロトロン / サイト: シンクロトロン / サイト:  ESRF ESRF  / ビームライン: ID14-1 / 波長: 0.934 / ビームライン: ID14-1 / 波長: 0.934 |
| 検出器 | タイプ: ADSC CCD / 検出器: CCD / 日付: 2002年9月15日 |
| 放射 | プロトコル: SINGLE WAVELENGTH / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 0.934 Å / 相対比: 1 |
| 反射 | 解像度: 1.9→29.2 Å / Num. obs: 479707 / % possible obs: 94.4 % / 冗長度: 1.8 % / Rmerge(I) obs: 0.053 |
| 反射 シェル | 解像度: 1.9→1.95 Å / 冗長度: 1.5 % / Rmerge(I) obs: 0.238 / % possible all: 67.9 |
| 反射 | *PLUS 最高解像度: 1.9 Å / 最低解像度: 30 Å / Num. obs: 239946 |
| 反射 シェル | *PLUS % possible obs: 67.9 % / Mean I/σ(I) obs: 3.3 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換, 分子置換,  多波長異常分散 多波長異常分散開始モデル: PDB ENTRY 1JJY  1jjy 解像度: 1.9→25 Å / Cor.coef. Fo:Fc: 0.967 / Cor.coef. Fo:Fc free: 0.952 / SU B: 2.296 / SU ML: 0.068 / TLS residual ADP flag: LIKELY RESIDUAL / 交差検証法: THROUGHOUT / ESU R: 0.114 / ESU R Free: 0.108 / 立体化学のターゲット値: MAXIMUM LIKELIHOOD
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | イオンプローブ半径: 0.8 Å / 減衰半径: 0.8 Å / VDWプローブ半径: 1.4 Å / 溶媒モデル: BABINET MODEL WITH MASK | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 12.79 Å2
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 1.9→25 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj
















