+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1n2c | ||||||
|---|---|---|---|---|---|---|---|
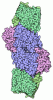
| タイトル | NITROGENASE COMPLEX FROM AZOTOBACTER VINELANDII STABILIZED BY ADP-TETRAFLUOROALUMINATE | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | COMPLEX OF NITROGENASE PROTEINS / NITROGENASE / NITROGEN FIXATION / SIGNAL TRANSDUCTION / ELECTRON TRANSFER / ATP HYDROLYSIS | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報molybdenum-iron nitrogenase complex / nitrogenase / nitrogenase activity / nitrogen fixation / iron-sulfur cluster binding / 4 iron, 4 sulfur cluster binding / ATP binding / metal ion binding 類似検索 - 分子機能 | ||||||
| 生物種 |  Azotobacter vinelandii (窒素固定) Azotobacter vinelandii (窒素固定) | ||||||
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 3 Å 分子置換 / 解像度: 3 Å | ||||||
 データ登録者 データ登録者 | Schindelin, H. / Kisker, C. / Rees, D.C. | ||||||
 引用 引用 |  ジャーナル: Nature / 年: 1997 ジャーナル: Nature / 年: 1997タイトル: Structure of ADP x AIF4(-)-stabilized nitrogenase complex and its implications for signal transduction. 著者: Schindelin, H. / Kisker, C. / Schlessman, J.L. / Howard, J.B. / Rees, D.C. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1n2c.cif.gz 1n2c.cif.gz | 544.2 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1n2c.ent.gz pdb1n2c.ent.gz | 444.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1n2c.json.gz 1n2c.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1n2c_validation.pdf.gz 1n2c_validation.pdf.gz | 731.3 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1n2c_full_validation.pdf.gz 1n2c_full_validation.pdf.gz | 795.4 KB | 表示 | |
| XML形式データ |  1n2c_validation.xml.gz 1n2c_validation.xml.gz | 66.2 KB | 表示 | |
| CIF形式データ |  1n2c_validation.cif.gz 1n2c_validation.cif.gz | 96.3 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/n2/1n2c https://data.pdbj.org/pub/pdb/validation_reports/n2/1n2c ftp://data.pdbj.org/pub/pdb/validation_reports/n2/1n2c ftp://data.pdbj.org/pub/pdb/validation_reports/n2/1n2c | HTTPS FTP |
-関連構造データ
| 関連構造データ |  1min S: 精密化の開始モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| ||||||||||||||||||||||||||||||||||||
| 単位格子 |
| ||||||||||||||||||||||||||||||||||||
| 非結晶学的対称性 (NCS) | NCSドメイン:
NCS oper:
|
- 要素
要素
-NITROGENASE MOLYBDENUM-IRON ... , 2種, 4分子 ACBD
| #1: タンパク質 | 分子量: 55231.848 Da / 分子数: 2 断片: CHAINS A AND C ARE THE ALPHA CHAINS, CHAINS B AND D ARE THE BETA CHAINS 由来タイプ: 天然 / 由来: (天然)  Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07328, nitrogenase Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07328, nitrogenase#2: タンパク質 | 分子量: 59404.684 Da / 分子数: 2 断片: CHAINS A AND C ARE THE ALPHA CHAINS, CHAINS B AND D ARE THE BETA CHAINS 由来タイプ: 天然 / 由来: (天然)  Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07329, nitrogenase Azotobacter vinelandii (窒素固定) / 参照: UniProt: P07329, nitrogenase |
|---|
-タンパク質 , 1種, 4分子 EFGH
| #3: タンパク質 | 分子量: 31417.045 Da / 分子数: 4 / 由来タイプ: 天然 詳細: 2\:1 COMPLEX OF HOMODIMERIC FE-PROTEIN AND HETEROTETRAMERIC MOFE-PROTEIN 由来: (天然)  Azotobacter vinelandii (窒素固定) / 参照: UniProt: P00459, nitrogenase Azotobacter vinelandii (窒素固定) / 参照: UniProt: P00459, nitrogenase |
|---|
-非ポリマー , 8種, 22分子 


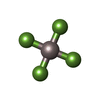


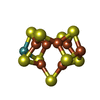

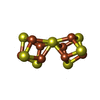

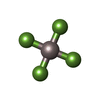


| #4: 化合物 | | #5: 化合物 | #6: 化合物 | #7: 化合物 | #8: 化合物 | ChemComp-MG / #9: 化合物 | ChemComp-ALF / #10: 化合物 | ChemComp-ADP / #11: 化合物 | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.8 Å3/Da / 溶媒含有率: 55.5 % | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | pH: 6.5 詳細: 16-20% PEG 8000, 0.1 M CACODYLATE PH 6.5 AND 20-50 MM MGCL2 | ||||||||||||||||||||||||
| 結晶化 | *PLUS 手法: batch method | ||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 120 K |
|---|---|
| 放射光源 | 由来:  回転陽極 / タイプ: RIGAKU RUH2R / 波長: 1.5418 回転陽極 / タイプ: RIGAKU RUH2R / 波長: 1.5418 |
| 検出器 | タイプ: RIGAKU / 検出器: IMAGE PLATE / 日付: 1996年4月1日 |
| 放射 | モノクロメーター: GRAPHITE(002) / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.5418 Å / 相対比: 1 |
| 反射 | 解像度: 3→50 Å / Num. obs: 57735 / % possible obs: 73.8 % / 冗長度: 1.8 % / Rsym value: 0.098 / Net I/σ(I): 9.8 |
| 反射 シェル | 解像度: 3→3.11 Å / Mean I/σ(I) obs: 2 / Rsym value: 0.245 / % possible all: 28.8 |
| 反射 | *PLUS Num. measured all: 104037 / Rmerge(I) obs: 0.098 |
| 反射 シェル | *PLUS % possible obs: 28.8 % / Rmerge(I) obs: 0.245 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: PDB ENTRY 1MIN  1min 解像度: 3→50 Å / Data cutoff high absF: 1000000 / Data cutoff low absF: 0 / Isotropic thermal model: ONE B-FACTOR PER RESIDUE / 交差検証法: THROUGHOUT / σ(F): 0
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 3→50 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Refine LS restraints NCS |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Xplor file |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ソフトウェア | *PLUS 名称:  X-PLOR / バージョン: 3.1 / 分類: refinement X-PLOR / バージョン: 3.1 / 分類: refinement | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 | *PLUS
|
 ムービー
ムービー コントローラー
コントローラー











 PDBj
PDBj