+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1hhx | ||||||
|---|---|---|---|---|---|---|---|
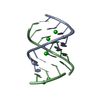
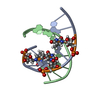
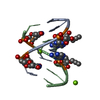
| タイトル | Solution structure of LNA3:RNA hybrid | ||||||
 要素 要素 |
| ||||||
 キーワード キーワード | ANTISENSE / LOCKED NUCLEIC ACID / LNA / RNA / HYBRID / RNASE H | ||||||
| 機能・相同性 | DNA/RNA hybrid / RNA 機能・相同性情報 機能・相同性情報 | ||||||
| 手法 | 溶液NMR / simulated annealing | ||||||
 データ登録者 データ登録者 | Petersen, M. / Bondensgaard, K. / Wengel, J. / Jacobsen, J.P. | ||||||
 引用 引用 |  ジャーナル: J.Am.Chem.Soc. / 年: 2002 ジャーナル: J.Am.Chem.Soc. / 年: 2002タイトル: Locked Nucleic Acid (Lna) Recognition of RNA: NMR Solution Structures of Lna:RNA Hybrids 著者: Petersen, M. / Bondensgaard, K. / Wengel, J. / Jacobsen, J.P. #1:  ジャーナル: Chemistry / 年: 2000 ジャーナル: Chemistry / 年: 2000タイトル: Structural Studies of Lna:RNA Duplexes by NMR: Conformations and Implications for Rnase H Activity. 著者: Bondensgaard, K. / Petersen, M. / Singh, S.K. / Rajwanshi, V.K. / Kumar, R. / Wengel, J. / Jacobsen, J.P. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1hhx.cif.gz 1hhx.cif.gz | 389.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1hhx.ent.gz pdb1hhx.ent.gz | 320.6 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1hhx.json.gz 1hhx.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  1hhx_validation.pdf.gz 1hhx_validation.pdf.gz | 339.2 KB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  1hhx_full_validation.pdf.gz 1hhx_full_validation.pdf.gz | 622.1 KB | 表示 | |
| XML形式データ |  1hhx_validation.xml.gz 1hhx_validation.xml.gz | 15.7 KB | 表示 | |
| CIF形式データ |  1hhx_validation.cif.gz 1hhx_validation.cif.gz | 26.9 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/hh/1hhx https://data.pdbj.org/pub/pdb/validation_reports/hh/1hhx ftp://data.pdbj.org/pub/pdb/validation_reports/hh/1hhx ftp://data.pdbj.org/pub/pdb/validation_reports/hh/1hhx | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| 1 |
| |||||||||
| NMR アンサンブル |
|
- 要素
要素
| #1: DNA/RNAハイブリッド | 分子量: 2814.843 Da / 分子数: 1 / 由来タイプ: 合成 |
|---|---|
| #2: RNA鎖 | 分子量: 2855.767 Da / 分子数: 1 / 由来タイプ: 合成 |
| 配列の詳細 | CHAIN A RESIDUES 2,5,7 ARE LOCKED NUCLEIC ACIDS OR (1R,3R,4R,7S)-7-HYDROXY-1-HYDROXYMETHYL-3- ...CHAIN A RESIDUES 2,5,7 ARE LOCKED NUCLEIC ACIDS OR (1R,3R,4R,7S)-7-HYDROXY-1-HYDROXYMET |
-実験情報
-実験
| 実験 | 手法: 溶液NMR |
|---|---|
| NMR実験 | タイプ: NOESY |
- 試料調製
試料調製
| 詳細 | 内容: 0.7E-3M LNA1:RNA, 0.1M NACL, 5E-5M EDTA AND 1E-2M PHOSPHATE BUFFER IN 100% D2O |
|---|---|
| 試料状態 | イオン強度: 0.1 / pH: 7 / 圧: 1 atm / 温度: 298 K |
| 結晶化 | *PLUS 手法: other / 詳細: NMR |
-NMR測定
| NMRスペクトロメーター | タイプ: Varian INOVA / 製造業者: Varian / モデル: INOVA / 磁場強度: 750 MHz |
|---|
- 解析
解析
| NMR software |
| |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 手法: simulated annealing / ソフトェア番号: 1 詳細: A TOTAL OF 423 NOE DISTANCE RESTRAINTS WERE OBTAINED FROM A FULL RELAXATION MATRIX ANALYSIS WITH THE PROGRAM RANDMARDI. A FURTHER 58 NOE DISTANCE RESTRAINTS WERE OBTAINED FROM NOESY IN H2O ...詳細: A TOTAL OF 423 NOE DISTANCE RESTRAINTS WERE OBTAINED FROM A FULL RELAXATION MATRIX ANALYSIS WITH THE PROGRAM RANDMARDI. A FURTHER 58 NOE DISTANCE RESTRAINTS WERE OBTAINED FROM NOESY IN H2O USING ISPA. 22 WATSON-CRICK BASE PAIRING RESTRAINTS. | |||||||||||||||
| NMRアンサンブル | コンフォーマー選択の基準: LOWEST ENERGY / 計算したコンフォーマーの数: 40 / 登録したコンフォーマーの数: 34 |
 ムービー
ムービー コントローラー
コントローラー







 PDBj
PDBj Amber
Amber