+ Open data
Open data
- Basic information
Basic information
| Entry | Database: PDB / ID: 1fhy | ||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Title | PSORALEN CROSS-LINKED D(CCGCTAGCGG) FORMS HOLLIDAY JUNCTION | ||||||||||||||||||
 Components Components | DNA (5'-D(* Keywords KeywordsDNA / psoralen / cross-linked DNA / Holliday junction / 4-way junction / DNA-drug complex | Function / homology | 4'-HYDROXYMETHYL-4,5',8-TRIMETHYLPSORALEN / DNA |  Function and homology information Function and homology informationMethod |  X-RAY DIFFRACTION / X-RAY DIFFRACTION /  SYNCHROTRON / SYNCHROTRON /  MOLECULAR REPLACEMENT / Resolution: 2.2 Å MOLECULAR REPLACEMENT / Resolution: 2.2 Å  Authors AuthorsEichman, B.F. / Mooers, B.H.M. / Alberti, M. / Hearst, J.E. / Ho, P.S. |  Citation Citation Journal: J.Mol.Biol. / Year: 2001 Journal: J.Mol.Biol. / Year: 2001Title: The crystal structures of psoralen cross-linked DNAs: drug-dependent formation of Holliday junctions. Authors: Eichman, B.F. / Mooers, B.H. / Alberti, M. / Hearst, J.E. / Ho, P.S. #1:  Journal: Proc.Natl.Acad.Sci.USA / Year: 2000 Journal: Proc.Natl.Acad.Sci.USA / Year: 2000Title: The Holliday junction in an inverted repeat DNA sequence: Sequence effects on the structure of four-way junctions Authors: Eichman, B.F. / Vargason, J.M. / Mooers, B.H.M. / Ho, P.S. History |
|
- Structure visualization
Structure visualization
| Structure viewer | Molecule:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- Downloads & links
Downloads & links
- Download
Download
| PDBx/mmCIF format |  1fhy.cif.gz 1fhy.cif.gz | 21.6 KB | Display |  PDBx/mmCIF format PDBx/mmCIF format |
|---|---|---|---|---|
| PDB format |  pdb1fhy.ent.gz pdb1fhy.ent.gz | 14.1 KB | Display |  PDB format PDB format |
| PDBx/mmJSON format |  1fhy.json.gz 1fhy.json.gz | Tree view |  PDBx/mmJSON format PDBx/mmJSON format | |
| Others |  Other downloads Other downloads |
-Validation report
| Arichive directory |  https://data.pdbj.org/pub/pdb/validation_reports/fh/1fhy https://data.pdbj.org/pub/pdb/validation_reports/fh/1fhy ftp://data.pdbj.org/pub/pdb/validation_reports/fh/1fhy ftp://data.pdbj.org/pub/pdb/validation_reports/fh/1fhy | HTTPS FTP |
|---|
-Related structure data
| Related structure data | 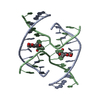 1fhzC C: citing same article ( |
|---|---|
| Similar structure data | |
| Other databases |
|
- Links
Links
- Assembly
Assembly
| Deposited unit | 
| ||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 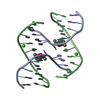
| ||||||||||
| Unit cell |
| ||||||||||
| Details | A four-way junction is a dimer constructed from chains A and B and a symmetry partner generated by the two-fold |
- Components
Components
| #1: DNA chain | Mass: 3045.993 Da / Num. of mol.: 2 / Source method: obtained synthetically / Details: DNA IS CROSS-LINKED BY PSORALEN #2: Chemical | ChemComp-PSO / | #3: Chemical | ChemComp-CA / | #4: Water | ChemComp-HOH / | |
|---|
-Experimental details
-Experiment
| Experiment | Method:  X-RAY DIFFRACTION / Number of used crystals: 1 X-RAY DIFFRACTION / Number of used crystals: 1 |
|---|
- Sample preparation
Sample preparation
| Crystal | Density Matthews: 2.23 Å3/Da / Density % sol: 44.9 % | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Crystal grow | Temperature: 277 K / Method: vapor diffusion, sitting drop / pH: 7 Details: sodium cacodylate, MgCl2, MPD, pH 7, VAPOR DIFFUSION, SITTING DROP, temperature 277K | ||||||||||||||||||||||||||||||||||||
| Components of the solutions |
| ||||||||||||||||||||||||||||||||||||
| Crystal grow | *PLUS Temperature: 4 ℃ / Method: vapor diffusion | ||||||||||||||||||||||||||||||||||||
| Components of the solutions | *PLUS
|
-Data collection
| Diffraction | Mean temperature: 298 K |
|---|---|
| Diffraction source | Source:  SYNCHROTRON / Site: SYNCHROTRON / Site:  ALS ALS  / Beamline: 5.0.2 / Wavelength: 1.1 / Beamline: 5.0.2 / Wavelength: 1.1 |
| Detector | Type: ADSC QUANTUM 4 / Detector: CCD / Date: Oct 8, 1999 |
| Radiation | Protocol: SINGLE WAVELENGTH / Monochromatic (M) / Laue (L): M / Scattering type: x-ray |
| Radiation wavelength | Wavelength: 1.1 Å / Relative weight: 1 |
| Reflection | Resolution: 2.2→34.65 Å / Num. all: 10418 / Num. obs: 2937 / % possible obs: 99.2 % / Observed criterion σ(I): -3 / Redundancy: 3.5 % / Rmerge(I) obs: 0.059 / Net I/σ(I): 16.9 |
| Reflection shell | Resolution: 2.2→2.28 Å / Redundancy: 3.6 % / Rmerge(I) obs: 0.08 / Num. unique all: 299 / % possible all: 99.3 |
| Reflection | *PLUS Num. measured all: 10418 |
| Reflection shell | *PLUS % possible obs: 99.3 % / Mean I/σ(I) obs: 8.2 |
- Processing
Processing
| Software |
| |||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Refinement | Method to determine structure:  MOLECULAR REPLACEMENT / Resolution: 2.2→34.65 Å / Cross valid method: THROUGHOUT / σ(F): 0 / σ(I): 0 / Stereochemistry target values: Parkinson et al. MOLECULAR REPLACEMENT / Resolution: 2.2→34.65 Å / Cross valid method: THROUGHOUT / σ(F): 0 / σ(I): 0 / Stereochemistry target values: Parkinson et al.Details: ANISOTROPIC B VALUES WERE APPLIED TO FCALC DURING REFINEMENT IN ORDER TO SCALE FCALC TO FOBS
| |||||||||||||||||||||||||
| Displacement parameters |
| |||||||||||||||||||||||||
| Refinement step | Cycle: LAST / Resolution: 2.2→34.65 Å
| |||||||||||||||||||||||||
| Refine LS restraints |
| |||||||||||||||||||||||||
| Software | *PLUS Name:  X-PLOR / Version: 3.851 / Classification: refinement X-PLOR / Version: 3.851 / Classification: refinement | |||||||||||||||||||||||||
| Refinement | *PLUS Lowest resolution: 34.7 Å / Rfactor Rfree: 0.283 | |||||||||||||||||||||||||
| Solvent computation | *PLUS | |||||||||||||||||||||||||
| Displacement parameters | *PLUS | |||||||||||||||||||||||||
| Refine LS restraints | *PLUS
|
 Movie
Movie Controller
Controller









 PDBj
PDBj