+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 1bda | ||||||
|---|---|---|---|---|---|---|---|
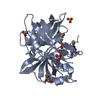
| タイトル | CATALYTIC DOMAIN OF HUMAN SINGLE CHAIN TISSUE PLASMINOGEN ACTIVATOR IN COMPLEX WITH DANSYL-EGR-CMK (DANSYL-GLU-GLY-ARG CHLOROMETHYL KETONE) | ||||||
 要素 要素 | SINGLE CHAIN TISSUE TYPE PLASMINOGEN ACTIVATOR | ||||||
 キーワード キーワード | HYDROLASE/HYDROLASE INHIBITOR / TRYPSIN LIKE SERINE PROTEASE / FIBRINOLYTIC ENZYMES / PLASMINOGEN ACTIVATORS / HYDROLASE-HYDROLASE INHIBITOR COMPLEX | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報t-plasminogen activator / prevention of polyspermy / trans-synaptic signaling by BDNF, modulating synaptic transmission / Signaling by PDGF / negative regulation of plasminogen activation / Dissolution of Fibrin Clot / smooth muscle cell migration / plasminogen activation / platelet-derived growth factor receptor signaling pathway / negative regulation of fibrinolysis ...t-plasminogen activator / prevention of polyspermy / trans-synaptic signaling by BDNF, modulating synaptic transmission / Signaling by PDGF / negative regulation of plasminogen activation / Dissolution of Fibrin Clot / smooth muscle cell migration / plasminogen activation / platelet-derived growth factor receptor signaling pathway / negative regulation of fibrinolysis / serine protease inhibitor complex / fibrinolysis / negative regulation of proteolysis / secretory granule / phosphoprotein binding / protein modification process / Schaffer collateral - CA1 synapse / apical part of cell / blood coagulation / response to hypoxia / signaling receptor binding / serine-type endopeptidase activity / glutamatergic synapse / cell surface / proteolysis / extracellular space / extracellular exosome / extracellular region / cytoplasm 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 |  X線回折 / X線回折 /  分子置換 / 解像度: 3.35 Å 分子置換 / 解像度: 3.35 Å | ||||||
 データ登録者 データ登録者 | Bode, W. / Renatus, M. / Engh, R.A. | ||||||
 引用 引用 |  ジャーナル: EMBO J. / 年: 1997 ジャーナル: EMBO J. / 年: 1997タイトル: Lysine 156 promotes the anomalous proenzyme activity of tPA: X-ray crystal structure of single-chain human tPA. 著者: Renatus, M. / Engh, R.A. / Stubbs, M.T. / Huber, R. / Fischer, S. / Kohnert, U. / Bode, W. #1:  ジャーナル: Biochemistry / 年: 1997 ジャーナル: Biochemistry / 年: 1997タイトル: Catalytic Domain Structure of Vampire Bat Plasminogen Activator: A Molecular Paradigm for Proteolysis without Activation Cleavage 著者: Renatus, M. / Stubbs, M.T. / Huber, R. / Bringmann, P. / Donner, P. / Schleuning, W.D. / Bode, W. #2:  ジャーナル: J.Mol.Biol. / 年: 1996 ジャーナル: J.Mol.Biol. / 年: 1996タイトル: The 2.3 A Crystal Structure of the Catalytic Domain of Recombinant Two-Chain Human Tissue-Type Plasminogen Activator 著者: Lamba, D. / Bauer, M. / Huber, R. / Fischer, S. / Rudolph, R. / Kohnert, U. / Bode, W. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  1bda.cif.gz 1bda.cif.gz | 119.5 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb1bda.ent.gz pdb1bda.ent.gz | 92.4 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  1bda.json.gz 1bda.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/bd/1bda https://data.pdbj.org/pub/pdb/validation_reports/bd/1bda ftp://data.pdbj.org/pub/pdb/validation_reports/bd/1bda ftp://data.pdbj.org/pub/pdb/validation_reports/bd/1bda | HTTPS FTP |
|---|
-関連構造データ
| 関連構造データ |  1rtfS S: 精密化の開始モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
| ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 1 | 
| ||||||||||||
| 2 | 
| ||||||||||||
| 単位格子 |
| ||||||||||||
| 非結晶学的対称性 (NCS) | NCS oper:
|
- 要素
要素
| #1: タンパク質 | 分子量: 29725.654 Da / 分子数: 2 / 断片: UNP residues 298-562 / 変異: DELETION MUTANT / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 発現宿主: Homo sapiens (ヒト) / 発現宿主:  #2: 化合物 | #3: 水 | ChemComp-HOH / | Has protein modification | Y | 非ポリマーの詳細 | THE UNBOUND FORM OF THE INHIBITOR IS DANSYL-GLU-GLY-ARG-CMK-CHLOROMETHYLKETONE. UPON REACTION WITH ...THE UNBOUND FORM OF THE INHIBITOR IS DANSYL-GLU-GLY-ARG-CMK-CHLOROMETH | |
|---|
-実験情報
-実験
| 実験 | 手法:  X線回折 / 使用した結晶の数: 1 X線回折 / 使用した結晶の数: 1 |
|---|
- 試料調製
試料調製
| 結晶 | マシュー密度: 2.36 Å3/Da / 溶媒含有率: 48 % | ||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 結晶化 | pH: 8.2 / 詳細: pH 8.2 | ||||||||||||||||||||||||||||||||||||||||||
| 結晶 | *PLUS 溶媒含有率: 50 % | ||||||||||||||||||||||||||||||||||||||||||
| 結晶化 | *PLUS 温度: 23 ℃ / 手法: 蒸気拡散法, シッティングドロップ法 | ||||||||||||||||||||||||||||||||||||||||||
| 溶液の組成 | *PLUS
|
-データ収集
| 回折 | 平均測定温度: 290 K |
|---|---|
| 放射光源 | 由来:  回転陽極 / タイプ: RIGAKU RUH2R / 波長: 1.5418 回転陽極 / タイプ: RIGAKU RUH2R / 波長: 1.5418 |
| 検出器 | タイプ: MARRESEARCH / 検出器: IMAGE PLATE / 日付: 1996年6月13日 |
| 放射 | モノクロメーター: GRAPHITE(002) / 単色(M)・ラウエ(L): M / 散乱光タイプ: x-ray |
| 放射波長 | 波長: 1.5418 Å / 相対比: 1 |
| 反射 | 解像度: 3.1→25 Å / Num. obs: 9414 / % possible obs: 86.7 % / Observed criterion σ(I): 2 / 冗長度: 2.9 % / Rmerge(I) obs: 0.147 / Net I/σ(I): 3.6 |
| 反射 シェル | 解像度: 3.1→3.18 Å / 冗長度: 1.7 % / Rmerge(I) obs: 0.63 / Mean I/σ(I) obs: 1.2 / % possible all: 55.2 |
| 反射 | *PLUS Num. measured all: 27265 |
| 反射 シェル | *PLUS % possible obs: 55.2 % / Rmerge(I) obs: 0.63 |
- 解析
解析
| ソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 精密化 | 構造決定の手法:  分子置換 分子置換開始モデル: 1RTF 解像度: 3.35→7 Å / Data cutoff high absF: 100000 / Data cutoff low absF: 0.25 / Isotropic thermal model: RESTRAINED / 交差検証法: NO FREE R-FACTOR / σ(F): 2 /
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 26.1 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: LAST / 解像度: 3.35→7 Å
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| LS精密化 シェル | 解像度: 3.25→3.35 Å / Total num. of bins used: 10 /
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| Xplor file |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ソフトウェア | *PLUS 名称:  X-PLOR / バージョン: 3.851 / 分類: refinement X-PLOR / バージョン: 3.851 / 分類: refinement | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | *PLUS Rfactor obs: 0.2037 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | *PLUS | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 | *PLUS
|
 ムービー
ムービー コントローラー
コントローラー












 PDBj
PDBj