+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-7459 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure at 3.8 A resolution of vaccine-elicited antibody vFP20.01 in complex with HIV-1 Env BG505 DS-SOSIP, and antibodies VRC03 and PGT122 | |||||||||
 マップデータ マップデータ | primary map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | HIV-1 Env / BG505 SOSIP / fusion peptide / VRC03 / PGT122 / vFP20.01 / VIRAL PROTEIN | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / viral protein processing / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / host cell plasma membrane ...positive regulation of plasma membrane raft polarization / positive regulation of receptor clustering / host cell endosome membrane / clathrin-dependent endocytosis of virus by host cell / viral protein processing / fusion of virus membrane with host plasma membrane / fusion of virus membrane with host endosome membrane / viral envelope / virion attachment to host cell / host cell plasma membrane / virion membrane / structural molecule activity / membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) / Homo sapiens (ヒト) /   Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) Human immunodeficiency virus 1 (ヒト免疫不全ウイルス) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.8 Å | |||||||||
 データ登録者 データ登録者 | Acharya P / Carragher B / Potter CS / Kwong PD | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Med / 年: 2018 ジャーナル: Nat Med / 年: 2018タイトル: Epitope-based vaccine design yields fusion peptide-directed antibodies that neutralize diverse strains of HIV-1. 著者: Kai Xu / Priyamvada Acharya / Rui Kong / Cheng Cheng / Gwo-Yu Chuang / Kevin Liu / Mark K Louder / Sijy O'Dell / Reda Rawi / Mallika Sastry / Chen-Hsiang Shen / Baoshan Zhang / Tongqing Zhou ...著者: Kai Xu / Priyamvada Acharya / Rui Kong / Cheng Cheng / Gwo-Yu Chuang / Kevin Liu / Mark K Louder / Sijy O'Dell / Reda Rawi / Mallika Sastry / Chen-Hsiang Shen / Baoshan Zhang / Tongqing Zhou / Mangaiarkarasi Asokan / Robert T Bailer / Michael Chambers / Xuejun Chen / Chang W Choi / Venkata P Dandey / Nicole A Doria-Rose / Aliaksandr Druz / Edward T Eng / S Katie Farney / Kathryn E Foulds / Hui Geng / Ivelin S Georgiev / Jason Gorman / Kurt R Hill / Alexander J Jafari / Young D Kwon / Yen-Ting Lai / Thomas Lemmin / Krisha McKee / Tiffany Y Ohr / Li Ou / Dongjun Peng / Ariana P Rowshan / Zizhang Sheng / John-Paul Todd / Yaroslav Tsybovsky / Elise G Viox / Yiran Wang / Hui Wei / Yongping Yang / Amy F Zhou / Rui Chen / Lu Yang / Diana G Scorpio / Adrian B McDermott / Lawrence Shapiro / Bridget Carragher / Clinton S Potter / John R Mascola / Peter D Kwong /  要旨: A central goal of HIV-1 vaccine research is the elicitation of antibodies capable of neutralizing diverse primary isolates of HIV-1. Here we show that focusing the immune response to exposed N- ...A central goal of HIV-1 vaccine research is the elicitation of antibodies capable of neutralizing diverse primary isolates of HIV-1. Here we show that focusing the immune response to exposed N-terminal residues of the fusion peptide, a critical component of the viral entry machinery and the epitope of antibodies elicited by HIV-1 infection, through immunization with fusion peptide-coupled carriers and prefusion stabilized envelope trimers, induces cross-clade neutralizing responses. In mice, these immunogens elicited monoclonal antibodies capable of neutralizing up to 31% of a cross-clade panel of 208 HIV-1 strains. Crystal and cryoelectron microscopy structures of these antibodies revealed fusion peptide conformational diversity as a molecular explanation for the cross-clade neutralization. Immunization of guinea pigs and rhesus macaques induced similarly broad fusion peptide-directed neutralizing responses, suggesting translatability. The N terminus of the HIV-1 fusion peptide is thus a promising target of vaccine efforts aimed at eliciting broadly neutralizing antibodies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_7459.map.gz emd_7459.map.gz | 203.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-7459-v30.xml emd-7459-v30.xml emd-7459.xml emd-7459.xml | 33.7 KB 33.7 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
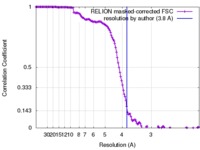
| FSC (解像度算出) |  emd_7459_fsc.xml emd_7459_fsc.xml | 13.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_7459.png emd_7459.png | 128.9 KB | ||
| マスクデータ |  emd_7459_msk_1.map emd_7459_msk_1.map emd_7459_msk_2.map emd_7459_msk_2.map | 216 MB 216 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-7459.cif.gz emd-7459.cif.gz | 7.9 KB | ||
| その他 |  emd_7459_additional_1.map.gz emd_7459_additional_1.map.gz emd_7459_additional_2.map.gz emd_7459_additional_2.map.gz emd_7459_additional_3.map.gz emd_7459_additional_3.map.gz emd_7459_additional_4.map.gz emd_7459_additional_4.map.gz | 107.8 MB 20.3 MB 13.9 MB 20.3 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-7459 http://ftp.pdbj.org/pub/emdb/structures/EMD-7459 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7459 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7459 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_7459_validation.pdf.gz emd_7459_validation.pdf.gz | 630.2 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_7459_full_validation.pdf.gz emd_7459_full_validation.pdf.gz | 629.8 KB | 表示 | |
| XML形式データ |  emd_7459_validation.xml.gz emd_7459_validation.xml.gz | 13.9 KB | 表示 | |
| CIF形式データ |  emd_7459_validation.cif.gz emd_7459_validation.cif.gz | 18.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7459 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7459 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7459 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7459 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6cdeMC  7460C  8420C  8421C  8422C  5tkjC  5tkkC  6cdiC  6cdmC  6cdoC  6cdpC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_7459.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_7459.map.gz / 形式: CCP4 / 大きさ: 216 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | primary map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.06 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
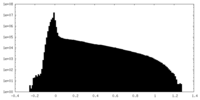
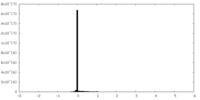
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_7459_msk_1.map emd_7459_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
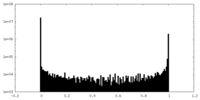
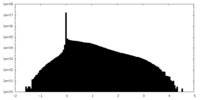
| 密度ヒストグラム |
-マスク #2
| ファイル |  emd_7459_msk_2.map emd_7459_msk_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: additional map #1
| ファイル | emd_7459_additional_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | additional map #1 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
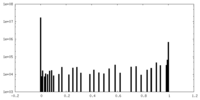
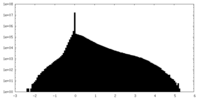
| 密度ヒストグラム |
-追加マップ: additional map #2
| ファイル | emd_7459_additional_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | additional map #2 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-追加マップ: additional map #3
| ファイル | emd_7459_additional_3.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | additional map #3 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
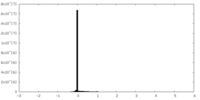
| 密度ヒストグラム |
-追加マップ: additional map #4
| ファイル | emd_7459_additional_4.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | additional map #4 | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : vFP20.01-BG505 DS-SOSIP-VRC03-PGT122
+超分子 #1: vFP20.01-BG505 DS-SOSIP-VRC03-PGT122
+超分子 #2: PGT122
+超分子 #3: VRC03
+超分子 #4: Glycoprotein
+超分子 #5: vFP20.01
+分子 #1: vFP20.01 Heavy Chain
+分子 #2: vFP20.01 Light chain
+分子 #3: PGT122 Heavy chain
+分子 #4: PGT122 Light Chain
+分子 #5: VRC03 Light Chain
+分子 #6: VRC03 Heavy Chain
+分子 #7: Glycoprotein 41
+分子 #8: Glycoprotein 120
+分子 #18: 2-acetamido-2-deoxy-beta-D-glucopyranose
+分子 #19: alpha-D-mannopyranose
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.5 mg/mL |
|---|---|
| 緩衝液 | pH: 7 |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - 画像ごとのフレーム数: 1-40 / 撮影したグリッド数: 1 / 実像数: 723 / 平均電子線量: 70.7 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 最大 デフォーカス(補正後): -2.8000000000000003 µm 最小 デフォーカス(補正後): -1.8 µm / 倍率(補正後): 130000 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: FLEXIBLE FIT / 温度因子: 107 / 当てはまり具合の基準: Correlation Coefficient |
|---|---|
| 得られたモデル |  PDB-6cde: |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)