+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-6571 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The cryo-EM structure of yeast spliceosomal U4/U6.U5 tri-snRNP (improved map for U5 Sm ring region at 4.7 A) | |||||||||
 マップデータ マップデータ | Reconstruction of tri-snRNP | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | tri-snRNP / pre-mRNA splicing | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報spliceosomal conformational changes to generate catalytic conformation / mRNA decay by 5' to 3' exoribonuclease / snoRNA splicing / Lsm1-7-Pat1 complex / U6 snRNP / snoRNA guided rRNA 2'-O-methylation / deadenylation-dependent decapping of nuclear-transcribed mRNA / generation of catalytic spliceosome for first transesterification step / box C/D sno(s)RNA 3'-end processing / spliceosome conformational change to release U4 (or U4atac) and U1 (or U11) ...spliceosomal conformational changes to generate catalytic conformation / mRNA decay by 5' to 3' exoribonuclease / snoRNA splicing / Lsm1-7-Pat1 complex / U6 snRNP / snoRNA guided rRNA 2'-O-methylation / deadenylation-dependent decapping of nuclear-transcribed mRNA / generation of catalytic spliceosome for first transesterification step / box C/D sno(s)RNA 3'-end processing / spliceosome conformational change to release U4 (or U4atac) and U1 (or U11) / box C/D methylation guide snoRNP complex / U4/U6 snRNP / 7-methylguanosine cap hypermethylation / pICln-Sm protein complex / snRNP binding / small nuclear ribonucleoprotein complex / sno(s)RNA-containing ribonucleoprotein complex / splicing factor binding / SMN-Sm protein complex / spliceosomal tri-snRNP complex / U4 snRNA binding / commitment complex / U2-type prespliceosome assembly / U2-type catalytic step 2 spliceosome / P-body assembly / U2 snRNP / U1 snRNP / U4 snRNP / poly(U) RNA binding / U2-type prespliceosome / U3 snoRNA binding / tRNA processing / precatalytic spliceosome / generation of catalytic spliceosome for second transesterification step / Major pathway of rRNA processing in the nucleolus and cytosol / mRNA 5'-splice site recognition / spliceosomal complex assembly / mRNA 3'-splice site recognition / nuclear-transcribed mRNA catabolic process / spliceosomal tri-snRNP complex assembly / Prp19 complex / U5 snRNA binding / U5 snRNP / U2 snRNA binding / U6 snRNA binding / pre-mRNA intronic binding / spliceosomal snRNP assembly / U1 snRNA binding / cellular response to glucose starvation / U4/U6 x U5 tri-snRNP complex / catalytic step 2 spliceosome / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of SSU-rRNA / spliceosomal complex / small-subunit processome / P-body / mRNA splicing, via spliceosome / metallopeptidase activity / rRNA processing / nucleic acid binding / RNA helicase activity / RNA helicase / GTPase activity / mRNA binding / GTP binding / nucleolus / ATP hydrolysis activity / mitochondrion / RNA binding / nucleoplasm / ATP binding / identical protein binding / nucleus / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.7 Å | |||||||||
 データ登録者 データ登録者 | Wan R / Yan C / Bai R / Wang L / Huang M / Wong C / Shi Y | |||||||||
 引用 引用 |  ジャーナル: Science / 年: 2016 ジャーナル: Science / 年: 2016タイトル: The 3.8 Å structure of the U4/U6.U5 tri-snRNP: Insights into spliceosome assembly and catalysis. 著者: Ruixue Wan / Chuangye Yan / Rui Bai / Lin Wang / Min Huang / Catherine C L Wong / Yigong Shi /  要旨: Splicing of precursor messenger RNA is accomplished by a dynamic megacomplex known as the spliceosome. Assembly of a functional spliceosome requires a preassembled U4/U6.U5 tri-snRNP complex, which ...Splicing of precursor messenger RNA is accomplished by a dynamic megacomplex known as the spliceosome. Assembly of a functional spliceosome requires a preassembled U4/U6.U5 tri-snRNP complex, which comprises the U5 small nuclear ribonucleoprotein (snRNP), the U4 and U6 small nuclear RNA (snRNA) duplex, and a number of protein factors. Here we report the three-dimensional structure of a Saccharomyces cerevisiae U4/U6.U5 tri-snRNP at an overall resolution of 3.8 angstroms by single-particle electron cryomicroscopy. The local resolution for the core regions of the tri-snRNP reaches 3.0 to 3.5 angstroms, allowing construction of a refined atomic model. Our structure contains U5 snRNA, the extensively base-paired U4/U6 snRNA, and 30 proteins including Prp8 and Snu114, which amount to 8495 amino acids and 263 nucleotides with a combined molecular mass of ~1 megadalton. The catalytic nucleotide U80 from U6 snRNA exists in an inactive conformation, stabilized by its base-pairing interactions with U4 snRNA and protected by Prp3. Pre-messenger RNA is bound in the tri-snRNP through base-pairing interactions with U6 snRNA and loop I of U5 snRNA. This structure, together with that of the spliceosome, reveals the molecular choreography of the snRNAs in the activation process of the spliceosomal ribozyme. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_6571.map.gz emd_6571.map.gz | 116.3 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-6571-v30.xml emd-6571-v30.xml emd-6571.xml emd-6571.xml | 10.1 KB 10.1 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  400_6571.gif 400_6571.gif 80_6571.gif 80_6571.gif | 58.3 KB 3.8 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-6571 http://ftp.pdbj.org/pub/emdb/structures/EMD-6571 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6571 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6571 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  3jcmMC  6561C  6562C  6563C  6564C  6565C  6566C  6567C  6568C  6569C  6570C  6572C  6573C C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_6571.map.gz / 形式: CCP4 / 大きさ: 122.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_6571.map.gz / 形式: CCP4 / 大きさ: 122.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Reconstruction of tri-snRNP | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.32 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
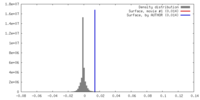
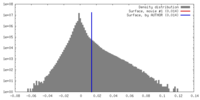
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : U4/U6.U5 tri-snRNP from Saccharomyces cerevisiae
| 全体 | 名称: U4/U6.U5 tri-snRNP from Saccharomyces cerevisiae |
|---|---|
| 要素 |
|
-超分子 #1000: U4/U6.U5 tri-snRNP from Saccharomyces cerevisiae
| 超分子 | 名称: U4/U6.U5 tri-snRNP from Saccharomyces cerevisiae / タイプ: sample / ID: 1000 / Number unique components: 34 |
|---|
-超分子 #1: U4/U6.U5 tri-snRNP
| 超分子 | 名称: U4/U6.U5 tri-snRNP / タイプ: organelle_or_cellular_component / ID: 1 / 組換発現: No / データベース: NCBI |
|---|---|
| 由来(天然) | 生物種:  |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 凍結 | 凍結剤: ETHANE / 装置: FEI VITROBOT MARK IV |
|---|
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 日付 | 2015年8月8日 |
| 撮影 | カテゴリ: FILM フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) デジタル化 - スキャナー: TEMSCAN / 実像数: 3141 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 4.7 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: RELION / 使用した粒子像数: 75799 |
|---|
 ムービー
ムービー コントローラー
コントローラー



























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)