+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-6465 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | The Architecture of a Eukaryotic Replisome | |||||||||
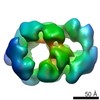
 マップデータ マップデータ | Yeast CMGE complex | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Eukaryotic replisome / CMGE / Electron microscopy | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / ネガティブ染色法 / 解像度: 16.0 Å | |||||||||
 データ登録者 データ登録者 | Sun J / Shi Y / Georgescu RE / Yuan Z / Chait B / Li H / O'Donnell ME | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2015 ジャーナル: Nat Struct Mol Biol / 年: 2015タイトル: The architecture of a eukaryotic replisome. 著者: Jingchuan Sun / Yi Shi / Roxana E Georgescu / Zuanning Yuan / Brian T Chait / Huilin Li / Michael E O'Donnell /  要旨: At the eukaryotic DNA replication fork, it is widely believed that the Cdc45-Mcm2-7-GINS (CMG) helicase is positioned in front to unwind DNA and that DNA polymerases trail behind the helicase. Here ...At the eukaryotic DNA replication fork, it is widely believed that the Cdc45-Mcm2-7-GINS (CMG) helicase is positioned in front to unwind DNA and that DNA polymerases trail behind the helicase. Here we used single-particle EM to directly image a Saccharomyces cerevisiae replisome. Contrary to expectations, the leading strand Pol ɛ is positioned ahead of CMG helicase, whereas Ctf4 and the lagging-strand polymerase (Pol) α-primase are behind the helicase. This unexpected architecture indicates that the leading-strand DNA travels a long distance before reaching Pol ɛ, first threading through the Mcm2-7 ring and then making a U-turn at the bottom and reaching Pol ɛ at the top of CMG. Our work reveals an unexpected configuration of the eukaryotic replisome, suggests possible reasons for this architecture and provides a basis for further structural and biochemical replisome studies. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_6465.map.gz emd_6465.map.gz | 58.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-6465-v30.xml emd-6465-v30.xml emd-6465.xml emd-6465.xml | 9.3 KB 9.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_6465.jpg emd_6465.jpg | 21.5 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-6465 http://ftp.pdbj.org/pub/emdb/structures/EMD-6465 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6465 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-6465 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_6465_validation.pdf.gz emd_6465_validation.pdf.gz | 79.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_6465_full_validation.pdf.gz emd_6465_full_validation.pdf.gz | 78.2 KB | 表示 | |
| XML形式データ |  emd_6465_validation.xml.gz emd_6465_validation.xml.gz | 494 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-6465 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-6465 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-6465 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-6465 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_6465.map.gz / 形式: CCP4 / 大きさ: 62.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_6465.map.gz / 形式: CCP4 / 大きさ: 62.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Yeast CMGE complex | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.12 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Saccharomyces cerevisiae CMGE complex
| 全体 | 名称: Saccharomyces cerevisiae CMGE complex |
|---|---|
| 要素 |
|
-超分子 #1000: Saccharomyces cerevisiae CMGE complex
| 超分子 | 名称: Saccharomyces cerevisiae CMGE complex / タイプ: sample / ID: 1000 / Number unique components: 2 |
|---|---|
| 分子量 | 理論値: 1.2 MDa |
-分子 #1: CMG complex
| 分子 | 名称: CMG complex / タイプ: protein_or_peptide / ID: 1 / Name.synonym: CMG / コピー数: 1 / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 700 KDa |
| 組換発現 | 生物種:  |
-分子 #2: Polymerase Epsilon
| 分子 | 名称: Polymerase Epsilon / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 500 KDa |
| 組換発現 | 生物種:  |
-実験情報
-構造解析
| 手法 | ネガティブ染色法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.5 mg/mL |
|---|---|
| 緩衝液 | 詳細: 20 mM Tris-acetate, 40 mM potassium glutamate, 2 mM DTT, 0.1 mM EDTA |
| 染色 | タイプ: NEGATIVE 詳細: Grids were stained with 1% w/v uranyl acetate for 1 minute. |
| 凍結 | 凍結剤: NONE / 装置: OTHER |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL 2010F |
|---|---|
| 日付 | 2014年9月10日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: GATAN ULTRASCAN 4000 (4k x 4k) 実像数: 320 / 平均電子線量: 20 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / 倍率(公称値): 50000 |
| 試料ステージ | 試料ホルダーモデル: GATAN LIQUID NITROGEN |
- 画像解析
画像解析
| 詳細 | Particles were selected in EMAN 2.1 using SWAM. |
|---|---|
| CTF補正 | 詳細: CTFFIND3 |
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 16.0 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: Relion_1.3 / 使用した粒子像数: 18721 |
 ムービー
ムービー コントローラー
コントローラー










 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















