登録情報 データベース : EMDB / ID : EMD-63324タイトル Cryo-EM structure of the histamine H1 receptor-Gs protein complex 複合体 : Histamine H1 receptor-Gs protein complexタンパク質・ペプチド : Guanine nucleotide-binding protein G(s) subunit alpha isoforms shortタンパク質・ペプチド : Guanine nucleotide-binding protein G(I)/G(S)/G(T) subunit beta-1タンパク質・ペプチド : Guanine nucleotide-binding protein G(I)/G(S)/G(O) subunit gamma-2タンパク質・ペプチド : nanobody 35タンパク質・ペプチド : Histamine H1 receptor,Genome polyproteinリガンド : HISTAMINE / / / / / 機能・相同性 分子機能 ドメイン・相同性 構成要素
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Homo sapiens (ヒト) / Rattus norvegicus (ドブネズミ) / Bos taurus (ウシ) / unidentified (未定義) 手法 / / 解像度 : 2.77 Å Matsuzaki Y / Sano FK / Oshima HS / Akasaka H / Kobayashi K / Tanaka T / Itoh Y / Shihoya W / Kise Y / Kusakizako T / Nureki O 資金援助 Organization Grant number 国 Japan Society for the Promotion of Science (JSPS)
ジャーナル : Commun Biol / 年 : 2025タイトル : Structural insights into ligand recognition and G protein preferences across histamine receptors.著者 : Yuma Matsuzaki / Fumiya K Sano / Hidetaka S Oshima / Hiroaki Akasaka / Kazuhiro Kobayashi / Tatsuki Tanaka / Yuzuru Itoh / Wataru Shihoya / Yoshiaki Kise / Tsukasa Kusakizako / Asuka Inoue / Osamu Nureki / 要旨 : Histamine exerts critical physiological roles by activating four receptor subtypes, each exhibiting a specific G protein preference. Among these, the histamine H receptor (HR) modulates chemotaxis ... Histamine exerts critical physiological roles by activating four receptor subtypes, each exhibiting a specific G protein preference. Among these, the histamine H receptor (HR) modulates chemotaxis and interferon production through G protein activation, suggesting its therapeutic potential. Despite its physiological significance, the mechanisms underlying HR signalling and G protein preference across histamine receptors remain poorly understood. Here, we present the cryo-electron microscopy structure of the HR-G complex, revealing unique mechanisms of histamine recognition and receptor activation. We further solved the structures of the histamine H receptor (HR) bound to the non-canonical G proteins G and G. Through a combination of functional and computational analyses, we identified the intracellular loop 2 as a critical determinant of G protein preference in HR and HR. Collectively, our comprehensive study revealed the structural basis for distinct mechanisms of ligand recognition and receptor activation, offering a profound insight into G protein preference across receptor subtypes. 履歴 登録 2025年1月30日 - ヘッダ(付随情報) 公開 2025年6月11日 - マップ公開 2025年6月11日 - 更新 2025年7月23日 - 現状 2025年7月23日 処理サイト : PDBj / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報
 マップデータ
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報 Homo sapiens (ヒト) /
Homo sapiens (ヒト) / 

 データ登録者
データ登録者 日本, 1件
日本, 1件  引用
引用 ジャーナル: Commun Biol / 年: 2025
ジャーナル: Commun Biol / 年: 2025
 構造の表示
構造の表示 ダウンロードとリンク
ダウンロードとリンク emd_63324.map.gz
emd_63324.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-63324-v30.xml
emd-63324-v30.xml emd-63324.xml
emd-63324.xml EMDBヘッダ
EMDBヘッダ emd_63324.png
emd_63324.png emd_63324_msk_1.map
emd_63324_msk_1.map マスクマップ
マスクマップ emd-63324.cif.gz
emd-63324.cif.gz emd_63324_half_map_1.map.gz
emd_63324_half_map_1.map.gz emd_63324_half_map_2.map.gz
emd_63324_half_map_2.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-63324
http://ftp.pdbj.org/pub/emdb/structures/EMD-63324 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-63324
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-63324 emd_63324_validation.pdf.gz
emd_63324_validation.pdf.gz EMDB検証レポート
EMDB検証レポート emd_63324_full_validation.pdf.gz
emd_63324_full_validation.pdf.gz emd_63324_validation.xml.gz
emd_63324_validation.xml.gz emd_63324_validation.cif.gz
emd_63324_validation.cif.gz https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-63324
https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-63324 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-63324
ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-63324 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_63324.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_63324.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) emd_63324_msk_1.map
emd_63324_msk_1.map 試料の構成要素
試料の構成要素 Homo sapiens (ヒト)
Homo sapiens (ヒト) Homo sapiens (ヒト)
Homo sapiens (ヒト)





 Homo sapiens (ヒト)
Homo sapiens (ヒト) Homo sapiens (ヒト)
Homo sapiens (ヒト)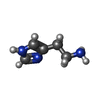
 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN
 ムービー
ムービー コントローラー
コントローラー






























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)













































