+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of human band 3-protein 4.2 complex in vertical conformation | |||||||||
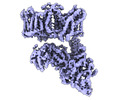
 マップデータ マップデータ | band 3-protein 4.2 complex in vertical conformation | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Red blood cell / Ankyrin complex / membrane protein / band 3 / protein 4.2 | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報hemoglobin metabolic process / protein-glutamine gamma-glutamyltransferase activity / pH elevation / Defective SLC4A1 causes hereditary spherocytosis type 4 (HSP4), distal renal tubular acidosis (dRTA) and dRTA with hemolytic anemia (dRTA-HA) / negative regulation of urine volume / Bicarbonate transporters / intracellular monoatomic ion homeostasis / ankyrin-1 complex / monoatomic anion transmembrane transporter activity / plasma membrane phospholipid scrambling ...hemoglobin metabolic process / protein-glutamine gamma-glutamyltransferase activity / pH elevation / Defective SLC4A1 causes hereditary spherocytosis type 4 (HSP4), distal renal tubular acidosis (dRTA) and dRTA with hemolytic anemia (dRTA-HA) / negative regulation of urine volume / Bicarbonate transporters / intracellular monoatomic ion homeostasis / ankyrin-1 complex / monoatomic anion transmembrane transporter activity / plasma membrane phospholipid scrambling / chloride:bicarbonate antiporter activity / solute:inorganic anion antiporter activity / bicarbonate transport / bicarbonate transmembrane transporter activity / monoatomic anion transport / chloride transport / chloride transmembrane transporter activity / ankyrin binding / hemoglobin binding / erythrocyte maturation / negative regulation of glycolytic process through fructose-6-phosphate / erythrocyte development / cortical cytoskeleton / spleen development / protein-membrane adaptor activity / chloride transmembrane transport / regulation of intracellular pH / protein localization to plasma membrane / Erythrocytes take up oxygen and release carbon dioxide / Erythrocytes take up carbon dioxide and release oxygen / structural constituent of cytoskeleton / multicellular organismal-level iron ion homeostasis / transmembrane transport / cytoplasmic side of plasma membrane / Z disc / cell morphogenesis / blood coagulation / regulation of cell shape / blood microparticle / basolateral plasma membrane / cytoskeleton / protein homodimerization activity / extracellular exosome / ATP binding / membrane / plasma membrane 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.6 Å | |||||||||
 データ登録者 データ登録者 | Xia X / Liu SH | |||||||||
| 資金援助 |  米国, 1件 米国, 1件
| |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2022 ジャーナル: Nat Struct Mol Biol / 年: 2022タイトル: Structure, dynamics and assembly of the ankyrin complex on human red blood cell membrane. 著者: Xian Xia / Shiheng Liu / Z Hong Zhou /  要旨: The cytoskeleton of a red blood cell (RBC) is anchored to the cell membrane by the ankyrin complex. This complex is assembled during RBC genesis and comprises primarily band 3, protein 4.2 and ...The cytoskeleton of a red blood cell (RBC) is anchored to the cell membrane by the ankyrin complex. This complex is assembled during RBC genesis and comprises primarily band 3, protein 4.2 and ankyrin, whose mutations contribute to numerous human inherited diseases. High-resolution structures of the ankyrin complex have been long sought-after to understand its assembly and disease-causing mutations. Here, we analyzed native complexes on the human RBC membrane by stepwise fractionation. Cryo-electron microscopy structures of nine band-3-associated complexes reveal that protein 4.2 stabilizes the cytoplasmic domain of band 3 dimer. In turn, the superhelix-shaped ankyrin binds to this protein 4.2 via ankyrin repeats (ARs) 6-13 and to another band 3 dimer via ARs 17-20, bridging two band 3 dimers in the ankyrin complex. Integration of these structures with both prior data and our biochemical data supports a model of ankyrin complex assembly during erythropoiesis and identifies interactions essential for the mechanical stability of RBC. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_26146.map.gz emd_26146.map.gz | 116.4 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-26146-v30.xml emd-26146-v30.xml emd-26146.xml emd-26146.xml | 16.2 KB 16.2 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_26146.png emd_26146.png | 103.3 KB | ||
| Filedesc metadata |  emd-26146.cif.gz emd-26146.cif.gz | 6.4 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-26146 http://ftp.pdbj.org/pub/emdb/structures/EMD-26146 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26146 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-26146 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_26146_validation.pdf.gz emd_26146_validation.pdf.gz | 612.4 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_26146_full_validation.pdf.gz emd_26146_full_validation.pdf.gz | 611.9 KB | 表示 | |
| XML形式データ |  emd_26146_validation.xml.gz emd_26146_validation.xml.gz | 6.3 KB | 表示 | |
| CIF形式データ |  emd_26146_validation.cif.gz emd_26146_validation.cif.gz | 7.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26146 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26146 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26146 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-26146 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  7tw0MC  7tvzC  7tw1C  7tw2C  7tw3C  7tw5C  7tw6C C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_26146.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_26146.map.gz / 形式: CCP4 / 大きさ: 125 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | band 3-protein 4.2 complex in vertical conformation | ||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : High-salt fraction 1 from human red blood cell membrane
| 全体 | 名称: High-salt fraction 1 from human red blood cell membrane |
|---|---|
| 要素 |
|
-超分子 #1: High-salt fraction 1 from human red blood cell membrane
| 超分子 | 名称: High-salt fraction 1 from human red blood cell membrane タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 280 KDa |
-分子 #1: Band 3 anion transport protein
| 分子 | 名称: Band 3 anion transport protein / タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 101.883859 KDa |
| 配列 | 文字列: MEELQDDYED MMEENLEQEE YEDPDIPESQ MEEPAAHDTE ATATDYHTTS HPGTHKVYVE LQELVMDEKN QELRWMEAAR WVQLEENLG ENGAWGRPHL SHLTFWSLLE LRRVFTKGTV LLDLQETSLA GVANQLLDRF IFEDQIRPQD REELLRALLL K HSHAGELE ...文字列: MEELQDDYED MMEENLEQEE YEDPDIPESQ MEEPAAHDTE ATATDYHTTS HPGTHKVYVE LQELVMDEKN QELRWMEAAR WVQLEENLG ENGAWGRPHL SHLTFWSLLE LRRVFTKGTV LLDLQETSLA GVANQLLDRF IFEDQIRPQD REELLRALLL K HSHAGELE ALGGVKPAVL TRSGDPSQPL LPQHSSLETQ LFCEQGDGGT EGHSPSGILE KIPPDSEATL VLVGRADFLE QP VLGFVRL QEAAELEAVE LPVPIRFLFV LLGPEAPHID YTQLGRAAAT LMSERVFRID AYMAQSRGEL LHSLEGFLDC SLV LPPTDA PSEQALLSLV PVQRELLRRR YQSSPAKPDS SFYKGLDLNG GPDDPLQQTG QLFGGLVRDI RRRYPYYLSD ITDA FSPQV LAAVIFIYFA ALSPAITFGG LLGEKTRNQM GVSELLISTA VQGILFALLG AQPLLVVGFS GPLLVFEEAF FSFCE TNGL EYIVGRVWIG FWLILLVVLV VAFEGSFLVR FISRYTQEIF SFLISLIFIY ETFSKLIKIF QDHPLQKTYN YNVLMV PKP QGPLPNTALL SLVLMAGTFF FAMMLRKFKN SSYFPGKLRR VIGDFGVPIS ILIMVLVDFF IQDTYTQKLS VPDGFKV SN SSARGWVIHP LGLRSEFPIW MMFASALPAL LVFILIFLES QITTLIVSKP ERKMVKGSGF HLDLLLVVGM GGVAALFG M PWLSATTVRS VTHANALTVM GKASTPGAAA QIQEVKEQRI SGLLVAVLVG LSILMEPILS RIPLAVLFGI FLYMGVTSL SGIQLFDRIL LLFKPPKYHP DVPYVKRVKT WRMHLFTGIQ IICLAVLWVV KSTPASLALP FVLILTVPLR RVLLPLIFRN VELQCLDAD DAKATFDEEE GRDEYDEVAM PV UniProtKB: Band 3 anion transport protein |
-分子 #2: Protein 4.2
| 分子 | 名称: Protein 4.2 / タイプ: protein_or_peptide / ID: 2 / コピー数: 1 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 分子量 | 理論値: 77.096914 KDa |
| 配列 | 文字列: MGQALGIKSC DFQAARNNEE HHTKALSSRR LFVRRGQPFT IILYFRAPVR AFLPALKKVA LTAQTGEQPS KINRTQATFP ISSLGDRKW WSAVVEERDA QSWTISVTTP ADAVIGHYSL LLQVSGRKQL LLGQFTLLFN PWNREDAVFL KNEAQRMEYL L NQNGLIYL ...文字列: MGQALGIKSC DFQAARNNEE HHTKALSSRR LFVRRGQPFT IILYFRAPVR AFLPALKKVA LTAQTGEQPS KINRTQATFP ISSLGDRKW WSAVVEERDA QSWTISVTTP ADAVIGHYSL LLQVSGRKQL LLGQFTLLFN PWNREDAVFL KNEAQRMEYL L NQNGLIYL GTADCIQAES WDFGQFEGDV IDLSLRLLSK DKQVEKWSQP VHVARVLGAL LHFLKEQRVL PTPQTQATQE GA LLNKRRG SVPILRQWLT GRGRPVYDGQ AWVLAAVACT VLRCLGIPAR VVTTFASAQG TGGRLLIDEY YNEEGLQNGE GQR GRIWIF QTSTECWMTR PALPQGYDGW QILHPSAPNG GGVLGSCDLV PVRAVKEGTL GLTPAVSDLF AAINASCVVW KCCE DGTLE LTDSNTKYVG NNISTKGVGS DRCEDITQNY KYPEGSLQEK EVLERVEKEK MEREKDNGIR PPSLETASPL YLLLK APSS LPLRGDAQIS VTLVNHSEQE KAVQLAIGVQ AVHYNGVLAA KLWRKKLHLT LSANLEKIIT IGLFFSNFER NPPENT FLR LTAMATHSES NLSCFAQEDI AICRPHLAIK MPEKAEQYQP LTASVSLQNS LDAPMEDCVI SILGRGLIHR ERSYRFR SV WPENTMCAKF QFTPTHVGLQ RLTVEVDCNM FQNLTNYKSV TVVAPELSA UniProtKB: Protein 4.2 |
-分子 #3: 2-acetamido-2-deoxy-beta-D-glucopyranose
| 分子 | 名称: 2-acetamido-2-deoxy-beta-D-glucopyranose / タイプ: ligand / ID: 3 / コピー数: 2 / 式: NAG |
|---|---|
| 分子量 | 理論値: 221.208 Da |
| Chemical component information |  ChemComp-NAG: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 2.5 mg/mL | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| |||||||||||||||
| グリッド | モデル: UltrAuFoil R1.2/1.3 / 材質: GOLD / メッシュ: 300 / 支持フィルム - 材質: GOLD / 支持フィルム - トポロジー: HOLEY | |||||||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 温度 | 最低: 100.0 K / 最高: 100.0 K |
| 撮影 | フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) 撮影したグリッド数: 1 / 実像数: 20842 / 平均露光時間: 2.0 sec. / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.5 µm / 最小 デフォーカス(公称値): 1.8 µm / 倍率(公称値): 81000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL / プロトコル: AB INITIO MODEL / 温度因子: 192 |
|---|---|
| 得られたモデル |  PDB-7tw0: |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)




















