+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 |  | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of human eIF3 core from closed 48S translation initiation complex | |||||||||
 マップデータ マップデータ | ||||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | RIBOSOME / TRANSLATION / initiation / 48S / eIF / human / eukaryotic / factor / codon / scanning / open / reading | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of mRNA binding / viral translational termination-reinitiation / eukaryotic translation initiation factor 3 complex, eIF3e / cap-dependent translational initiation / eukaryotic translation initiation factor 3 complex, eIF3m / translation reinitiation / IRES-dependent viral translational initiation / multi-eIF complex / formation of cytoplasmic translation initiation complex / eukaryotic translation initiation factor 3 complex ...positive regulation of mRNA binding / viral translational termination-reinitiation / eukaryotic translation initiation factor 3 complex, eIF3e / cap-dependent translational initiation / eukaryotic translation initiation factor 3 complex, eIF3m / translation reinitiation / IRES-dependent viral translational initiation / multi-eIF complex / formation of cytoplasmic translation initiation complex / eukaryotic translation initiation factor 3 complex / eukaryotic 43S preinitiation complex / cytoplasmic translational initiation / mRNA cap binding / eukaryotic 48S preinitiation complex / negative regulation of RNA splicing / metal-dependent deubiquitinase activity / regulation of translational initiation / rRNA modification in the nucleus and cytosol / Formation of the ternary complex, and subsequently, the 43S complex / erythrocyte homeostasis / cytoplasmic side of rough endoplasmic reticulum membrane / laminin receptor activity / nuclear-transcribed mRNA catabolic process, nonsense-mediated decay / Ribosomal scanning and start codon recognition / Translation initiation complex formation / SARS-CoV-1 modulates host translation machinery / Peptide chain elongation / Selenocysteine synthesis / Formation of a pool of free 40S subunits / Eukaryotic Translation Termination / Response of EIF2AK4 (GCN2) to amino acid deficiency / SRP-dependent cotranslational protein targeting to membrane / Viral mRNA Translation / Nonsense Mediated Decay (NMD) independent of the Exon Junction Complex (EJC) / GTP hydrolysis and joining of the 60S ribosomal subunit / L13a-mediated translational silencing of Ceruloplasmin expression / Major pathway of rRNA processing in the nucleolus and cytosol / Nonsense Mediated Decay (NMD) enhanced by the Exon Junction Complex (EJC) / translation regulator activity / Amplification of signal from unattached kinetochores via a MAD2 inhibitory signal / cytosolic ribosome / Mitotic Prometaphase / laminin binding / EML4 and NUDC in mitotic spindle formation / negative regulation of translational initiation / negative regulation of proteasomal ubiquitin-dependent protein catabolic process / translation initiation factor binding / Resolution of Sister Chromatid Cohesion / translation initiation factor activity / 90S preribosome / erythrocyte differentiation / maturation of SSU-rRNA / small-subunit processome / positive regulation of translation / translational initiation / RHO GTPases Activate Formins / PML body / negative regulation of ERK1 and ERK2 cascade / receptor tyrosine kinase binding / fibrillar center / mRNA 5'-UTR binding / Regulation of expression of SLITs and ROBOs / rRNA processing / Separation of Sister Chromatids / metallopeptidase activity / ribosome biogenesis / ribosome binding / virus receptor activity / ribosomal small subunit biogenesis / ribosomal small subunit assembly / small ribosomal subunit / small ribosomal subunit rRNA binding / SARS-CoV-2 modulates host translation machinery / cytosolic small ribosomal subunit / ubiquitinyl hydrolase 1 / microtubule / cysteine-type deubiquitinase activity / cytoplasmic translation / postsynaptic density / cell differentiation / ribosome / structural constituent of ribosome / ribonucleoprotein complex / cadherin binding / translation / focal adhesion / mRNA binding / synapse / chromatin / nucleolus / negative regulation of apoptotic process / structural molecule activity / negative regulation of transcription by RNA polymerase II / endoplasmic reticulum / proteolysis / DNA binding / RNA binding / zinc ion binding / extracellular exosome / nucleoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
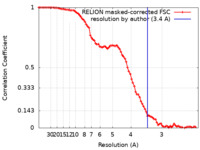
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.4 Å | |||||||||
 データ登録者 データ登録者 | Petrychenko V / Yi S-H / Liedtke D / Peng BZ / Rodnina MV / Fischer N | |||||||||
| 資金援助 |  ドイツ, 2件 ドイツ, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat.Struct.Mol.Biol. / 年: 2024 ジャーナル: Nat.Struct.Mol.Biol. / 年: 2024タイトル: Structural basis for translational control by the human 48S initiation complex from codon scanning toward subunit joining 著者: Petrychenko V / Yi S-H / Liedtke D / Peng BZ / Rodnina MV / Fischer N | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 添付画像 |
|---|
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_19128.map.gz emd_19128.map.gz | 47.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-19128-v30.xml emd-19128-v30.xml emd-19128.xml emd-19128.xml | 47.9 KB 47.9 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_19128_fsc.xml emd_19128_fsc.xml | 8.5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_19128.png emd_19128.png | 206.8 KB | ||
| マスクデータ |  emd_19128_msk_1.map emd_19128_msk_1.map | 52.7 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-19128.cif.gz emd-19128.cif.gz | 12.8 KB | ||
| その他 |  emd_19128_additional_1.map.gz emd_19128_additional_1.map.gz emd_19128_additional_2.map.gz emd_19128_additional_2.map.gz emd_19128_half_map_1.map.gz emd_19128_half_map_1.map.gz emd_19128_half_map_2.map.gz emd_19128_half_map_2.map.gz | 49.4 MB 40.6 MB 40.7 MB 40.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-19128 http://ftp.pdbj.org/pub/emdb/structures/EMD-19128 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19128 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-19128 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  8rg0MC  17696  17697  17698  17699  17700  17701  8pj1C  8pj2C  8pj3C  8pj4C  8pj5C  8pj6C M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_19128.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_19128.map.gz / 形式: CCP4 / 大きさ: 52.7 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 1.16 Å | ||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||
| 詳細 | EMDB XML:
|
-添付データ
-マスク #1
| ファイル |  emd_19128_msk_1.map emd_19128_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
+全体 : Human 48S initiation complex 40S-eIF1-eIF1A-eIF2-eIF3-tRNA-Met-mRNA
+超分子 #1: Human 48S initiation complex 40S-eIF1-eIF1A-eIF2-eIF3-tRNA-Met-mRNA
+超分子 #2: Human 48S initiation complex 40S-eIF1-eIF1A-eIF2-eIF3-tRNA-Met
+超分子 #3: mRNA
+分子 #1: Eukaryotic translation initiation factor 3 subunit K
+分子 #2: Eukaryotic translation initiation factor 3 subunit F
+分子 #3: Eukaryotic translation initiation factor 3 subunit L
+分子 #4: Eukaryotic translation initiation factor 3 subunit M
+分子 #6: Eukaryotic translation initiation factor 3 subunit H
+分子 #8: 40S ribosomal protein S27
+分子 #9: 40S ribosomal protein S13
+分子 #10: 40S ribosomal protein S17
+分子 #11: 40S ribosomal protein SA
+分子 #12: 40S ribosomal protein S3a
+分子 #13: 40S ribosomal protein S14
+分子 #14: 40S ribosomal protein S26
+分子 #15: 40S ribosomal protein S28
+分子 #16: Eukaryotic translation initiation factor 3 subunit A
+分子 #17: Eukaryotic translation initiation factor 3 subunit E
+分子 #18: Eukaryotic translation initiation factor 3 subunit D
+分子 #19: Eukaryotic translation initiation factor 3 subunit C
+分子 #5: mRNA
+分子 #7: 18S rRNA
+分子 #20: MAGNESIUM ION
+分子 #21: ZINC ION
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: HOMEMADE PLUNGER / 詳細: Manual blotting & plunge-freezing. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 特殊光学系 | 球面収差補正装置: Electron-optical aberrations were corrected using a CETCOR Cs-corrector (CEOS, Heidelberg) aligned with the CETCORPLUS 4.6.9 software package (CEOS, Heidelberg). |
| 撮影 | フィルム・検出器のモデル: FEI FALCON III (4k x 4k) 検出モード: INTEGRATING / 平均露光時間: 1.5 sec. / 平均電子線量: 45.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: SPOT SCAN / 撮影モード: BRIGHT FIELD / Cs: 0.01 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.2 µm / 倍率(公称値): 59000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | 空間: REAL |
|---|---|
| 得られたモデル |  PDB-8rg0: |
 ムービー
ムービー コントローラー
コントローラー



















 Z
Z Y
Y X
X