+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-1207 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of the bacteriophage phi6 nucleocapsid suggests a mechanism for sequential RNA packaging. | |||||||||
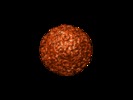
 マップデータ マップデータ | Reconstruction of phi6 empty nucleocapsid | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Pseudomonas phage phi6 (ファージ) Pseudomonas phage phi6 (ファージ) | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 12.0 Å | |||||||||
 データ登録者 データ登録者 | Huiskonen JT / de Haas F / Bubeck D / Bamford DH / Fuller SD / Butcher SJ | |||||||||
 引用 引用 |  ジャーナル: Structure / 年: 2006 ジャーナル: Structure / 年: 2006タイトル: Structure of the bacteriophage phi6 nucleocapsid suggests a mechanism for sequential RNA packaging. 著者: Juha T Huiskonen / Felix de Haas / Doryen Bubeck / Dennis H Bamford / Stephen D Fuller / Sarah J Butcher /  要旨: Bacteriophage phi6 is an enveloped dsRNA virus with a segmented genome. Phi6 specifically packages one copy of each of its three genome segments into a preassembled polymerase complex. This leads to ...Bacteriophage phi6 is an enveloped dsRNA virus with a segmented genome. Phi6 specifically packages one copy of each of its three genome segments into a preassembled polymerase complex. This leads to expansion of the polymerase complex, minus and plus strand RNA synthesis, and assembly of the nucleocapsid. The phi6 in vitro assembly and packaging system is a valuable model for dsRNA virus replication. The structure of the nucleocapsid at 7.5 A resolution presented here reveals the secondary structure of the two major capsid proteins. Asymmetric P1 dimers organize as an inner T = 1 shell, and P8 trimers organize as an outer T = 13 laevo shell. The organization of the P1 molecules in the unexpanded and expanded polymerase complex suggests that the expansion is accomplished by rigid body movements of the P1 monomers. This leads to exposure of new potential RNA binding surfaces to control the sequential packaging of the genome segments. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_1207.map.gz emd_1207.map.gz | 25.2 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-1207-v30.xml emd-1207-v30.xml emd-1207.xml emd-1207.xml | 8.5 KB 8.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  1207.gif 1207.gif | 42.1 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-1207 http://ftp.pdbj.org/pub/emdb/structures/EMD-1207 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1207 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-1207 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_1207_validation.pdf.gz emd_1207_validation.pdf.gz | 317.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_1207_full_validation.pdf.gz emd_1207_full_validation.pdf.gz | 317 KB | 表示 | |
| XML形式データ |  emd_1207_validation.xml.gz emd_1207_validation.xml.gz | 6.8 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1207 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1207 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1207 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-1207 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_1207.map.gz / 形式: CCP4 / 大きさ: 39.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_1207.map.gz / 形式: CCP4 / 大きさ: 39.1 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Reconstruction of phi6 empty nucleocapsid | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.8 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : Bacteriophage phi6 nucleocapsid
| 全体 | 名称: Bacteriophage phi6 nucleocapsid |
|---|---|
| 要素 |
|
-超分子 #1000: Bacteriophage phi6 nucleocapsid
| 超分子 | 名称: Bacteriophage phi6 nucleocapsid / タイプ: sample / ID: 1000 / Number unique components: 1 |
|---|---|
| 分子量 | 理論値: 22 MDa |
-超分子 #1: Pseudomonas phage phi6
| 超分子 | 名称: Pseudomonas phage phi6 / タイプ: virus / ID: 1 / Name.synonym: Bacteriophage phi6 / NCBI-ID: 10879 / 生物種: Pseudomonas phage phi6 / ウイルスタイプ: VIRION / ウイルス・単離状態: SPECIES / ウイルス・エンベロープ: Yes / ウイルス・中空状態: No / Syn species name: Bacteriophage phi6 |
|---|---|
| 宿主 | 生物種: Pseudomonas syringae pv phaesolicola HB10Y / 別称: BACTERIA(EUBACTERIA) |
| ウイルス殻 | Shell ID: 1 / 名称: PC shell / 直径: 485 Å / T番号(三角分割数): 1 |
| ウイルス殻 | Shell ID: 2 / 名称: NC shell / 直径: 555 Å / T番号(三角分割数): 13 |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 凍結 | 凍結剤: ETHANE |
|---|
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TECNAI F20 |
|---|---|
| 温度 | 平均: 93 K |
| 撮影 | カテゴリ: FILM / フィルム・検出器のモデル: KODAK SO-163 FILM / デジタル化 - スキャナー: ZEISS SCAI / デジタル化 - サンプリング間隔: 7 µm / 実像数: 37 / ビット/ピクセル: 12 |
| Tilt angle min | 0 |
| Tilt angle max | 0 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.0 mm / 最大 デフォーカス(公称値): 2.5 µm / 最小 デフォーカス(公称値): 0.5 µm / 倍率(公称値): 50000 |
| 試料ステージ | 試料ホルダー: Side entry liquid nitrogen-cooled cryo specimen holder 試料ホルダーモデル: OTHER |
| 実験機器 |  モデル: Tecnai F20 / 画像提供: FEI Company |
- 画像解析
画像解析
| CTF補正 | 詳細: each particle, full CTF correction |
|---|---|
| 最終 再構成 | 想定した対称性 - 点群: I (正20面体型対称) / アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 12.0 Å / 解像度の算出法: FSC 0.5 CUT-OFF / ソフトウェア - 名称: P3DR 詳細: The map was calculated from empty particles lacking the genome 使用した粒子像数: 1163 |
 ムービー
ムービー コントローラー
コントローラー












 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)





















