+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 8dns | ||||||
|---|---|---|---|---|---|---|---|
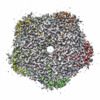
| タイトル | Human Brain Glyceraldehyde 3-phosphate dehydrogenase | ||||||
 要素 要素 | Glyceraldehyde-3-phosphate dehydrogenase | ||||||
 キーワード キーワード | OXIDOREDUCTASE / human brain / GAPDH | ||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報peptidyl-cysteine S-trans-nitrosylation / 転移酵素; 含窒素の基を移すもの; その他の含窒素の基を移すもの / peptidyl-cysteine S-nitrosylase activity / killing by host of symbiont cells / glyceraldehyde-3-phosphate dehydrogenase (phosphorylating) / aspartic-type endopeptidase inhibitor activity / negative regulation of endopeptidase activity / glyceraldehyde-3-phosphate dehydrogenase (NAD+) (phosphorylating) activity / Gluconeogenesis / GAIT complex ...peptidyl-cysteine S-trans-nitrosylation / 転移酵素; 含窒素の基を移すもの; その他の含窒素の基を移すもの / peptidyl-cysteine S-nitrosylase activity / killing by host of symbiont cells / glyceraldehyde-3-phosphate dehydrogenase (phosphorylating) / aspartic-type endopeptidase inhibitor activity / negative regulation of endopeptidase activity / glyceraldehyde-3-phosphate dehydrogenase (NAD+) (phosphorylating) activity / Gluconeogenesis / GAIT complex / Glycolysis / positive regulation of type I interferon production / regulation of macroautophagy / defense response to fungus / lipid droplet / positive regulation of cytokine production / glycolytic process / cellular response to type II interferon / microtubule cytoskeleton organization / antimicrobial humoral immune response mediated by antimicrobial peptide / glucose metabolic process / NAD binding / microtubule cytoskeleton / disordered domain specific binding / NADP binding / microtubule binding / nuclear membrane / neuron apoptotic process / positive regulation of canonical NF-kappaB signal transduction / vesicle / killing of cells of another organism / protein stabilization / negative regulation of translation / ribonucleoprotein complex / intracellular membrane-bounded organelle / perinuclear region of cytoplasm / extracellular exosome / identical protein binding / membrane / nucleus / plasma membrane / cytoplasm / cytosol 類似検索 - 分子機能 | ||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.22 Å | ||||||
 データ登録者 データ登録者 | Tringides, M.L. | ||||||
| 資金援助 |  米国, 1件 米国, 1件
| ||||||
 引用 引用 |  ジャーナル: Life Sci Alliance / 年: 2023 ジャーナル: Life Sci Alliance / 年: 2023タイトル: A cryo-electron microscopic approach to elucidate protein structures from human brain microsomes. 著者: Marios L Tringides / Zhemin Zhang / Christopher E Morgan / Chih-Chia Su / Edward W Yu /  要旨: We recently developed a "Build and Retrieve" cryo-electron microscopy (cryo-EM) methodology, which is capable of simultaneously producing near-atomic resolution cryo-EM maps for several individual ...We recently developed a "Build and Retrieve" cryo-electron microscopy (cryo-EM) methodology, which is capable of simultaneously producing near-atomic resolution cryo-EM maps for several individual proteins from a heterogeneous, multiprotein sample. Here we report the use of "Build and Retrieve" to define the composition of a raw human brain microsomal lysate. From this sample, we simultaneously identify and solve cryo-EM structures of five different brain enzymes whose functions affect neurotransmitter recycling, iron metabolism, glycolysis, axonal development, energy homeostasis, and retinoic acid biosynthesis. Interestingly, malfunction of these important proteins has been directly linked to several neurodegenerative disorders, such as Alzheimer's, Huntington's, and Parkinson's diseases. Our work underscores the importance of cryo-EM in facilitating tissue and organ proteomics at the atomic level. | ||||||
| 履歴 |
|
- 構造の表示
構造の表示
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
|---|
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  8dns.cif.gz 8dns.cif.gz | 220.4 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb8dns.ent.gz pdb8dns.ent.gz | 180.5 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  8dns.json.gz 8dns.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  8dns_validation.pdf.gz 8dns_validation.pdf.gz | 1.2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  8dns_full_validation.pdf.gz 8dns_full_validation.pdf.gz | 1.2 MB | 表示 | |
| XML形式データ |  8dns_validation.xml.gz 8dns_validation.xml.gz | 43.9 KB | 表示 | |
| CIF形式データ |  8dns_validation.cif.gz 8dns_validation.cif.gz | 60.6 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/dn/8dns https://data.pdbj.org/pub/pdb/validation_reports/dn/8dns ftp://data.pdbj.org/pub/pdb/validation_reports/dn/8dns ftp://data.pdbj.org/pub/pdb/validation_reports/dn/8dns | HTTPS FTP |
-関連構造データ
| 関連構造データ |  27579MC  8dnmC  8dnoC  8dnpC  8dnuC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | 類似検索 - 機能・相同性  F&H 検索 F&H 検索 |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 36099.168 Da / 分子数: 4 / 由来タイプ: 天然 / 由来: (天然)  Homo sapiens (ヒト) Homo sapiens (ヒト)参照: UniProt: P04406, glyceraldehyde-3-phosphate dehydrogenase (phosphorylating), 転移酵素; 含窒素の基を移すもの; その他の含窒素の基を移すもの |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: TISSUE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: Glyceraldehyde 3-phosphate dehydrogenase / タイプ: COMPLEX / Entity ID: all / 由来: NATURAL |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 緩衝液 | pH: 7.5 |
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 急速凍結 | 凍結剤: ETHANE |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: TFS KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 最大 デフォーカス(公称値): 3706 nm / 最小 デフォーカス(公称値): 1212 nm |
| 撮影 | 電子線照射量: 36.5 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) |
- 解析
解析
| ソフトウェア | 名称: PHENIX / バージョン: 1.19.2_4158: / 分類: 精密化 | ||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.22 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 8982 / 対称性のタイプ: POINT | ||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー






 PDBj
PDBj

