+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7abz | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of pre-accomodated trans-translation complex on E. coli stalled ribosome. | |||||||||||||||
 要素 要素 |
| |||||||||||||||
 キーワード キーワード | TRANSLATION / Trans-translation / tmRNA / SmpB / Ribosome | |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報trans-translation / guanyl-nucleotide exchange factor complex / guanosine tetraphosphate binding / stringent response / ornithine decarboxylase inhibitor activity / transcription antitermination factor activity, RNA binding / misfolded RNA binding / Group I intron splicing / RNA folding / translational elongation ...trans-translation / guanyl-nucleotide exchange factor complex / guanosine tetraphosphate binding / stringent response / ornithine decarboxylase inhibitor activity / transcription antitermination factor activity, RNA binding / misfolded RNA binding / Group I intron splicing / RNA folding / translational elongation / transcriptional attenuation / endoribonuclease inhibitor activity / RNA-binding transcription regulator activity / negative regulation of cytoplasmic translation / translation elongation factor activity / translational termination / four-way junction DNA binding / DnaA-L2 complex / translation repressor activity / negative regulation of translational initiation / negative regulation of DNA-templated DNA replication initiation / regulation of mRNA stability / mRNA regulatory element binding translation repressor activity / ribosome assembly / positive regulation of RNA splicing / assembly of large subunit precursor of preribosome / transcription elongation factor complex / regulation of DNA-templated transcription elongation / cytosolic ribosome assembly / DNA endonuclease activity / transcription antitermination / response to reactive oxygen species / DNA-templated transcription termination / maintenance of translational fidelity / response to radiation / mRNA 5'-UTR binding / ribosomal small subunit biogenesis / large ribosomal subunit / ribosome biogenesis / small ribosomal subunit rRNA binding / ribosome binding / ribosomal large subunit assembly / regulation of translation / ribosomal small subunit assembly / small ribosomal subunit / large ribosomal subunit rRNA binding / transferase activity / 5S rRNA binding / cytosolic small ribosomal subunit / cytosolic large ribosomal subunit / cytoplasmic translation / tRNA binding / molecular adaptor activity / negative regulation of translation / rRNA binding / ribosome / structural constituent of ribosome / translation / response to antibiotic / negative regulation of DNA-templated transcription / GTPase activity / mRNA binding / GTP binding / DNA binding / RNA binding / zinc ion binding / membrane / plasma membrane / cytosol / cytoplasm 類似検索 - 分子機能 | |||||||||||||||
| 生物種 |  | |||||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.21 Å | |||||||||||||||
 データ登録者 データ登録者 | Guyomar, C. / D'Urso, G. / Chat, S. / Giudice, E. / Gillet, R. | |||||||||||||||
| 資金援助 |  フランス, 4件 フランス, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2021 ジャーナル: Nat Commun / 年: 2021タイトル: Structures of tmRNA and SmpB as they transit through the ribosome. 著者: Charlotte Guyomar / Gaetano D'Urso / Sophie Chat / Emmanuel Giudice / Reynald Gillet /  要旨: In bacteria, trans-translation is the main rescue system, freeing ribosomes stalled on defective messenger RNAs. This mechanism is driven by small protein B (SmpB) and transfer-messenger RNA (tmRNA), ...In bacteria, trans-translation is the main rescue system, freeing ribosomes stalled on defective messenger RNAs. This mechanism is driven by small protein B (SmpB) and transfer-messenger RNA (tmRNA), a hybrid RNA known to have both a tRNA-like and an mRNA-like domain. Here we present four cryo-EM structures of the ribosome during trans-translation at resolutions from 3.0 to 3.4 Å. These include the high-resolution structure of the whole pre-accommodated state, as well as structures of the accommodated state, the translocated state, and a translocation intermediate. Together, they shed light on the movements of the tmRNA-SmpB complex in the ribosome, from its delivery by the elongation factor EF-Tu to its passage through the ribosomal A and P sites after the opening of the B1 bridges. Additionally, we describe the interactions between the tmRNA-SmpB complex and the ribosome. These explain why the process does not interfere with canonical translation. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7abz.cif.gz 7abz.cif.gz | 3.5 MB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7abz.ent.gz pdb7abz.ent.gz | 表示 |  PDB形式 PDB形式 | |
| PDBx/mmJSON形式 |  7abz.json.gz 7abz.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7abz_validation.pdf.gz 7abz_validation.pdf.gz | 2 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7abz_full_validation.pdf.gz 7abz_full_validation.pdf.gz | 2.2 MB | 表示 | |
| XML形式データ |  7abz_validation.xml.gz 7abz_validation.xml.gz | 238.7 KB | 表示 | |
| CIF形式データ |  7abz_validation.cif.gz 7abz_validation.cif.gz | 399 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/ab/7abz https://data.pdbj.org/pub/pdb/validation_reports/ab/7abz ftp://data.pdbj.org/pub/pdb/validation_reports/ab/7abz ftp://data.pdbj.org/pub/pdb/validation_reports/ab/7abz | HTTPS FTP |
-関連構造データ
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
-RNA鎖 , 6種, 6分子 123478
| #1: RNA鎖 | 分子量: 941832.625 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #2: RNA鎖 | 分子量: 499215.000 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #3: RNA鎖 | 分子量: 38177.762 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #4: RNA鎖 | 分子量: 117212.297 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   |
| #7: RNA鎖 | 分子量: 24745.979 Da / 分子数: 1 / 由来タイプ: 合成 / 詳細: Sigma-Aldrich / 由来: (合成)  |
| #8: RNA鎖 | 分子量: 4889.930 Da / 分子数: 1 / 由来タイプ: 合成 / 由来: (合成)  |
-タンパク質 , 2種, 2分子 56
| #5: タンパク質 | 分子量: 16776.314 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   |
|---|---|
| #6: タンパク質 | 分子量: 43370.492 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)   |
+50S ribosomal protein ... , 30種, 30分子 ABCDEFGHIJKLMNOPQRSTUVXYZbcdef
-30S ribosomal protein ... , 20種, 20分子 ghijklmnopqrstuvwxyz
| #39: タンパク質 | 分子量: 24971.764 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
|---|---|
| #40: タンパク質 | 分子量: 23078.785 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #41: タンパク質 | 分子量: 23383.002 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #42: タンパク質 | 分子量: 17659.447 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #43: タンパク質 | 分子量: 11669.371 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #44: タンパク質 | 分子量: 16861.523 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #45: タンパク質 | 分子量: 14015.361 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #46: タンパク質 | 分子量: 14554.882 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #47: タンパク質 | 分子量: 11196.988 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #48: タンパク質 | 分子量: 12487.200 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #49: タンパク質 | 分子量: 13683.053 Da / 分子数: 1 / 由来タイプ: 天然 詳細: modified residue position 88 (3S)-3-(methylsulfanyl)-L-aspartic acid 由来: (天然)  |
| #50: タンパク質 | 分子量: 12625.753 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #51: タンパク質 | 分子量: 11475.364 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #52: タンパク質 | 分子量: 10159.621 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #53: タンパク質 | 分子量: 9207.572 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #54: タンパク質 | 分子量: 9263.946 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #55: タンパク質 | 分子量: 6466.477 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #56: タンパク質 | 分子量: 9057.626 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #57: タンパク質 | 分子量: 9506.190 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
| #58: タンパク質 | 分子量: 6629.744 Da / 分子数: 1 / 由来タイプ: 天然 / 由来: (天然)  |
-非ポリマー , 4種, 195分子 
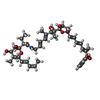





| #59: 化合物 | ChemComp-MG / #60: 化合物 | ChemComp-KIR / | #61: 化合物 | ChemComp-GDP / | #62: 化合物 | ChemComp-ZN / | |
|---|
-詳細
| 研究の焦点であるリガンドがあるか | N |
|---|
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 |
| ||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 分子量 | 実験値: NO | ||||||||||||||||||||||||||||||||||||
| 由来(天然) |
| ||||||||||||||||||||||||||||||||||||
| 由来(組換発現) |
| ||||||||||||||||||||||||||||||||||||
| 緩衝液 | pH: 7.5 | ||||||||||||||||||||||||||||||||||||
| 緩衝液成分 |
| ||||||||||||||||||||||||||||||||||||
| 試料 | 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES | ||||||||||||||||||||||||||||||||||||
| 試料支持 | 詳細: 10mA / グリッドの材料: COPPER / グリッドのタイプ: Quantifoil R2/2 | ||||||||||||||||||||||||||||||||||||
| 急速凍結 | 装置: FEI VITROBOT MARK III / 凍結剤: ETHANE / 湿度: 100 % / 凍結前の試料温度: 298 K / 詳細: blot for 3.5 seconds before plunging |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD / 倍率(公称値): 105000 X / 最大 デフォーカス(公称値): -3000 nm / 最小 デフォーカス(公称値): -1000 nm / Cs: 0.01 mm |
| 試料ホルダ | 凍結剤: NITROGEN |
| 撮影 | 平均露光時間: 8 sec. / 電子線照射量: 35 e/Å2 フィルム・検出器のモデル: GATAN K2 BASE (4k x 4k) 撮影したグリッド数: 4343 / 実像数: 59016 |
| 電子光学装置 | 球面収差補正装置: Microscope was modified with a Cs corrector |
| 画像スキャン | 横: 3710 / 縦: 3838 |
- 解析
解析
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| CTF補正 | タイプ: NONE | ||||||||||||||||||||||||||||||||||||||||
| 粒子像の選択 | 選択した粒子像数: 59016 | ||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.21 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 18452 / クラス平均像の数: 1 / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: OTHER / 空間: REAL | ||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | PDB-ID: 4YBB Accession code: 4YBB / Source name: PDB / タイプ: experimental model | ||||||||||||||||||||||||||||||||||||||||
| 精密化 | 立体化学のターゲット値: GeoStd + Monomer Library + CDL v1.2 | ||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 142.02 Å2 | ||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー




















 PDBj
PDBj


































