+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-5890 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of MAVS CARD filament | |||||||||
 マップデータ マップデータ | Cryo-EM map of MAVS CARD filament | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Innate immunity / helical filament | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報positive regulation of IP-10 production / regulation of peroxisome organization / RIG-I binding / positive regulation of chemokine (C-C motif) ligand 5 production / positive regulation of myeloid dendritic cell cytokine production / CARD domain binding / NF-kB activation through FADD/RIP-1 pathway mediated by caspase-8 and -10 / positive regulation of response to cytokine stimulus / protein localization to mitochondrion / positive regulation of type I interferon-mediated signaling pathway ...positive regulation of IP-10 production / regulation of peroxisome organization / RIG-I binding / positive regulation of chemokine (C-C motif) ligand 5 production / positive regulation of myeloid dendritic cell cytokine production / CARD domain binding / NF-kB activation through FADD/RIP-1 pathway mediated by caspase-8 and -10 / positive regulation of response to cytokine stimulus / protein localization to mitochondrion / positive regulation of type I interferon-mediated signaling pathway / peroxisomal membrane / TRAF6 mediated IRF7 activation / negative regulation of type I interferon-mediated signaling pathway / negative regulation of viral genome replication / cytoplasmic pattern recognition receptor signaling pathway / positive regulation of NLRP3 inflammasome complex assembly / type I interferon-mediated signaling pathway / cellular response to exogenous dsRNA / positive regulation of interferon-alpha production / TRAF6 mediated NF-kB activation / positive regulation of type I interferon production / ubiquitin ligase complex / signaling adaptor activity / positive regulation of defense response to virus by host / antiviral innate immune response / activation of innate immune response / positive regulation of interferon-beta production / positive regulation of interleukin-8 production / Negative regulators of DDX58/IFIH1 signaling / mitochondrial membrane / positive regulation of DNA-binding transcription factor activity / molecular condensate scaffold activity / DDX58/IFIH1-mediated induction of interferon-alpha/beta / PKR-mediated signaling / Evasion by RSV of host interferon responses / positive regulation of protein import into nucleus / positive regulation of interleukin-6 production / SARS-CoV-1 activates/modulates innate immune responses / positive regulation of tumor necrosis factor production / Ovarian tumor domain proteases / TRAF3-dependent IRF activation pathway / defense response to virus / positive regulation of canonical NF-kappaB signal transduction / mitochondrial outer membrane / molecular adaptor activity / defense response to bacterium / positive regulation of protein phosphorylation / innate immune response / protein kinase binding / SARS-CoV-2 activates/modulates innate and adaptive immune responses / signal transduction / positive regulation of transcription by RNA polymerase II / mitochondrion / identical protein binding 類似検索 - 分子機能 | |||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | |||||||||
| 手法 | らせん対称体再構成法 / クライオ電子顕微鏡法 / 解像度: 9.6 Å | |||||||||
 データ登録者 データ登録者 | Xu H / He X / Zheng H / Huang LJ / Hou F / Yu Z / de la Cruz MJ / Borkowski B / Zhang X / Chen ZJ / Jiang Q-X | |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2014 ジャーナル: Elife / 年: 2014タイトル: Structural basis for the prion-like MAVS filaments in antiviral innate immunity. 著者: Hui Xu / Xiaojing He / Hui Zheng / Lily J Huang / Fajian Hou / Zhiheng Yu / Michael Jason de la Cruz / Brian Borkowski / Xuewu Zhang / Zhijian J Chen / Qiu-Xing Jiang /  要旨: Mitochondrial antiviral signaling (MAVS) protein is required for innate immune responses against RNA viruses. In virus-infected cells MAVS forms prion-like aggregates to activate antiviral signaling ...Mitochondrial antiviral signaling (MAVS) protein is required for innate immune responses against RNA viruses. In virus-infected cells MAVS forms prion-like aggregates to activate antiviral signaling cascades, but the underlying structural mechanism is unknown. Here we report cryo-electron microscopic structures of the helical filaments formed by both the N-terminal caspase activation and recruitment domain (CARD) of MAVS and a truncated MAVS lacking part of the proline-rich region and the C-terminal transmembrane domain. Both structures are left-handed three-stranded helical filaments, revealing specific interfaces between individual CARD subunits that are dictated by electrostatic interactions between neighboring strands and hydrophobic interactions within each strand. Point mutations at multiple locations of these two interfaces impaired filament formation and antiviral signaling. Super-resolution imaging of virus-infected cells revealed rod-shaped MAVS clusters on mitochondria. These results elucidate the structural mechanism of MAVS polymerization, and explain how an α-helical domain uses distinct chemical interactions to form self-perpetuating filaments. DOI: http://dx.doi.org/10.7554/eLife.01489.001. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_5890.map.gz emd_5890.map.gz | 297.2 KB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-5890-v30.xml emd-5890-v30.xml emd-5890.xml emd-5890.xml | 12 KB 12 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_5890.tif emd_5890.tif | 129.2 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-5890 http://ftp.pdbj.org/pub/emdb/structures/EMD-5890 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-5890 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-5890 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_5890_validation.pdf.gz emd_5890_validation.pdf.gz | 297.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_5890_full_validation.pdf.gz emd_5890_full_validation.pdf.gz | 297.5 KB | 表示 | |
| XML形式データ |  emd_5890_validation.xml.gz emd_5890_validation.xml.gz | 4.4 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-5890 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-5890 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-5890 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-5890 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  3j6cMC  5891C  4o9fC  4o9lC M: このマップから作成された原子モデル C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10014 (タイトル: MAVS CARD and DeltaProTM filaments / Data size: 35.3 / Data #1: CARD set1 micrographs [micrographs - single frame] / Data #2: CARD set2 micrographs [micrographs - single frame] / Data #3: CARD set3 micrographs [micrographs - single frame] / Data #4: CARD set4 micrographs [micrographs - single frame] EMPIAR-10014 (タイトル: MAVS CARD and DeltaProTM filaments / Data size: 35.3 / Data #1: CARD set1 micrographs [micrographs - single frame] / Data #2: CARD set2 micrographs [micrographs - single frame] / Data #3: CARD set3 micrographs [micrographs - single frame] / Data #4: CARD set4 micrographs [micrographs - single frame]Data #5: CARD set1 segments [picked particles - multiframe - unprocessed] Data #6: CARD set2 segments [picked particles - multiframe - unprocessed] Data #7: CARD set3 segments [picked particles - multiframe - unprocessed] Data #8: CARD set4 segments [picked particles - multiframe - unprocessed] Data #9: DeltProTM micrographs [micrographs - single frame] Data #10: DeltaProTM segments [picked particles - multiframe - unprocessed]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_5890.map.gz / 形式: CCP4 / 大きさ: 955.1 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_5890.map.gz / 形式: CCP4 / 大きさ: 955.1 KB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Cryo-EM map of MAVS CARD filament | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 これらの図は立方格子座標系で作成されたものです | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.333 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
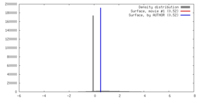
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
-全体 : MAVS CARD filament
| 全体 | 名称: MAVS CARD filament |
|---|---|
| 要素 |
|
-超分子 #1000: MAVS CARD filament
| 超分子 | 名称: MAVS CARD filament / タイプ: sample / ID: 1000 / 集合状態: polymer / Number unique components: 1 |
|---|---|
| 分子量 | 理論値: 546 KDa |
-分子 #1: Mitochondrial antiviral-signaling protein (MAVS)
| 分子 | 名称: Mitochondrial antiviral-signaling protein (MAVS) / タイプ: protein_or_peptide / ID: 1 / Name.synonym: IPS1, KIAA1271, VISA / 集合状態: polymer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  Homo sapiens (ヒト) / 別称: Human Homo sapiens (ヒト) / 別称: Human |
| 分子量 | 理論値: 13 KDa |
| 組換発現 | 生物種:  Homo sapiens (ヒト) / 組換細胞: HEK293T / 組換プラスミド: pcDNA3 Homo sapiens (ヒト) / 組換細胞: HEK293T / 組換プラスミド: pcDNA3 |
| 配列 | UniProtKB: Mitochondrial antiviral-signaling protein |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | らせん対称体再構成法 |
| 試料の集合状態 | filament |
- 試料調製
試料調製
| 緩衝液 | pH: 7.5 / 詳細: 20mM Tris-HCl, 50mM NaCl, 1mM DTT |
|---|---|
| グリッド | 詳細: Quantifoil grids coated with thin carbon on top |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK III |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL 2200FS |
|---|---|
| アライメント法 | Legacy - 非点収差: Objective lens astigmatism was corrected at 100,000x magnification |
| 特殊光学系 | エネルギーフィルター - 名称: JEOL omega filter エネルギーフィルター - エネルギー下限: 0.0 eV エネルギーフィルター - エネルギー上限: 35.0 eV |
| 日付 | 2011年10月20日 |
| 撮影 | カテゴリ: FILM / フィルム・検出器のモデル: KODAK SO-163 FILM / デジタル化 - スキャナー: ZEISS SCAI / デジタル化 - サンプリング間隔: 7 µm / 平均電子線量: 20 e/Å2 |
| 電子線 | 加速電圧: 200 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 61950 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.0 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 0.8 µm / 倍率(公称値): 60000 |
| 試料ステージ | 試料ホルダーモデル: GATAN LIQUID NITROGEN |
- 画像解析
画像解析
| 詳細 | IHRSR |
|---|---|
| 最終 再構成 | 想定した対称性 - らせんパラメータ - Δz: 16.8 Å 想定した対称性 - らせんパラメータ - ΔΦ: 53.6 ° 想定した対称性 - らせんパラメータ - 軸対称性: C3 (3回回転対称) アルゴリズム: OTHER / 解像度のタイプ: BY AUTHOR / 解像度: 9.6 Å / 解像度の算出法: OTHER / ソフトウェア - 名称: Spider, MRC, EMAN, IMAGIC4D 詳細: Final data were calculated from three separate datasets from three sessions of data collection. The handedness of the map was determined by cryo-electron tomography. |
| CTF補正 | 詳細: Each filament segment |
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Chain ID: A |
|---|---|
| ソフトウェア | 名称: Chimera, SITUS |
| 詳細 | The docking of one X-ray model into a segmented map corresponding to one subunit was first done manually in Chimera, and then optimized using SITUS. |
| 精密化 | 空間: REAL / プロトコル: RIGID BODY FIT |
| 得られたモデル |  PDB-3j6c: |
 ムービー
ムービー コントローラー
コントローラー





















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)