+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-4141 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of the E. coli replicative DNA polymerase-clamp-exonuclase-theta complex bound to DNA in the editing mode | |||||||||
 マップデータ マップデータ | Main map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | DNA editing Proofreading Exonuclease Polymerase / DNA Binding protein | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報DNA polymerase III, core complex / DNA polymerase III complex / replisome / DNA replication proofreading / lagging strand elongation / exonuclease activity / leading strand elongation / 3'-5' exonuclease activity / DNA-templated DNA replication / DNA-directed DNA polymerase ...DNA polymerase III, core complex / DNA polymerase III complex / replisome / DNA replication proofreading / lagging strand elongation / exonuclease activity / leading strand elongation / 3'-5' exonuclease activity / DNA-templated DNA replication / DNA-directed DNA polymerase / DNA-directed DNA polymerase activity / ribosome / structural constituent of ribosome / ribonucleoprotein complex / translation / DNA binding / metal ion binding / cytosol / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 6.7 Å | |||||||||
 データ登録者 データ登録者 | Fernandez-Leiro R / Conrad J | |||||||||
 引用 引用 |  ジャーナル: Nat Struct Mol Biol / 年: 2017 ジャーナル: Nat Struct Mol Biol / 年: 2017タイトル: Self-correcting mismatches during high-fidelity DNA replication. 著者: Rafael Fernandez-Leiro / Julian Conrad / Ji-Chun Yang / Stefan M V Freund / Sjors H W Scheres / Meindert H Lamers /  要旨: Faithful DNA replication is essential to all forms of life and depends on the action of 3'-5' exonucleases that remove misincorporated nucleotides from the newly synthesized strand. However, how the ...Faithful DNA replication is essential to all forms of life and depends on the action of 3'-5' exonucleases that remove misincorporated nucleotides from the newly synthesized strand. However, how the DNA is transferred from the polymerase to the exonuclease active site is not known. Here we present the cryo-EM structure of the editing mode of the catalytic core of the Escherichia coli replisome, revealing a dramatic distortion of the DNA whereby the polymerase thumb domain acts as a wedge that separates the two DNA strands. Importantly, NMR analysis of the DNA substrate shows that the presence of a mismatch increases the fraying of the DNA, thus enabling it to reach the exonuclease active site. Therefore the mismatch corrects itself, whereas the exonuclease subunit plays a passive role. Hence, our work provides unique insights into high-fidelity replication and establishes a new paradigm for the correction of misincorporated nucleotides. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_4141.map.gz emd_4141.map.gz | 9.7 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-4141-v30.xml emd-4141-v30.xml emd-4141.xml emd-4141.xml | 27.4 KB 27.4 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_4141_fsc.xml emd_4141_fsc.xml | 5 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_4141.png emd_4141.png | 105.8 KB | ||
| マスクデータ |  emd_4141_msk_1.map emd_4141_msk_1.map | 10.5 MB |  マスクマップ マスクマップ | |
| Filedesc metadata |  emd-4141.cif.gz emd-4141.cif.gz | 7.9 KB | ||
| その他 |  emd_4141_half_map_1.map.gz emd_4141_half_map_1.map.gz emd_4141_half_map_2.map.gz emd_4141_half_map_2.map.gz | 7.9 MB 7.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-4141 http://ftp.pdbj.org/pub/emdb/structures/EMD-4141 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4141 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-4141 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_4141_validation.pdf.gz emd_4141_validation.pdf.gz | 447.7 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_4141_full_validation.pdf.gz emd_4141_full_validation.pdf.gz | 446.8 KB | 表示 | |
| XML形式データ |  emd_4141_validation.xml.gz emd_4141_validation.xml.gz | 10.5 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4141 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4141 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4141 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-4141 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_4141.map.gz / 形式: CCP4 / 大きさ: 10.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_4141.map.gz / 形式: CCP4 / 大きさ: 10.5 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Main map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.76 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
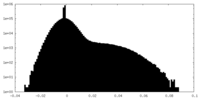
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_4141_msk_1.map emd_4141_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
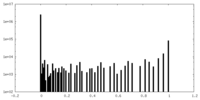
| 密度ヒストグラム |
-ハーフマップ: half map for main map
| ファイル | emd_4141_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map for main map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
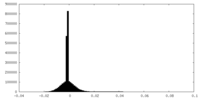
| 密度ヒストグラム |
-ハーフマップ: half map for main map
| ファイル | emd_4141_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | half map for main map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
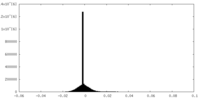
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : DNA polymerase III alpha, beta, epsilon, theta complex with misma...
| 全体 | 名称: DNA polymerase III alpha, beta, epsilon, theta complex with mismatched DNA duplex |
|---|---|
| 要素 |
|
-超分子 #1: DNA polymerase III alpha, beta, epsilon, theta complex with misma...
| 超分子 | 名称: DNA polymerase III alpha, beta, epsilon, theta complex with mismatched DNA duplex タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#6 |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 250 KDa |
-超分子 #2: DNA polymerase III alpha, beta, epsilon, theta complex with misma...
| 超分子 | 名称: DNA polymerase III alpha, beta, epsilon, theta complex with mismatched DNA duplex タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1-#3, #6 詳細: Map obtained after signal subtraction of the beta subunit and alignment of the remaining parts. Final reconstruction obtained with non-subtracted images and angles from local alignment |
|---|---|
| 由来(天然) | 生物種:  |
-超分子 #3: mismatched DNA duplex
| 超分子 | 名称: mismatched DNA duplex / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #4-#5 |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
-分子 #1: DNA polymerase III subunit alpha
| 分子 | 名称: DNA polymerase III subunit alpha / タイプ: protein_or_peptide / ID: 1 / コピー数: 1 / 光学異性体: LEVO / EC番号: DNA-directed DNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 103.554422 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSEPRFVHLR VHSDYSMIDG LAKTAPLVKK AAALGMPALA ITDFTNLCGL VKFYGAGHGA GIKPIVGADF NVQCDLLGDE LTHLTVLAA NNTGYQNLTL LISKAYQRGY GAAGPIIDRD WLIELNEGLI LLSGGRMGDV GRSLLRGNSA LVDECVAFYE E HFPDRYFL ...文字列: MSEPRFVHLR VHSDYSMIDG LAKTAPLVKK AAALGMPALA ITDFTNLCGL VKFYGAGHGA GIKPIVGADF NVQCDLLGDE LTHLTVLAA NNTGYQNLTL LISKAYQRGY GAAGPIIDRD WLIELNEGLI LLSGGRMGDV GRSLLRGNSA LVDECVAFYE E HFPDRYFL ELIRTGRPDE ESYLHAAVEL AEARGLPVVA TNDVRFIDSS DFDAHEIRVA IHDGFTLDDP KRPRNYSPQQ YM RSEEEMC ELFADIPEAL ANTVEIAKRC NVTVRLGEYF LPQFPTGDMS TEDYLVKRAK EGLEERLAFL FPDEEERLKR RPE YDERLE TELQVINQMG FPGYFLIVME FIQWSKDNGV PVGPGRGSGA GSLVAYALKI TDLDPLEFDL LFERFLNPER VSMP DFDVD FCMEKRDQVI EHVADMYGRD AVSQIITFGT MAAKAVIRDV GRVLGHPYGF VDRISKLIPP DPGMTLAKAF EAEPQ LPEI YEADEEVKAL IDMARKLEGV TRNAGKHAGG VVIAPTKITD FAPLYCDEEG KHPVTQFDKS DVEYAGLVKF DFLGLR TLT IINWALEMIN KRRAKNGEPP LDIAAIPLDD KKSFDMLQRS ETTAVFQLES RGMKDLIKRL QPDCFEDMIA LVALFRP GP LQSGMVDNFI DRKHGREEIS YPDVQWQHES LKPVLEPTYG IILYQEQVMQ IAQVLSGYTL GGADMLRRAM GKKKPEEM A KQRSVFAEGA EKNGINAELA MKIFDLVEKF AGYGFNKSHS AAYALVSYQT LWLKAHYPAE FMAAVMTADM DNTEKVVGL VDECWRMGLK ILPPDINSGL YHFHVNDDGE IVYGIGAIKG VGEGPIEAII EARNKGGYFR ELFDLCARTD TKKLNRRVLE KLIMSGAFD RLGPHRAALM NSLGDALKAA DQHAKAEAIG QLDLFGVL UniProtKB: DNA polymerase III subunit alpha |
-分子 #2: DNA polymerase III subunit beta
| 分子 | 名称: DNA polymerase III subunit beta / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO / EC番号: DNA-directed DNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 40.630508 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MKFTVEREHL LKPLQQVSGP LGGRPTLPIL GNLLLQVADG TLSLTGTDLE MEMVARVALV QPHEPGATTV PARKFFDICR GLPEGAEIA VQLEGERMLV RSGRSRFSLS TLPAADFPNL DDWQSEVEFT LPQATMKRLI EATQFSMAHQ DVRYYLNGML F ETEGEELR ...文字列: MKFTVEREHL LKPLQQVSGP LGGRPTLPIL GNLLLQVADG TLSLTGTDLE MEMVARVALV QPHEPGATTV PARKFFDICR GLPEGAEIA VQLEGERMLV RSGRSRFSLS TLPAADFPNL DDWQSEVEFT LPQATMKRLI EATQFSMAHQ DVRYYLNGML F ETEGEELR TVATDGHRLA VCSMPIGQSL PSHSVIVPRK GVIELMRMLD GGDNPLRVQI GSNNIRAHVG DFIFTSKLVD GR FPDYRRV LPKNPDKHLE AGCDLLKQAF ARAAILSNEK FRGVRLYVSE NQLKITANNP EQEEAEEILD VTYSGAEMEI GFN VSYVLD VLNALKCENV RMMLTDSVSS VQIEDAASQS AAYVVMPMRL UniProtKB: Large ribosomal subunit protein bL34 |
-分子 #3: DNA polymerase III subunit epsilon
| 分子 | 名称: DNA polymerase III subunit epsilon / タイプ: protein_or_peptide / ID: 3 / コピー数: 1 / 光学異性体: LEVO / EC番号: DNA-directed DNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 27.118984 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: MSTAITRQIV LDTETTGMNQ IGAHYEGHKI IEIGAVEVVN RRLTGNNFHV YLKPDRLVDP EAFGVHGIAD EFLLDKPTFA EVADEFMDY IRGAELVIHN AAFDIGFMDY EFSLLKRDIP KTNTFCKVTD SLAVARKMFP GKRNSLDALC ARYEIDNSKR T LHGALLDA ...文字列: MSTAITRQIV LDTETTGMNQ IGAHYEGHKI IEIGAVEVVN RRLTGNNFHV YLKPDRLVDP EAFGVHGIAD EFLLDKPTFA EVADEFMDY IRGAELVIHN AAFDIGFMDY EFSLLKRDIP KTNTFCKVTD SLAVARKMFP GKRNSLDALC ARYEIDNSKR T LHGALLDA QILAEVYLAM TGGQLSLPLA MEGETQQQQG EATIQRIVRQ ASKLRVVFAT DEEIAAHEAR LDLVQKKGGS CL WRA UniProtKB: DNA polymerase III subunit epsilon |
-分子 #6: DNA polymerase III subunit theta
| 分子 | 名称: DNA polymerase III subunit theta / タイプ: protein_or_peptide / ID: 6 / コピー数: 1 / 光学異性体: LEVO / EC番号: DNA-directed DNA polymerase |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 6.503385 KDa |
| 組換発現 | 生物種:  |
| 配列 | 文字列: QTEMDKVNVD LAAAGVAFKE RYNMPVIAEA VEREQPEHLR SWFRERLIAH RLASVN UniProtKB: DNA polymerase III subunit theta |
-分子 #4: DNA Primer Strand
| 分子 | 名称: DNA Primer Strand / タイプ: dna / ID: 4 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 5.275448 KDa |
| 配列 | 文字列: (DT)(DA)(DG)(DT)(DA)(DC)(DT)(DA)(DG)(DG) (DA)(DC)(DG)(DA)(DA)(DG)(DT) |
-分子 #5: DNA Template Strand
| 分子 | 名称: DNA Template Strand / タイプ: dna / ID: 5 / コピー数: 1 / 分類: DNA |
|---|---|
| 由来(天然) | 生物種: synthetic construct (人工物) |
| 分子量 | 理論値: 6.718339 KDa |
| 配列 | 文字列: (DG)(DG)(DA)(DG)(DT)(DC)(DC)(DT)(DT)(DC) (DG)(DT)(DC)(DC)(DT)(DA)(DG)(DT)(DA)(DC) (DT)(DA) |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.25 mg/mL | ||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.5 構成要素:
| ||||||||||
| グリッド | モデル: Quantifoil R1.2/1.3 / 材質: COPPER / メッシュ: 300 / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 60 sec. / 前処理 - 雰囲気: AIR | ||||||||||
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 277 K / 装置: FEI VITROBOT MARK IV 詳細: Prior to sample preparation 0.1 volumes of 0.05% Tween 20 were added to the sample 3 microliters were pipetted onto the grid and blotted for 4 seconds. | ||||||||||
| 詳細 | Sample was run over a gel filtration column prior to vitrification |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 温度 | 最低: 80.0 K / 最高: 80.0 K |
| 特殊光学系 | エネルギーフィルター - 名称: GIF Quantum エネルギーフィルター - エネルギー下限: 0 eV エネルギーフィルター - エネルギー上限: 20 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / デジタル化 - サイズ - 横: 3710 pixel / デジタル化 - サイズ - 縦: 3710 pixel / デジタル化 - 画像ごとのフレーム数: 1-20 / 撮影したグリッド数: 3 / 実像数: 1157 / 平均露光時間: 25.0 sec. / 平均電子線量: 2.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 倍率(補正後): 79545 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 3.5 µm / 最小 デフォーカス(公称値): 1.8 µm / 倍率(公称値): 64000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 詳細 | The cryo-EM structure of the PolIIIalpha-clamp-exonuclease complex in the polymerase mode (PDB code: 5FKW) was used as a starting model, and the NMR structure of theta bound to the exonuclease catalytic domain (PDB code: 2XY8) was used to place theta into the cryo-EM map. The model was manually adjusted in Coot and geometry of the protein optimized in Refmac5 using DNA-specific restraints generated in LibG |
|---|---|
| 精密化 | プロトコル: OTHER |
| 得られたモデル |  PDB-5m1s: |
 ムービー
ムービー コントローラー
コントローラー
















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)