+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-3048 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Structure of a partial yeast 48S preinitiation complex in closed conformation | |||||||||
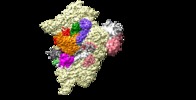
 マップデータ マップデータ | To see a continuous density for factors eIF1, eIF2, mRNA, entire tRNA and eIF3 at the 40S subunit interface, apply a Gaussian filtering of 1.34 and a contour level of 0.025. To see a continuous density for the PCI domain of eIF3, apply a Gaussian filtering of 2.5 and a contour level of 0.008. | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | Eukaryotic translation initiation / 48S / small ribosome subunit. | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報formation of translation initiation ternary complex / Cellular response to mitochondrial stress / Recycling of eIF2:GDP / eukaryotic translation initiation factor 3 complex, eIF3e / ABC-family proteins mediated transport / eukaryotic translation initiation factor 3 complex, eIF3m / methionyl-initiator methionine tRNA binding / incipient cellular bud site / translation reinitiation / eukaryotic translation initiation factor 2 complex ...formation of translation initiation ternary complex / Cellular response to mitochondrial stress / Recycling of eIF2:GDP / eukaryotic translation initiation factor 3 complex, eIF3e / ABC-family proteins mediated transport / eukaryotic translation initiation factor 3 complex, eIF3m / methionyl-initiator methionine tRNA binding / incipient cellular bud site / translation reinitiation / eukaryotic translation initiation factor 2 complex / eukaryotic translation initiation factor 3 complex / formation of cytoplasmic translation initiation complex / cytoplasmic translational initiation / multi-eIF complex / protein-synthesizing GTPase / eukaryotic 43S preinitiation complex / formation of translation preinitiation complex / eukaryotic 48S preinitiation complex / positive regulation of translational fidelity / Formation of the ternary complex, and subsequently, the 43S complex / Translation initiation complex formation / Ribosomal scanning and start codon recognition / Formation of a pool of free 40S subunits / L13a-mediated translational silencing of Ceruloplasmin expression / ribosomal small subunit binding / endonucleolytic cleavage to generate mature 3'-end of SSU-rRNA from (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / 90S preribosome / regulation of translational fidelity / translation regulator activity / endonucleolytic cleavage in ITS1 to separate SSU-rRNA from 5.8S rRNA and LSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / translation initiation factor binding / translation initiation factor activity / rescue of stalled ribosome / maturation of SSU-rRNA from tricistronic rRNA transcript (SSU-rRNA, 5.8S rRNA, LSU-rRNA) / maturation of SSU-rRNA / small-subunit processome / translational initiation / protein kinase C binding / maintenance of translational fidelity / positive regulation of apoptotic signaling pathway / cytoplasmic stress granule / modification-dependent protein catabolic process / rRNA processing / protein tag activity / double-stranded RNA binding / ribosomal small subunit biogenesis / small ribosomal subunit rRNA binding / ribosome binding / ribosomal small subunit assembly / small ribosomal subunit / cytosolic small ribosomal subunit / cytosolic large ribosomal subunit / cytoplasmic translation / rRNA binding / ribosome / protein ubiquitination / structural constituent of ribosome / ribonucleoprotein complex / translation / positive regulation of protein phosphorylation / GTPase activity / mRNA binding / ubiquitin protein ligase binding / GTP binding / nucleolus / protein kinase binding / RNA binding / zinc ion binding / identical protein binding / nucleus / metal ion binding / cytosol / cytoplasm 類似検索 - 分子機能 | |||||||||
| 生物種 |  Kluyveromyces lactis (酵母) / Kluyveromyces lactis (酵母) /  | |||||||||
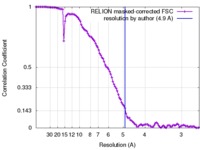
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 4.9 Å | |||||||||
 データ登録者 データ登録者 | Llacer JL / Hussain T / Ramakrishnan V | |||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2015 ジャーナル: Mol Cell / 年: 2015タイトル: Conformational Differences between Open and Closed States of the Eukaryotic Translation Initiation Complex. 著者: Jose L Llácer / Tanweer Hussain / Laura Marler / Colin Echeverría Aitken / Anil Thakur / Jon R Lorsch / Alan G Hinnebusch / V Ramakrishnan /   要旨: Translation initiation in eukaryotes begins with the formation of a pre-initiation complex (PIC) containing the 40S ribosomal subunit, eIF1, eIF1A, eIF3, ternary complex (eIF2-GTP-Met-tRNAi), and ...Translation initiation in eukaryotes begins with the formation of a pre-initiation complex (PIC) containing the 40S ribosomal subunit, eIF1, eIF1A, eIF3, ternary complex (eIF2-GTP-Met-tRNAi), and eIF5. The PIC, in an open conformation, attaches to the 5' end of the mRNA and scans to locate the start codon, whereupon it closes to arrest scanning. We present single particle cryo-electron microscopy (cryo-EM) reconstructions of 48S PICs from yeast in these open and closed states, at 6.0 Å and 4.9 Å, respectively. These reconstructions show eIF2β as well as a configuration of eIF3 that appears to encircle the 40S, occupying part of the subunit interface. Comparison of the complexes reveals a large conformational change in the 40S head from an open mRNA latch conformation to a closed one that constricts the mRNA entry channel and narrows the P site to enclose tRNAi, thus elucidating key events in start codon recognition. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
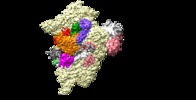
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_3048.map.gz emd_3048.map.gz | 96.5 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-3048-v30.xml emd-3048-v30.xml emd-3048.xml emd-3048.xml | 18.5 KB 18.5 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_3048_fsc.xml emd_3048_fsc.xml | 10.6 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  EMD-3048.png EMD-3048.png emd_3048.png emd_3048.png | 420.6 KB 420.6 KB | ||
| その他 |  emd_3048_half_map_1.map.gz emd_3048_half_map_1.map.gz emd_3048_half_map_2.map.gz emd_3048_half_map_2.map.gz | 80.9 MB 80.9 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-3048 http://ftp.pdbj.org/pub/emdb/structures/EMD-3048 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3048 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-3048 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_3048_validation.pdf.gz emd_3048_validation.pdf.gz | 437.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_3048_full_validation.pdf.gz emd_3048_full_validation.pdf.gz | 436.7 KB | 表示 | |
| XML形式データ |  emd_3048_validation.xml.gz emd_3048_validation.xml.gz | 11.3 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3048 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3048 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3048 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-3048 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_3048.map.gz / 形式: CCP4 / 大きさ: 100.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_3048.map.gz / 形式: CCP4 / 大きさ: 100.6 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | To see a continuous density for factors eIF1, eIF2, mRNA, entire tRNA and eIF3 at the 40S subunit interface, apply a Gaussian filtering of 1.34 and a contour level of 0.025. To see a continuous density for the PCI domain of eIF3, apply a Gaussian filtering of 2.5 and a contour level of 0.008. | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.34 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-添付マップデータ: emd 3048 half map 1.map
| ファイル | emd_3048_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-添付マップデータ: emd 3048 half map 2.map
| ファイル | emd_3048_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Partial yeast 48S preinitiation complex
| 全体 | 名称: Partial yeast 48S preinitiation complex |
|---|---|
| 要素 |
|
-超分子 #1000: Partial yeast 48S preinitiation complex
| 超分子 | 名称: Partial yeast 48S preinitiation complex / タイプ: sample / ID: 1000 / 集合状態: 1 / Number unique components: 7 |
|---|---|
| 分子量 | 理論値: 1.75 MDa |
-超分子 #1: Ribosome small subunit
| 超分子 | 名称: Ribosome small subunit / タイプ: complex / ID: 1 / Name.synonym: 40S / 組換発現: No / Ribosome-details: ribosome-eukaryote: SSU 40S, SSU RNA 18S |
|---|---|
| 由来(天然) | 生物種:  Kluyveromyces lactis (酵母) Kluyveromyces lactis (酵母) |
| 分子量 | 理論値: 1.2 MDa |
-分子 #1: Eukaryotic initiation factor 1
| 分子 | 名称: Eukaryotic initiation factor 1 / タイプ: protein_or_peptide / ID: 1 / Name.synonym: eIF1 / コピー数: 1 / 集合状態: Monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 12.3 KDa |
| 組換発現 | 生物種:  |
| 配列 | UniProtKB: Eukaryotic translation initiation factor eIF-1 |
-分子 #2: Eukaryotic initiation factor 1A
| 分子 | 名称: Eukaryotic initiation factor 1A / タイプ: protein_or_peptide / ID: 2 / Name.synonym: eIF1A / コピー数: 1 / 集合状態: Monomer / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 17.4 KDa |
| 組換発現 | 生物種:  |
| 配列 | UniProtKB: Eukaryotic translation initiation factor 1A |
-分子 #3: Eukaryotic initiation factor 2
| 分子 | 名称: Eukaryotic initiation factor 2 / タイプ: protein_or_peptide / ID: 3 / Name.synonym: eIF2 詳細: Uniprot codes are: alpha-P20459 beta-P09064 gamma-P32481 コピー数: 1 / 集合状態: Three subunits, alpha, beta, gamma / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 124 KDa |
| 組換発現 | 生物種:  |
-分子 #4: Eukaryotic initiation factor 3
| 分子 | 名称: Eukaryotic initiation factor 3 / タイプ: protein_or_peptide / ID: 4 / Name.synonym: eIF3 詳細: Uniprot codes are: 3a-P38249, 3b-P06103, 3c-P32497, 3g-A6ZZ25, 3i-P40217 コピー数: 1 / 集合状態: Five subunits, 3a, 3b, 3c, 3g, 3i / 組換発現: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 395 KDa |
| 組換発現 | 生物種:  |
-分子 #5: Initiator transfer RNA
| 分子 | 名称: Initiator transfer RNA / タイプ: rna / ID: 5 / Name.synonym: Met-tRNAi 詳細: Doble mutation (G31U:C39A) when compared with yeast WT initiator tRNA. 分類: TRANSFER / Structure: SINGLE STRANDED / Synthetic?: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 23 KDa |
| 配列 | 文字列: AGCGCCGUGG CGCAGUGGAA GCGCGCAGGU CUCAUAAACC UGAUGUCCUC GGAUCGAAAC CGAGCGGCGC UACCA |
-分子 #6: Messenger RNA
| 分子 | 名称: Messenger RNA / タイプ: rna / ID: 6 / Name.synonym: mRNA / 分類: OTHER / Structure: SINGLE STRANDED / Synthetic?: Yes |
|---|---|
| 由来(天然) | 生物種:  |
| 分子量 | 理論値: 7.4 KDa |
| 配列 | 文字列: GGAAUCUCUC UCUAUGCUCU CUCUC |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 0.17 mg/mL |
|---|---|
| 緩衝液 | pH: 6.5 詳細: 20mM MES-KOH, 40mM K-acetate, 10mM NH4-acetate, 8mM Mg-acetate, 2mM DTT |
| グリッド | 詳細: Quantifoil R2/2 400 mesh copper grids with 4-5 nm thin carbon on top |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / チャンバー内温度: 120 K / 装置: FEI VITROBOT MARK I / Timed resolved state: 30 second incubation time / 手法: Blot for 2.5-3 seconds before plunging |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| アライメント法 | Legacy - 非点収差: Objective lens astigmatism was corrected at 59,000 times magnification |
| 詳細 | Complete dataset was collected in 4 non-consecutive sessions |
| 日付 | 2014年7月4日 |
| 撮影 | カテゴリ: CCD フィルム・検出器のモデル: FEI FALCON II (4k x 4k) 実像数: 5500 / 平均電子線量: 27 e/Å2 詳細: Complete dataset was collected in 4 non-consecutive sessions |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 倍率(補正後): 104478 / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 4.0 µm / 最小 デフォーカス(公称値): 1.5 µm / 倍率(公称値): 78000 |
| 試料ステージ | 試料ホルダーモデル: GATAN LIQUID NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
-原子モデル構築 1
| 初期モデル | PDB ID: Chain - Chain ID: 2 |
|---|---|
| ソフトウェア | 名称: Chimera, Coot, Refmac |
| 精密化 | 空間: RECIPROCAL / プロトコル: FLEXIBLE FIT / 当てはまり具合の基準: R-factor, FSC |
| 得られたモデル |  PDB-3jap: |
-原子モデル構築 2
| 初期モデル | PDB ID: Chain - Chain ID: K |
|---|---|
| ソフトウェア | 名称: Chimera, Coot, Refmac |
| 精密化 | 空間: RECIPROCAL / プロトコル: FLEXIBLE FIT / 当てはまり具合の基準: R-factor, FSC |
| 得られたモデル |  PDB-3jap: |
-原子モデル構築 3
| 初期モデル | PDB ID: Chain - #0 - Chain ID: A / Chain - #1 - Chain ID: C |
|---|---|
| ソフトウェア | 名称: Chimera, Coot, Refmac |
| 精密化 | 空間: RECIPROCAL / プロトコル: FLEXIBLE FIT / 当てはまり具合の基準: R-factor, FSC |
| 得られたモデル |  PDB-3jap: |
-原子モデル構築 4
| 初期モデル | PDB ID: Chain - Chain ID: A |
|---|---|
| ソフトウェア | 名称: Chimera, Coot, Refmac |
| 精密化 | 空間: RECIPROCAL / プロトコル: FLEXIBLE FIT / 当てはまり具合の基準: R-factor, FSC |
| 得られたモデル |  PDB-3jap: |
 ムービー
ムービー コントローラー
コントローラー
































 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)