+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-30217 | |||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Cryo-EM structure of Mycobacterium smegmatis arabinosyltransferase EmbC2-AcpM2 in complex with ethambutol | |||||||||||||||
 マップデータ マップデータ | ||||||||||||||||
 試料 試料 |
| |||||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報indolylacetylinositol arabinosyltransferase / indolylacetylinositol arabinosyltransferase activity / arabinosyltransferase activity / Actinobacterium-type cell wall biogenesis / lipid A biosynthetic process / 転移酵素; グリコシル基を移すもの; 五炭糖残基を移すもの / acyl binding / acyl carrier activity / cell wall organization / plasma membrane / cytosol 類似検索 - 分子機能 | |||||||||||||||
| 生物種 |  Mycolicibacterium smegmatis MC2 155 (バクテリア) / Mycolicibacterium smegmatis MC2 155 (バクテリア) /  Mycolicibacterium smegmatis (strain ATCC 700084 / mc(2)155) (バクテリア) Mycolicibacterium smegmatis (strain ATCC 700084 / mc(2)155) (バクテリア) | |||||||||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 2.81 Å | |||||||||||||||
 データ登録者 データ登録者 | Zhang L / Zhao Y / Gao Y / Wang Q / Li J / Besra GS / Rao Z | |||||||||||||||
| 資金援助 |  中国, 中国,  英国, 4件 英国, 4件
| |||||||||||||||
 引用 引用 |  ジャーナル: Science / 年: 2020 ジャーナル: Science / 年: 2020タイトル: Structures of cell wall arabinosyltransferases with the anti-tuberculosis drug ethambutol. 著者: Lu Zhang / Yao Zhao / Yan Gao / Lijie Wu / Ruogu Gao / Qi Zhang / Yinan Wang / Chengyao Wu / Fangyu Wu / Sudagar S Gurcha / Natacha Veerapen / Sarah M Batt / Wei Zhao / Ling Qin / Xiuna Yang ...著者: Lu Zhang / Yao Zhao / Yan Gao / Lijie Wu / Ruogu Gao / Qi Zhang / Yinan Wang / Chengyao Wu / Fangyu Wu / Sudagar S Gurcha / Natacha Veerapen / Sarah M Batt / Wei Zhao / Ling Qin / Xiuna Yang / Manfu Wang / Yan Zhu / Bing Zhang / Lijun Bi / Xian'en Zhang / Haitao Yang / Luke W Guddat / Wenqing Xu / Quan Wang / Jun Li / Gurdyal S Besra / Zihe Rao /    要旨: The arabinosyltransferases EmbA, EmbB, and EmbC are involved in cell wall synthesis and are recognized as targets for the anti-tuberculosis drug ethambutol. In this study, we determined cryo- ...The arabinosyltransferases EmbA, EmbB, and EmbC are involved in cell wall synthesis and are recognized as targets for the anti-tuberculosis drug ethambutol. In this study, we determined cryo-electron microscopy and x-ray crystal structures of mycobacterial EmbA-EmbB and EmbC-EmbC complexes in the presence of their glycosyl donor and acceptor substrates and with ethambutol. These structures show how the donor and acceptor substrates bind in the active site and how ethambutol inhibits arabinosyltransferases by binding to the same site as both substrates in EmbB and EmbC. Most drug-resistant mutations are located near the ethambutol binding site. Collectively, our work provides a structural basis for understanding the biochemical function and inhibition of arabinosyltransferases and the development of new anti-tuberculosis agents. | |||||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_30217.map.gz emd_30217.map.gz | 167.8 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-30217-v30.xml emd-30217-v30.xml emd-30217.xml emd-30217.xml | 24.3 KB 24.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_30217.png emd_30217.png | 72.2 KB | ||
| マスクデータ |  emd_30217_msk_1.map emd_30217_msk_1.map | 178 MB |  マスクマップ マスクマップ | |
| その他 |  emd_30217_half_map_1.map.gz emd_30217_half_map_1.map.gz emd_30217_half_map_2.map.gz emd_30217_half_map_2.map.gz | 164.8 MB 164.8 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-30217 http://ftp.pdbj.org/pub/emdb/structures/EMD-30217 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30217 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-30217 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_30217_validation.pdf.gz emd_30217_validation.pdf.gz | 860.9 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_30217_full_validation.pdf.gz emd_30217_full_validation.pdf.gz | 860.5 KB | 表示 | |
| XML形式データ |  emd_30217_validation.xml.gz emd_30217_validation.xml.gz | 15.1 KB | 表示 | |
| CIF形式データ |  emd_30217_validation.cif.gz emd_30217_validation.cif.gz | 17.9 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30217 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30217 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30217 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-30217 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_30217.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_30217.map.gz / 形式: CCP4 / 大きさ: 178 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| ボクセルのサイズ | X=Y=Z: 0.82 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
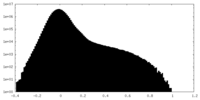
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-マスク #1
| ファイル |  emd_30217_msk_1.map emd_30217_msk_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
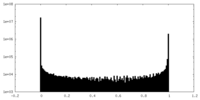
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #2
| ファイル | emd_30217_half_map_1.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
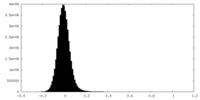
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
-ハーフマップ: #1
| ファイル | emd_30217_half_map_2.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
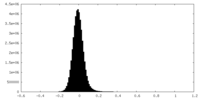
| 投影像・断面図 |
| ||||||||||||
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : Mycobacterium smegmatis arabinosyltransferase EmbC2-AcpM2 in comp...
| 全体 | 名称: Mycobacterium smegmatis arabinosyltransferase EmbC2-AcpM2 in complex with ethambutol |
|---|---|
| 要素 |
|
-超分子 #1: Mycobacterium smegmatis arabinosyltransferase EmbC2-AcpM2 in comp...
| 超分子 | 名称: Mycobacterium smegmatis arabinosyltransferase EmbC2-AcpM2 in complex with ethambutol タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|
-超分子 #2: EmbC
| 超分子 | 名称: EmbC / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Mycolicibacterium smegmatis MC2 155 (バクテリア) Mycolicibacterium smegmatis MC2 155 (バクテリア) |
| 組換発現 | 生物種:  Mycolicibacterium smegmatis MC2 155 (バクテリア) Mycolicibacterium smegmatis MC2 155 (バクテリア) |
-超分子 #3: AcpM
| 超分子 | 名称: AcpM / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|---|
| 由来(天然) | 生物種:  Mycolicibacterium smegmatis MC2 155 (バクテリア) Mycolicibacterium smegmatis MC2 155 (バクテリア) |
-分子 #1: Integral membrane indolylacetylinositol arabinosyltransferase EmbC
| 分子 | 名称: Integral membrane indolylacetylinositol arabinosyltransferase EmbC タイプ: protein_or_peptide / ID: 1 / コピー数: 2 / 光学異性体: LEVO / EC番号: indolylacetylinositol arabinosyltransferase |
|---|---|
| 由来(天然) | 生物種:  Mycolicibacterium smegmatis (strain ATCC 700084 / mc(2)155) (バクテリア) Mycolicibacterium smegmatis (strain ATCC 700084 / mc(2)155) (バクテリア)株: ATCC 700084 / mc(2)155 |
| 分子量 | 理論値: 116.878898 KDa |
| 組換発現 | 生物種:  Mycolicibacterium smegmatis MC2 155 (バクテリア) Mycolicibacterium smegmatis MC2 155 (バクテリア) |
| 配列 | 文字列: MTGPHAAGGS NHRTARLVAI IAGLLGTLMA IATPLLPVEQ TTAELNWPQN GVWQSVDAPL IGYVATDLTV TVPCQAAAGL VGPENRNRS VLLSTVPKQA PKAIDRGLLI ERINNDLTVI VRNTPVVSAP LEQVLSPDCR YLTFTAHADK VTGEFVGLTQ G PDDDDPGE ...文字列: MTGPHAAGGS NHRTARLVAI IAGLLGTLMA IATPLLPVEQ TTAELNWPQN GVWQSVDAPL IGYVATDLTV TVPCQAAAGL VGPENRNRS VLLSTVPKQA PKAIDRGLLI ERINNDLTVI VRNTPVVSAP LEQVLSPDCR YLTFTAHADK VTGEFVGLTQ G PDDDDPGE AVRGERSGYD FRPQIVGVFT DLSGPAPEGL QLSATIDTRY STSPTLLKLL AMIVGVAMTV IALGALHVLD CA DGRRHKR FLPSRWWSMT PLDGLVSAML VWWHFVGANT ADDGYILTMA RVSEHAGYMA NYYRWFGTPE SPFGWYYDLL ALW AHVSTA SVWMRFPTLL MGLACWWVIS REVIPRLGAA AKHSRAAAWT AAGLFLAFWL PLNNGLRPEP IIALGILLTW CSVE RGVAT SRLLPVAVAI IIGALTLFSG PTGIAAVGAL LVAIGPLKTI VAAHVSRFGY WALLAPIAAA GTVTIFLIFR DQTLA AELQ ASSFKSAVGP SLAWFDEHIR YSRLFTTSPD GSVARRFAVL TLLLALAVSI AMTLRKGRIP GTALGPSRRI IGITII SFL AMMFTPTKWT HHFGVFAGLA GCLGALAAVA VTTTAMKSRR NRTVFGAAVL FVTALSFATV NGWWYVSNFG VPWSNSF PE FKFGFTTMLL GLSVLALLVA AWFHFSGRDV SPDRPQRRWQ RLLVAPLAVA TWALVIFEVV SLTLGMINQY PAWSVGRS N LNALTGKTCG LANDVLVEQN ANAGMLTPIG EPAGQALGAV TSLGFGPNGI PSDVSADPVM EQPGTDNFAD SDSGVVTGT EVGTEGGTTA AAGINGSRAR LPYGLNPATT PVLGSWRSGT QQPAVLRSAW YRLPDRDQAG PLLVVSAAGR FDQGEVEVQW ATDEQAAAN EPGGSITFGD VGAAPAWRNL RAPLSSIPPE ATQIRLVASD DDLAPQHWIA LTPPRIPELR TLQEVVGSSD P VMLDWLVG LAFPCQRPFD HRYGVVEVPK WRILPDRFGA EANSPVMDYL GGGPLGITEL LLRPSSVPTY LKDDWYRDWG SL QRLTPWY PDAQPARLDL GTATRSGWWS PAPLRLSHHH HHHHHHH |
-分子 #2: Meromycolate extension acyl carrier protein
| 分子 | 名称: Meromycolate extension acyl carrier protein / タイプ: protein_or_peptide / ID: 2 / コピー数: 2 / 光学異性体: LEVO |
|---|---|
| 由来(天然) | 生物種:  Mycolicibacterium smegmatis MC2 155 (バクテリア) Mycolicibacterium smegmatis MC2 155 (バクテリア) |
| 分子量 | 理論値: 10.743876 KDa |
| 配列 | 文字列: MAATQEEIIA GLAEIIEEVT GIEPSEVTPE KSFVDDLDID SLSMVEIAVQ TEDKYGVKIP DEDLAGLRTV GDVVAYIQKL EEENPEAAA ALREKFAADQ |
-分子 #3: CALCIUM ION
| 分子 | 名称: CALCIUM ION / タイプ: ligand / ID: 3 / コピー数: 2 / 式: CA |
|---|---|
| 分子量 | 理論値: 40.078 Da |
-分子 #4: PHOSPHATE ION
| 分子 | 名称: PHOSPHATE ION / タイプ: ligand / ID: 4 / コピー数: 2 / 式: PO4 |
|---|---|
| 分子量 | 理論値: 94.971 Da |
| Chemical component information |  ChemComp-PO4: |
-分子 #5: Ethambutol
| 分子 | 名称: Ethambutol / タイプ: ligand / ID: 5 / コピー数: 2 / 式: 95E |
|---|---|
| 分子量 | 理論値: 204.31 Da |
| Chemical component information | 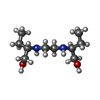 ChemComp-95E: |
-分子 #6: N~3~-[(2S)-2-hydroxy-3,3-dimethyl-4-(phosphonooxy)butanoyl]-N-(2-...
| 分子 | 名称: N~3~-[(2S)-2-hydroxy-3,3-dimethyl-4-(phosphonooxy)butanoyl]-N-(2-sulfanylethyl)-beta-alaninamide タイプ: ligand / ID: 6 / コピー数: 2 / 式: PN7 |
|---|---|
| 分子量 | 理論値: 358.348 Da |
| Chemical component information |  ChemComp-PN7: |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 濃度 | 5 mg/mL | ||||||||
|---|---|---|---|---|---|---|---|---|---|
| 緩衝液 | pH: 7.4 / 構成要素:
| ||||||||
| 凍結 | 凍結剤: ETHANE | ||||||||
| 詳細 | The sample was monodisperse. |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 温度 | 最低: 78.5 K / 最高: 78.6 K |
| アライメント法 | Coma free - Residual tilt: 10.0 mrad |
| 撮影 | フィルム・検出器のモデル: GATAN K3 (6k x 4k) / 撮影したグリッド数: 2 / 実像数: 5100 / 平均露光時間: 2.0 sec. / 平均電子線量: 50.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 50.0 µm / 最大 デフォーカス(補正後): 2.0 µm / 最小 デフォーカス(補正後): 1.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 2.0 µm / 最小 デフォーカス(公称値): 1.0 µm / 倍率(公称値): 29000 |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER ホルダー冷却材: NITROGEN |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
+ 画像解析
画像解析
-原子モデル構築 1
| 精密化 | プロトコル: RIGID BODY FIT / 温度因子: 62.01 / 当てはまり具合の基準: correlation coefficient |
|---|---|
| 得られたモデル |  PDB-7bve: |
 ムービー
ムービー コントローラー
コントローラー

















 Z
Z Y
Y X
X