登録情報 データベース : EMDB / ID : EMD-21853タイトル E. coli RNAPs70-SspA-gadA DNA complex E. coli RNAPs70-SspA-gadA DNA unsharpened map 複合体 : E. coli RNAPs70SspA-gadA DNA complexタンパク質・ペプチド : x 6種DNA : x 4種リガンド : x 2種 / 機能・相同性 分子機能 ドメイン・相同性 構成要素
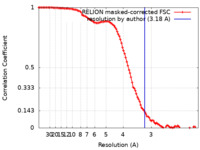
/ / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / / 生物種 Escherichia coli (大腸菌) / Escherichia coli TA054 (大腸菌)手法 / / 解像度 : 3.18 Å Travis BA / Brennan RG 資金援助 Organization Grant number 国 National Institutes of Health/National Institute of General Medical Sciences (NIH/NIGMS) R35GM130290
ジャーナル : Mol Cell / 年 : 2021タイトル : Structural Basis for Virulence Activation of Francisella tularensis.著者 : Brady A Travis / Kathryn M Ramsey / Samantha M Prezioso / Thomas Tallo / Jamie M Wandzilak / Allen Hsu / Mario Borgnia / Alberto Bartesaghi / Simon L Dove / Richard G Brennan / Maria A Schumacher / 要旨 : The bacterium Francisella tularensis (Ft) is one of the most infectious agents known. Ft virulence is controlled by a unique combination of transcription regulators: the MglA-SspA heterodimer, PigR, ... The bacterium Francisella tularensis (Ft) is one of the most infectious agents known. Ft virulence is controlled by a unique combination of transcription regulators: the MglA-SspA heterodimer, PigR, and the stress signal, ppGpp. MglA-SspA assembles with the σ-associated RNAP holoenzyme (RNAPσ), forming a virulence-specialized polymerase. These factors activate Francisella pathogenicity island (FPI) gene expression, which is required for virulence, but the mechanism is unknown. Here we report FtRNAPσ-promoter-DNA, FtRNAPσ-(MglA-SspA)-promoter DNA, and FtRNAPσ-(MglA-SspA)-ppGpp-PigR-promoter DNA cryo-EM structures. Structural and genetic analyses show MglA-SspA facilitates σ binding to DNA to regulate virulence and virulence-enhancing genes. Our Escherichia coli RNAPσhomodimeric EcSspA structure suggests this is a general SspA-transcription regulation mechanism. Strikingly, our FtRNAPσ-(MglA-SspA)-ppGpp-PigR-DNA structure reveals ppGpp binding to MglA-SspA tethers PigR to promoters. PigR in turn recruits FtRNAP αCTDs to DNA UP elements. Thus, these studies unveil a unique mechanism for Ft pathogenesis involving a virulence-specialized RNAP that employs two (MglA-SspA)-based strategies to activate virulence genes. 履歴 登録 2020年4月21日 - ヘッダ(付随情報) 公開 2020年11月11日 - マップ公開 2020年11月11日 - 更新 2024年3月6日 - 現状 2024年3月6日 処理サイト : RCSB / 状態 : 公開
すべて表示 表示を減らす
 データを開く
データを開く 基本情報
基本情報 マップデータ
マップデータ 試料
試料 キーワード
キーワード 機能・相同性情報
機能・相同性情報

 データ登録者
データ登録者 米国, 1件
米国, 1件  引用
引用 ジャーナル: Mol Cell / 年: 2021
ジャーナル: Mol Cell / 年: 2021
 構造の表示
構造の表示 ムービービューア
ムービービューア SurfView
SurfView Molmil
Molmil Jmol/JSmol
Jmol/JSmol ダウンロードとリンク
ダウンロードとリンク emd_21853.map.gz
emd_21853.map.gz EMDBマップデータ形式
EMDBマップデータ形式 emd-21853-v30.xml
emd-21853-v30.xml emd-21853.xml
emd-21853.xml EMDBヘッダ
EMDBヘッダ emd_21853_fsc.xml
emd_21853_fsc.xml FSCデータファイル
FSCデータファイル emd_21853.png
emd_21853.png emd-21853.cif.gz
emd-21853.cif.gz emd_21853_additional_1.map.gz
emd_21853_additional_1.map.gz http://ftp.pdbj.org/pub/emdb/structures/EMD-21853
http://ftp.pdbj.org/pub/emdb/structures/EMD-21853 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21853
ftp://ftp.pdbj.org/pub/emdb/structures/EMD-21853 emd_21853_validation.pdf.gz
emd_21853_validation.pdf.gz EMDB検証レポート
EMDB検証レポート emd_21853_full_validation.pdf.gz
emd_21853_full_validation.pdf.gz emd_21853_validation.xml.gz
emd_21853_validation.xml.gz emd_21853_validation.cif.gz
emd_21853_validation.cif.gz https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21853
https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21853 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21853
ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-21853 リンク
リンク EMDB (EBI/PDBe) /
EMDB (EBI/PDBe) /  EMDataResource
EMDataResource マップ
マップ ダウンロード / ファイル: emd_21853.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES)
ダウンロード / ファイル: emd_21853.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) 試料の構成要素
試料の構成要素 解析
解析 試料調製
試料調製 電子顕微鏡法
電子顕微鏡法 FIELD EMISSION GUN
FIELD EMISSION GUN
 画像解析
画像解析
 ムービー
ムービー コントローラー
コントローラー
























 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)