+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-7319 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | Mtb RNAP Holo/RbpA/Fidaxomicin/upstream fork DNA | |||||||||
 マップデータ マップデータ | primary map | |||||||||
 試料 試料 |
| |||||||||
 キーワード キーワード | RNA Polymerase / Antibiotic / Inhibitor / TRANSCRIPTION / transcription-dna-antibiotic complex | |||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報bacterial-type RNA polymerase holo enzyme binding / response to water / Antimicrobial action and antimicrobial resistance in Mtb / bacterial-type RNA polymerase core enzyme binding / sigma factor activity / DNA-directed RNA polymerase complex / peptidoglycan-based cell wall / DNA-templated transcription initiation / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity ...bacterial-type RNA polymerase holo enzyme binding / response to water / Antimicrobial action and antimicrobial resistance in Mtb / bacterial-type RNA polymerase core enzyme binding / sigma factor activity / DNA-directed RNA polymerase complex / peptidoglycan-based cell wall / DNA-templated transcription initiation / ribonucleoside binding / DNA-directed 5'-3' RNA polymerase activity / DNA-directed RNA polymerase / nucleic acid binding / protein dimerization activity / response to antibiotic / DNA-templated transcription / positive regulation of DNA-templated transcription / magnesium ion binding / DNA binding / zinc ion binding / plasma membrane / cytoplasm / cytosol 類似検索 - 分子機能 | |||||||||
| 生物種 |  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.38 Å | |||||||||
 データ登録者 データ登録者 | Darst SA / Campbell EA | |||||||||
 引用 引用 |  ジャーナル: Elife / 年: 2018 ジャーナル: Elife / 年: 2018タイトル: Fidaxomicin jams RNA polymerase motions needed for initiation via RbpA contacts. 著者: Hande Boyaci / James Chen / Mirjana Lilic / Margaret Palka / Rachel Anne Mooney / Robert Landick / Seth A Darst / Elizabeth A Campbell /  要旨: Fidaxomicin (Fdx) is an antimicrobial RNA polymerase (RNAP) inhibitor highly effective against RNAP in vitro, but clinical use of Fdx is limited to treating intestinal infections due to poor ...Fidaxomicin (Fdx) is an antimicrobial RNA polymerase (RNAP) inhibitor highly effective against RNAP in vitro, but clinical use of Fdx is limited to treating intestinal infections due to poor absorption. To identify the structural determinants of Fdx binding to RNAP, we determined the 3.4 Å cryo-electron microscopy structure of a complete RNAP holoenzyme in complex with Fdx. We find that the actinobacteria general transcription factor RbpA contacts fidaxomycin, explaining its strong effect on . Additional structures define conformational states of RNAP between the free apo-holoenzyme and the promoter-engaged open complex ready for transcription. The results establish that Fdx acts like a doorstop to jam the enzyme in an open state, preventing the motions necessary to secure promoter DNA in the active site. Our results provide a structural platform to guide development of anti-tuberculosis antimicrobials based on the Fdx binding pocket. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_7319.map.gz emd_7319.map.gz | 96.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-7319-v30.xml emd-7319-v30.xml emd-7319.xml emd-7319.xml | 22.3 KB 22.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| 画像 |  emd_7319.png emd_7319.png | 130.1 KB | ||
| Filedesc metadata |  emd-7319.cif.gz emd-7319.cif.gz | 8.3 KB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-7319 http://ftp.pdbj.org/pub/emdb/structures/EMD-7319 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7319 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-7319 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_7319_validation.pdf.gz emd_7319_validation.pdf.gz | 551.1 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_7319_full_validation.pdf.gz emd_7319_full_validation.pdf.gz | 550.7 KB | 表示 | |
| XML形式データ |  emd_7319_validation.xml.gz emd_7319_validation.xml.gz | 6.3 KB | 表示 | |
| CIF形式データ |  emd_7319_validation.cif.gz emd_7319_validation.cif.gz | 7.2 KB | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7319 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7319 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7319 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-7319 | HTTPS FTP |
-関連構造データ
| 関連構造データ |  6bzoMC  7320C  7322C  7323C  6c04C  6c05C  6c06C C: 同じ文献を引用 ( M: このマップから作成された原子モデル |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10887 (タイトル: CryoEM of Mycobacterium tuberculosis WT RNAP holoenzyme/RbpA/Fdx EMPIAR-10887 (タイトル: CryoEM of Mycobacterium tuberculosis WT RNAP holoenzyme/RbpA/FdxData size: 220.5 Data #1: Unaligned multi frame micrographs of M. tuberculosis RNAP/RbpA holoenzyme with Fdx [micrographs - multiframe])  EMPIAR-10896 (タイトル: CryoEM of Mycobacterium tuberculosis WT RNAP holoenzyme/RbpA EMPIAR-10896 (タイトル: CryoEM of Mycobacterium tuberculosis WT RNAP holoenzyme/RbpAData size: 838.9 Data #1: Unaligned multi-frame micrographs of M.tuberculosis RNAP holoenzyme with RbpA [micrographs - multiframe])  EMPIAR-10901 (タイトル: CryoEM of Mycobacterium tuberculosis WT RNAP holoenzyme/RbpA bound to the Fdx and upstream fork DNA EMPIAR-10901 (タイトル: CryoEM of Mycobacterium tuberculosis WT RNAP holoenzyme/RbpA bound to the Fdx and upstream fork DNAData size: 2.0 TB Data #1: Unaligned multiframe micrographs of M.tuberculosis RNAP holoenzyme with RbpA and inhibitor Fdx and upstream fork DNA [micrographs - multiframe] Data #2: Unaligned multiframe micrographs of M.tuberculosis RNAP holoenzyme with RbpA and inhibitor Fdx and upstream fork DNA [micrographs - multiframe]) |
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|---|
| 「今月の分子」の関連する項目 |
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_7319.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_7319.map.gz / 形式: CCP4 / 大きさ: 103 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | primary map | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 1.1 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
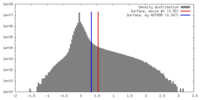
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
- 試料の構成要素
試料の構成要素
+全体 : Complex of Mtb RNAP with an antibiotic called fidaxomicin
+超分子 #1: Complex of Mtb RNAP with an antibiotic called fidaxomicin
+分子 #1: DNA-directed RNA polymerase subunit alpha
+分子 #2: DNA-directed RNA polymerase subunit beta
+分子 #3: DNA-directed RNA polymerase subunit beta'
+分子 #4: DNA-directed RNA polymerase subunit omega
+分子 #5: RNA polymerase sigma factor SigA
+分子 #6: RNA polymerase-binding protein RbpA
+分子 #7: DNA (32-MER)
+分子 #8: DNA (26-MER)
+分子 #9: Fidaxomicin
+分子 #10: ZINC ION
+分子 #11: MAGNESIUM ION
+分子 #12: water
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| グリッド | モデル: C-flat / 材質: GOLD / メッシュ: 400 / 支持フィルム - 材質: CARBON / 支持フィルム - トポロジー: HOLEY / 前処理 - タイプ: GLOW DISCHARGE / 前処理 - 時間: 20 sec. |
| 凍結 | 凍結剤: ETHANE / チャンバー内湿度: 100 % / 装置: FEI VITROBOT MARK IV |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | FEI TITAN KRIOS |
|---|---|
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 検出モード: COUNTING / 平均電子線量: 6.7 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | C2レンズ絞り径: 100.0 µm / 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD / Cs: 2.7 mm / 最大 デフォーカス(公称値): 1.8 µm / 最小 デフォーカス(公称値): 0.8 µm |
| 試料ステージ | 試料ホルダーモデル: FEI TITAN KRIOS AUTOGRID HOLDER |
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
- 画像解析
画像解析
| 初期モデル | モデルのタイプ: INSILICO MODEL |
|---|---|
| 最終 再構成 | 解像度のタイプ: BY AUTHOR / 解像度: 3.38 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 使用した粒子像数: 173509 |
| 初期 角度割当 | タイプ: ANGULAR RECONSTITUTION |
| 最終 角度割当 | タイプ: PROJECTION MATCHING |
 ムービー
ムービー コントローラー
コントローラー















 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)