+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: EMDB / ID: EMD-9399 | |||||||||
|---|---|---|---|---|---|---|---|---|---|---|
| タイトル | F-pilus/MS2 complex (Class 1 map with genome masked out) | |||||||||
 マップデータ マップデータ | Escherichia coli F-pilus and Enterobacteria phage MS2 complex. (Class 1 map with phage genome masked out). | |||||||||
 試料 試料 |
| |||||||||
| 生物種 |  Enterobacteria phage MS2 (ファージ) / Enterobacteria phage MS2 (ファージ) /  | |||||||||
| 手法 | 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 5.8 Å | |||||||||
 データ登録者 データ登録者 | Meng R / Jiang M / Zhang J | |||||||||
| 資金援助 |  米国, 2件 米国, 2件
| |||||||||
 引用 引用 |  ジャーナル: Nat Commun / 年: 2019 ジャーナル: Nat Commun / 年: 2019タイトル: Structural basis for the adsorption of a single-stranded RNA bacteriophage. 著者: Ran Meng / Mengqiu Jiang / Zhicheng Cui / Jeng-Yih Chang / Kailu Yang / Joanita Jakana / Xinzhe Yu / Zhao Wang / Bo Hu / Junjie Zhang /  要旨: Single-stranded RNA bacteriophages (ssRNA phages) infect Gram-negative bacteria via a single maturation protein (Mat), which attaches to a retractile pilus of the host. Here we present structures of ...Single-stranded RNA bacteriophages (ssRNA phages) infect Gram-negative bacteria via a single maturation protein (Mat), which attaches to a retractile pilus of the host. Here we present structures of the ssRNA phage MS2 in complex with the Escherichia coli F-pilus, showing a network of hydrophobic and electrostatic interactions at the Mat-pilus interface. Moreover, binding of the pilus induces slight orientational variations of the Mat relative to the rest of the phage capsid, priming the Mat-connected genomic RNA (gRNA) for its release from the virions. The exposed tip of the attached Mat points opposite to the direction of the pilus retraction, which may facilitate the translocation of the gRNA from the capsid into the host cytosol. In addition, our structures determine the orientation of the assembled F-pilin subunits relative to the cell envelope, providing insights into the F-like type IV secretion systems. | |||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | EMマップ:  SurfView SurfView Molmil Molmil Jmol/JSmol Jmol/JSmol |
| 添付画像 |
- ダウンロードとリンク
ダウンロードとリンク
-EMDBアーカイブ
| マップデータ |  emd_9399.map.gz emd_9399.map.gz | 4.6 MB |  EMDBマップデータ形式 EMDBマップデータ形式 | |
|---|---|---|---|---|
| ヘッダ (付随情報) |  emd-9399-v30.xml emd-9399-v30.xml emd-9399.xml emd-9399.xml | 13.3 KB 13.3 KB | 表示 表示 |  EMDBヘッダ EMDBヘッダ |
| FSC (解像度算出) |  emd_9399_fsc.xml emd_9399_fsc.xml | 7.7 KB | 表示 |  FSCデータファイル FSCデータファイル |
| 画像 |  emd_9399.png emd_9399.png | 233.6 KB | ||
| その他 |  emd_9399_additional.map.gz emd_9399_additional.map.gz | 4.7 MB | ||
| アーカイブディレクトリ |  http://ftp.pdbj.org/pub/emdb/structures/EMD-9399 http://ftp.pdbj.org/pub/emdb/structures/EMD-9399 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9399 ftp://ftp.pdbj.org/pub/emdb/structures/EMD-9399 | HTTPS FTP |
-検証レポート
| 文書・要旨 |  emd_9399_validation.pdf.gz emd_9399_validation.pdf.gz | 78.6 KB | 表示 |  EMDB検証レポート EMDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  emd_9399_full_validation.pdf.gz emd_9399_full_validation.pdf.gz | 77.7 KB | 表示 | |
| XML形式データ |  emd_9399_validation.xml.gz emd_9399_validation.xml.gz | 493 B | 表示 | |
| アーカイブディレクトリ |  https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9399 https://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9399 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9399 ftp://ftp.pdbj.org/pub/emdb/validation_reports/EMD-9399 | HTTPS FTP |
-関連構造データ
- リンク
リンク
| EMDBのページ |  EMDB (EBI/PDBe) / EMDB (EBI/PDBe) /  EMDataResource EMDataResource |
|---|
- マップ
マップ
| ファイル |  ダウンロード / ファイル: emd_9399.map.gz / 形式: CCP4 / 大きさ: 38.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) ダウンロード / ファイル: emd_9399.map.gz / 形式: CCP4 / 大きさ: 38.4 MB / タイプ: IMAGE STORED AS FLOATING POINT NUMBER (4 BYTES) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Escherichia coli F-pilus and Enterobacteria phage MS2 complex. (Class 1 map with phage genome masked out). | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 投影像・断面図 | 画像のコントロール
画像は Spider により作成 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| ボクセルのサイズ | X=Y=Z: 2.46 Å | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 密度 |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 空間群: 1 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 詳細 | EMDB XML:
CCP4マップ ヘッダ情報:
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
-添付データ
-追加マップ: Escherichia coli F-pilus and Enterobacteria phage MS2 complex....
| ファイル | emd_9399_additional.map | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| 注釈 | Escherichia coli F-pilus and Enterobacteria phage MS2 complex. (Class 1 map with phage genome), additional map | ||||||||||||
| 投影像・断面図 |
| ||||||||||||
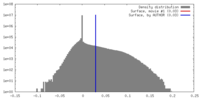
| 密度ヒストグラム |
- 試料の構成要素
試料の構成要素
-全体 : F-pilus/MS2 complex (Class 1 map with genome masked out)
| 全体 | 名称: F-pilus/MS2 complex (Class 1 map with genome masked out) |
|---|---|
| 要素 |
|
-超分子 #1: F-pilus/MS2 complex (Class 1 map with genome masked out)
| 超分子 | 名称: F-pilus/MS2 complex (Class 1 map with genome masked out) タイプ: complex / ID: 1 / 親要素: 0 / 含まれる分子: #1-#2 |
|---|
-超分子 #2: Enterobacteria phage MS2
| 超分子 | 名称: Enterobacteria phage MS2 / タイプ: complex / ID: 2 / 親要素: 1 / 含まれる分子: #1 |
|---|---|
| 由来(天然) | 生物種:  Enterobacteria phage MS2 (ファージ) Enterobacteria phage MS2 (ファージ) |
-超分子 #3: F-plius
| 超分子 | 名称: F-plius / タイプ: complex / ID: 3 / 親要素: 1 / 含まれる分子: #2 |
|---|---|
| 由来(天然) | 生物種:  |
-実験情報
-構造解析
| 手法 | クライオ電子顕微鏡法 |
|---|---|
 解析 解析 | 単粒子再構成法 |
| 試料の集合状態 | particle |
- 試料調製
試料調製
| 緩衝液 | pH: 8 |
|---|---|
| グリッド | 詳細: unspecified |
| 凍結 | 凍結剤: ETHANE |
- 電子顕微鏡法
電子顕微鏡法
| 顕微鏡 | JEOL 3200FSC |
|---|---|
| 特殊光学系 | エネルギーフィルター - スリット幅: 30 eV |
| 撮影 | フィルム・検出器のモデル: GATAN K2 SUMMIT (4k x 4k) 平均露光時間: 8.0 sec. / 平均電子線量: 37.0 e/Å2 |
| 電子線 | 加速電圧: 300 kV / 電子線源:  FIELD EMISSION GUN FIELD EMISSION GUN |
| 電子光学系 | 照射モード: FLOOD BEAM / 撮影モード: BRIGHT FIELD |
 ムービー
ムービー コントローラー
コントローラー














 Z (Sec.)
Z (Sec.) Y (Row.)
Y (Row.) X (Col.)
X (Col.)