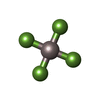+ データを開く
データを開く
- 基本情報
基本情報
| 登録情報 | データベース: PDB / ID: 7vpj | ||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
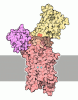
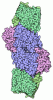
| タイトル | Cryo-EM structure of the human ATP13A2 (E1P-ADP state) | ||||||||||||
 要素 要素 | Polyamine-transporting ATPase 13A2 | ||||||||||||
 キーワード キーワード | MEMBRANE PROTEIN / ATP13A2 / PARK9 / P-type ATPase | ||||||||||||
| 機能・相同性 |  機能・相同性情報 機能・相同性情報polyamine transmembrane transporter activity / polyamine transmembrane transport / spermine transmembrane transport / peptidyl-aspartic acid autophosphorylation / regulation of ubiquitin-specific protease activity / ABC-type polyamine transporter activity / regulation of autophagosome size / extracellular exosome biogenesis / P-type ion transporter activity / regulation of chaperone-mediated autophagy ...polyamine transmembrane transporter activity / polyamine transmembrane transport / spermine transmembrane transport / peptidyl-aspartic acid autophosphorylation / regulation of ubiquitin-specific protease activity / ABC-type polyamine transporter activity / regulation of autophagosome size / extracellular exosome biogenesis / P-type ion transporter activity / regulation of chaperone-mediated autophagy / negative regulation of lysosomal protein catabolic process / regulation of autophagy of mitochondrion / regulation of lysosomal protein catabolic process / intracellular monoatomic cation homeostasis / autophagosome-lysosome fusion / autophagosome organization / protein localization to lysosome / phosphatidic acid binding / positive regulation of exosomal secretion / multivesicular body membrane / ATPase-coupled monoatomic cation transmembrane transporter activity / intracellular zinc ion homeostasis / regulation of protein localization to nucleus / トランスロカーゼ; 他の化合物の輸送を触媒; ヌクレオシド三リン酸の加水分解に伴う / cupric ion binding / regulation of mitochondrion organization / regulation of endopeptidase activity / lysosomal transport / phosphatidylinositol-3,5-bisphosphate binding / cellular response to zinc ion / regulation of intracellular protein transport / lipid homeostasis / Ion transport by P-type ATPases / autophagosome membrane / cellular response to manganese ion / regulation of macroautophagy / regulation of neuron apoptotic process / transport vesicle / autophagosome / multivesicular body / lysosomal lumen / positive regulation of protein secretion / transmembrane transport / autophagy / intracellular calcium ion homeostasis / late endosome / late endosome membrane / manganese ion binding / cellular response to oxidative stress / monoatomic ion transmembrane transport / intracellular iron ion homeostasis / vesicle / protein autophosphorylation / lysosome / neuron projection / lysosomal membrane / neuronal cell body / positive regulation of gene expression / ATP hydrolysis activity / zinc ion binding / ATP binding / membrane 類似検索 - 分子機能 | ||||||||||||
| 生物種 |  Homo sapiens (ヒト) Homo sapiens (ヒト) | ||||||||||||
| 手法 | 電子顕微鏡法 / 単粒子再構成法 / クライオ電子顕微鏡法 / 解像度: 3.54 Å | ||||||||||||
 データ登録者 データ登録者 | Tomita, A. / Yamashita, K. / Nishizawa, T. / Nureki, O. | ||||||||||||
| 資金援助 |  日本, 3件 日本, 3件
| ||||||||||||
 引用 引用 |  ジャーナル: Mol Cell / 年: 2021 ジャーナル: Mol Cell / 年: 2021タイトル: Cryo-EM reveals mechanistic insights into lipid-facilitated polyamine export by human ATP13A2. 著者: Atsuhiro Tomita / Takashi Daiho / Tsukasa Kusakizako / Keitaro Yamashita / Satoshi Ogasawara / Takeshi Murata / Tomohiro Nishizawa / Osamu Nureki /   要旨: The cytoplasmic polyamine maintains cellular homeostasis by chelating toxic metal cations, regulating transcriptional activity, and protecting DNA. ATP13A2 was identified as a lysosomal polyamine ...The cytoplasmic polyamine maintains cellular homeostasis by chelating toxic metal cations, regulating transcriptional activity, and protecting DNA. ATP13A2 was identified as a lysosomal polyamine exporter responsible for polyamine release into the cytosol, and its dysfunction is associated with Alzheimer's disease and other neural degradation diseases. ATP13A2 belongs to the P5 subfamily of the P-type ATPase family, but its mechanisms remain unknown. Here, we report the cryoelectron microscopy (cryo-EM) structures of human ATP13A2 under four different conditions, revealing the structural coupling between the polyamine binding and the dephosphorylation. Polyamine is bound at the luminal tunnel and recognized through numerous electrostatic and π-cation interactions, explaining its broad specificity. The unique N-terminal domain is anchored to the lipid membrane to stabilize the E2P conformation, thereby accelerating the E1P-to-E2P transition. These findings reveal the distinct mechanism of P5B ATPases, thereby paving the way for neuroprotective therapy by activating ATP13A2. | ||||||||||||
| 履歴 |
|
- 構造の表示
構造の表示
| ムービー |
 ムービービューア ムービービューア |
|---|---|
| 構造ビューア | 分子:  Molmil Molmil Jmol/JSmol Jmol/JSmol |
- ダウンロードとリンク
ダウンロードとリンク
- ダウンロード
ダウンロード
| PDBx/mmCIF形式 |  7vpj.cif.gz 7vpj.cif.gz | 205.8 KB | 表示 |  PDBx/mmCIF形式 PDBx/mmCIF形式 |
|---|---|---|---|---|
| PDB形式 |  pdb7vpj.ent.gz pdb7vpj.ent.gz | 154.1 KB | 表示 |  PDB形式 PDB形式 |
| PDBx/mmJSON形式 |  7vpj.json.gz 7vpj.json.gz | ツリー表示 |  PDBx/mmJSON形式 PDBx/mmJSON形式 | |
| その他 |  その他のダウンロード その他のダウンロード |
-検証レポート
| 文書・要旨 |  7vpj_validation.pdf.gz 7vpj_validation.pdf.gz | 1.1 MB | 表示 |  wwPDB検証レポート wwPDB検証レポート |
|---|---|---|---|---|
| 文書・詳細版 |  7vpj_full_validation.pdf.gz 7vpj_full_validation.pdf.gz | 1.1 MB | 表示 | |
| XML形式データ |  7vpj_validation.xml.gz 7vpj_validation.xml.gz | 33.2 KB | 表示 | |
| CIF形式データ |  7vpj_validation.cif.gz 7vpj_validation.cif.gz | 49.4 KB | 表示 | |
| アーカイブディレクトリ |  https://data.pdbj.org/pub/pdb/validation_reports/vp/7vpj https://data.pdbj.org/pub/pdb/validation_reports/vp/7vpj ftp://data.pdbj.org/pub/pdb/validation_reports/vp/7vpj ftp://data.pdbj.org/pub/pdb/validation_reports/vp/7vpj | HTTPS FTP |
-関連構造データ
| 関連構造データ |  32067MC  7vpiC  7vpkC  7vplC M: このデータのモデリングに利用したマップデータ C: 同じ文献を引用 ( |
|---|---|
| 類似構造データ | |
| 電子顕微鏡画像生データ |  EMPIAR-10975 (タイトル: Cryo-EM structure of the human ATP13A2 / Data size: 3.8 TB EMPIAR-10975 (タイトル: Cryo-EM structure of the human ATP13A2 / Data size: 3.8 TBData #1: Unaligned movies for E1-ATP state [micrographs - multiframe] Data #2: Unaligned movies for E1P-ADP state [micrographs - multiframe] Data #3: Unaligned movies for SPM-bound E2P state [micrographs - multiframe] Data #4: Unaligned movies for SPM-bound E2Pi state [micrographs - multiframe]) |
- リンク
リンク
- 集合体
集合体
| 登録構造単位 | 
|
|---|---|
| 1 |
|
- 要素
要素
| #1: タンパク質 | 分子量: 129313.391 Da / 分子数: 1 / 由来タイプ: 組換発現 / 由来: (組換発現)  Homo sapiens (ヒト) / 遺伝子: ATP13A2, PARK9 / 細胞株 (発現宿主): HEK293SGNTI- / 発現宿主: Homo sapiens (ヒト) / 遺伝子: ATP13A2, PARK9 / 細胞株 (発現宿主): HEK293SGNTI- / 発現宿主:  Homo sapiens (ヒト) Homo sapiens (ヒト)参照: UniProt: Q9NQ11, トランスロカーゼ; 他の化合物の輸送を触媒; ヌクレオシド三リン酸の加水分解に伴う |
|---|---|
| #2: 化合物 | ChemComp-MG / |
| #3: 化合物 | ChemComp-ADP / |
| #4: 糖 | ChemComp-NAG / |
| #5: 化合物 | ChemComp-ALF / |
| 研究の焦点であるリガンドがあるか | Y |
| Has protein modification | Y |
-実験情報
-実験
| 実験 | 手法: 電子顕微鏡法 |
|---|---|
| EM実験 | 試料の集合状態: PARTICLE / 3次元再構成法: 単粒子再構成法 |
- 試料調製
試料調製
| 構成要素 | 名称: ATP13A2 / タイプ: COMPLEX / 詳細: Human ATP13A2 in complex with AlF-ADP / Entity ID: #1 / 由来: RECOMBINANT |
|---|---|
| 分子量 | 実験値: NO |
| 由来(天然) | 生物種:  Homo sapiens (ヒト) Homo sapiens (ヒト) |
| 由来(組換発現) | 生物種:  Homo sapiens (ヒト) / 細胞: HEK293SGNTI- Homo sapiens (ヒト) / 細胞: HEK293SGNTI- |
| 緩衝液 | pH: 8 |
| 試料 | 濃度: 10 mg/ml / 包埋: NO / シャドウイング: NO / 染色: NO / 凍結: YES |
| 試料支持 | グリッドの材料: COPPER/RHODIUM / グリッドのサイズ: 300 divisions/in. / グリッドのタイプ: Quantifoil R1.2/1.3 |
| 急速凍結 | 凍結剤: ETHANE / 湿度: 100 % |
- 電子顕微鏡撮影
電子顕微鏡撮影
| 実験機器 |  モデル: Titan Krios / 画像提供: FEI Company |
|---|---|
| 顕微鏡 | モデル: FEI TITAN KRIOS |
| 電子銃 | 電子線源:  FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM FIELD EMISSION GUN / 加速電圧: 300 kV / 照射モード: FLOOD BEAM |
| 電子レンズ | モード: BRIGHT FIELD |
| 撮影 | 電子線照射量: 50 e/Å2 フィルム・検出器のモデル: GATAN K3 BIOQUANTUM (6k x 4k) |
- 解析
解析
| ソフトウェア | 名称: REFMAC / バージョン: 5.8.0267 / 分類: 精密化 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| EMソフトウェア |
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| CTF補正 | タイプ: PHASE FLIPPING AND AMPLITUDE CORRECTION | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 対称性 | 点対称性: C1 (非対称) | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 3次元再構成 | 解像度: 3.54 Å / 解像度の算出法: FSC 0.143 CUT-OFF / 粒子像の数: 3303 / アルゴリズム: FOURIER SPACE / 対称性のタイプ: POINT | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子モデル構築 | プロトコル: AB INITIO MODEL / 空間: RECIPROCAL | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化 | 解像度: 3.54→3.54 Å / Cor.coef. Fo:Fc: 0.897 / SU B: 39.165 / SU ML: 0.606 / ESU R: 0.952 立体化学のターゲット値: MAXIMUM LIKELIHOOD WITH PHASES 詳細: HYDROGENS HAVE BEEN ADDED IN THE RIDING POSITIONS
| ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 溶媒の処理 | 溶媒モデル: PARAMETERS FOR MASK CACLULATION | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 原子変位パラメータ | Biso mean: 231.424 Å2 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 精密化ステップ | サイクル: 1 / 合計: 7390 | ||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||||
| 拘束条件 |
|
 ムービー
ムービー コントローラー
コントローラー
















 PDBj
PDBj